Services on Demand
Journal
Article
Indicators
-
 Cited by SciELO
Cited by SciELO -
 Access statistics
Access statistics
Related links
-
 Cited by Google
Cited by Google -
 Similars in
SciELO
Similars in
SciELO -
 Similars in Google
Similars in Google
Share
Acta Agronómica
Print version ISSN 0120-2812
Acta Agron. vol.57 no.1 Palmira Jan./Mar. 2008
RESUMEN
Se realizó la caracterización molecular mediante el polimorfismo en la longitud de fragmentos amplificados (AFLP) de 121 introducciones de C. moschata, del Banco de Germoplasma del Programa de Investigación en Hortalizas de la Universidad Nacional de Colombia Sede Palmira, provenientes de ocho departamentos de Colombia. Los datos AFLP se evaluaron utilizando análisis de correspondencia múltiple (ACM), distancia genética, análisis genético con el programa TFPGA y el método de agrupamiento UPGMA. La diversidad genética de estas introducciones fue alta y estuvo de acuerdo con la diversidad morfoagronómica estudiada previamente. Los valores Fst indicaron que existe estructura genética entre la mayoría de las introducciones. La mayoría de la variación genética entre las introducciones se atribuyó a variación entre individuos dentro de cada departamento.
Palabras claves: Ahuyama,Cucurbita moschata, diversidad genética, estructura genética, marcadores moleculares AFLP.
ABSTRACT
The molecular characterization was carried out by means of the amplified fragment length polymorphism (AFLP) of 121 introductions of C. moschata, of the germoplasm bank of the Vegetables Research Program of the Universidad Nacional de Colombia campus Palmira, originating from eight departments of Colombia. The AFLP data were evaluated utilizing multiple correspondence analysis (MCA), genetic distance, genetic analysis with the TFPGA program and the UPGMA cluster analysis. The genetic diversity of these introductions was high and was according with the morphoagronomic diversity previously studied. The Fst values indicated that exist genetic structure between most of the introductions. The most of the genetic variation between the introductions corresponded to variations between them inside each department.
Key words: Squash, Cucurbita moschata, genetic diversity, genetic structure, molecular markers AFLP.
El zapallo, Cucurbita moschata (Duchesne ex Lam.) Duchesne ex Poir., es una de las cinco especies domesticadas del género Cucurbita en eventos independientes o simultáneos en meso-América y norte de Sur América(Vallejo y Estrada, 2004; Ferriol et al., 2004; Sanjur et al., 2002; Decker-Walters y Walters, 2000; Wessel-Beaver, 2000; Robinson and Decker- Walters, 1997; Nee, 1990; Esquinas-Alcázar y Gulick, 1983; Whitaker and Davis, 1962).
Los marcadores moleculares poco se han utilizado para estudiar la diversidad genética de C. moschata Jeon et al. (1994) utilizaron marcadores RAPD para discriminar entre cultivares de C. moschata y C. pepo. Lee et al. (1995) los utilizaron para analizar grupos de ligamiento en la generación F2 de híbridos de C. pepo x C. moschata. Youn et al. (1998) los usaron para investigar relaciones genéticas entre las variedades locales de zapallos nativos coreanos. Gwanama et al. (2000) analizaron la diversidad genética en las variedades tradicionales cultivadas en áfrica sur-central y las clasificaron para asistir en la selección de parentales para mejorar las características del fruto. Baranek et al. (2000) los usaron para revelar la diversidad genética dentro de las especies y entre las especies C. pepo, C. moschata y C. maxima. El único trabajo, hasta el momento reportado, que ha utilizado AFLP (Vos et al., 1995) en C. moschata fue realizado por el equipo de Ferrriol (2004) para determinar la diversidad molecular de una colección de germoplasma de zapallo en España.
El objetivo principal de la investigación fue determinar la diversidad genética de las introducciones colombianas del banco de germoplasma de zapallo de la Universidad Nacional de Colombia, mediante caracterización con marcadores AFLP.
En el Centro Experimental de la Universidad Nacional de Colombia Sede Palmira (CEUNP) se sembraron en vasos con turba 121 introducciones recolectadas en ocho departamentos de Colombia (Montes et al., 2004) y el cultivar UNAPAL Bolo Verde de C. moschata. La caracterización molecular se realizó en el Instituto de Investigación de Recursos Biológicos Alexander von Humboldt, localizado en el Centro Internacional de Agricultura Tropical – CIAT, con hojas de plántulas de 13 días.
Para la extracción del ADN se utilizó el protocolo DNeasy Plant Mini Kit de QIAGEN® (2004), con algunas modificaciones (Rueda et al., 2006) y adaptado a zapallo. El ADN se visualizó en gel de agarosa al 0.8% teñido con bromuro de etidio, mediante un transiluminador de luz ultravioleta. El ADN se cuantificó usando un fluorómetro Hoefer DyNA Quant 200, HiTechTrader. Se realizó un corte previo del ADN con la enzima de restricción EcoRI (Invitrogen) mediante digestión a 37°C por seis horas, en una máquina de PCR PTC-100 Peltier Thermal Cycler, MJ Research.
Para la caracterización molecular se utilizó el kit del sistema de análisis I de AFLP de Invitrogen (2003) y la mitad de las cantidades del protocolo. Los fragmentos de AFLP se corrieron en geles de poliacrilamida al 6% teñidos con nitrato de plata (Bassam, 1991) y se usaron los marcadores de peso molecular, ADN Ladder 10 bp (330- 10 bp) y ADN Ladder 25 bp (500-25 bp) de Invitrogen.
Los fragmentos de AFLP de 70-550 bp de la combinación de primer EcoRI-AGC/MseI-CTC se contaron manualmente como: presentes (1) y ausentes (0), utilizando un transiluminador de luz blanca. Con estos datos se realizó una matriz de 0 y 1.
Para realizar el análisis de correspondencia múltiple (ACM) y de distancia genética de las 121 introducciones se empleó una matriz con todas las bandas monomórficas y polimórficas, y se utilizó el paquete estadístico NTSYS-pc versión 2.0 (Rohlf, 1997).
Para el análisis genético se usó una matriz binaria sólo con las bandas polimórficas y se tuvo en cuenta el departamento de origen de las introducciones. Con esta matriz se realizaron los análisis estadísticos y se utilizó el programa TFPGA, versión 1.3 del 2000 (Miller, 1997).
Se estimó el porcentaje de loci polimórficos (P) y la heterocigosidad promedio, y se utilizó la fórmula no sesgada de Nei (1978). Para estimar la diferenciación poblacional, entre departamentos, se calculó el estadístico Fst. Para la interpretación del valor de Fst se empleó la clasificación de Wright (1978).
Se realizó la prueba exacta de diferenciación poblacional de Raymond y Rousset (1995). Se desarrolló una matriz de distancias euclidianas a partir de la matriz de datos binarios de las introducciones y se utilizó el programa AMOVA-PREP versión 1.01 (Miller, 1998). Las matrices de distancia se usaron para realizar el análisis de varianza molecular (AMOVA) mediante el programa WINAMOVA versión 1.55 (Excoffier et al., 1992). También se empleó la prueba de Bartlett mediante el programa WINAMOVA 1.55 (Excoffier et al., 1992).
Los cálculos de las distancias se basaron en la medida de la distancia genética mínima no sesgada de Nei (1978). También se realizó un dendrograma, mediante el método de agrupamiento UPGMA (Sneath y Sokal, 1973) y se utilizó la distancia mínima no sesgada de Nei (1978). Los cálculos y los dendrogramas se realizaron con el programa TFPGA (Miller, 1997).
Extracción de ADN y AFLP
Con el método de extracción se obtuvo alta cantidad de ADN ( X: 230 ng/ul), puro, no degradado, de buena calidad y se determinó en 15 minutos el tiempo adecuado de lisis del tejido vegetal macerado con el Buffer AP1 a 65°C. La concentración fue más alta que la obtenida por Restrepo (2005) en C. moschata (200 ng/ul), muy aproximada al rango de concentraciones (10 ng/ul-300 ng/ul) obtenida por Montes (2003), a la concentración (240 ng/ul) obtenida por Brown et al. (1998), y a la concentración (250 ng/ul) obtenida por Chen y Ronald (1999).
El ADN presentó digestión completa con EcoRI en todas las muestras, y confirmó así la buena calidad del ADN y la eficacia de este método de extracción de ADN. Este ADN presentó cualidades ideales para ser usado en la técnica AFLP. En las 121 introducciones más el cultivar UNAPAL Bolo Verde se presentaron 117 bandas, de las cuales 91 fueron polimórficas (77.80%) (Figura 1). Cada introducción presentó bandas diferentes que indicaban variación genética molecular entre ellas.

Diversidad genética de las introducciones provenientes de ocho departamentos de Colombia
La cantidad de loci polimórficos en las introducciones de C. moschata colombianas (89.01%) fue superior a la obtenida por Ferriol et al. (2004) (85.90%) y los valores por departamento fluctuaron entre 43.96 y 87.91% (Tabla 1). Los mayores porcentajes de loci polimórficos se presentaron en las introducciones provenientes de los departamentos del Valle del Cauca, Cauca y Caldas; los menores en las introducciones de Risaralda, Quindío y Bolívar y estuvieron relacionados con tamaños de muestra pequeños (Risaralda, n = 4; Quindío, n = 8; y Bolívar, n = 6).
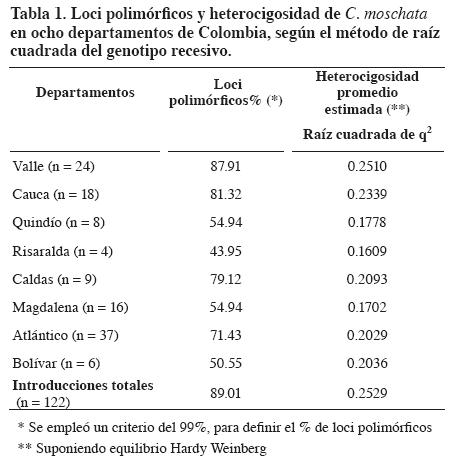
El valor de heterocigosidad promedio no sesgada o diversidad genética para todas las introducciones de C. moschata colombianas fue alta 0.2529, comparada con la obtenida por Ferriol et al. (2004) (0.17), en accesiones recolectadas en diferentes regiones de España, 12 accesiones de Sur y Centro América (Ecuador, Cuba, Perú, Guatemala y Republica Dominicana), dos accesiones de Marruecos y también el cultivar comercial de zapallo Butternut de U. S. La diversidad genética obtenida está de acuerdo con la alta diversidad morfoagronómica registrada en esta misma colección por Montes et al. (2004). Los valores fluctuaron entre 0.1609 (Risaralda) y 0.2510 (Valle del Cauca) (Tabla 1). Los departamentos del Valle del Cauca y Cauca exhibieron los niveles de heterocigosidad más altos, debida posiblemente a la cercanía y a los intercambios antrópicos; mientras que Risaralda presentó la más baja heterocigosidad con un 0.1609. La heterocigosidad promedio de todas las introducciones fue relativamente mayor que el promedio de heterocigosidad para cada departamento, lo que podría indicar un grado de diferenciación genética significativo entre departamentos.
La diversidad genética encontrada en la colección colombiana de C. moschata está de acuerdo con estudios previos realizados por Ferriol et al. (2004), Wessel-Beaver (2000) y Whitaker y Davis (1962). También está de acuerdo con la identificación de áreas de alta diversidad de C. moschata en Colombia, donde las variedades tradicionales exhiben características primitivas comunes (Zhiteneva, 1930; Nee, 1990; Wessel-Beaver, 2000; Sanjur et al., 2002).
Diferenciación entre introducciones
El valor de Fst promedio (0.1357 ± 0.0136, con un intervalo de confianza al 95% entre 0.1112 y 0.1614) indicó moderada diferenciación genética (Wright, 1978) entre las introducciones provenientes de los ocho departamentos colombianos. El Fst promedio entre todos los pares de departamentos fue 0.1355, que fluctuó entre -0.0027 para la pareja Valle-Cauca, con poca diferenciación genética y vecinos geográficamente y 0.3116 para la pareja Quindío (centro)-Magdalena (Costa Atlántica) con diferenciación genética muy grande y distantes geográficamente (Tabla 2).
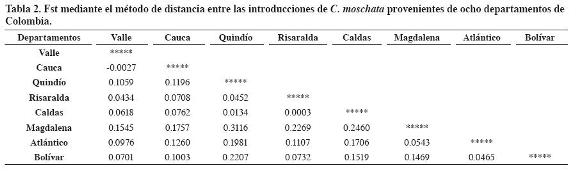
La mayoría de valores Fst entre pares de departamentos fueron significativamente altos, a excepción de las parejas Valle-Cauca, Valle-Risaralda, Quindío- Risaralda, Quindío-Caldas, Risaralda-Caldas y Atlántico-Bolívar, cuyos valores Fst indicaron poca diferenciación genética. La poca diferenciación se debió a que comparten características morfoagronómicas como forma y dimensiones de fruto, forma y dimensiones de semillas y tiempo de floración, según los cinco grupos conformados en la caracterización morfológica (Montes et al., 2004), en la cual fueron diferentes los grupos de las introducciones andinas de los departamentos de Valle, Cauca, Quindío, Risaralda y Caldas y los de la Costa Atlántica (departamentos de Atlántico, Bolívar y Magdalena). Además, las seis parejas de departamentos están situadas muy cerca geográficamente y con posible efecto antrópico.
Los valores Fst indicaron moderada diferenciación genética para las parejas de departamentos Valle- Quindío, Valle-Caldas, Valle-Atlántico, Valle-Bolívar, Cauca-Quindío, Cauca-Risaralda, Cauca-Caldas, Cauca-Atlántico, Cauca-Bolívar, Risaralda-Atlántico, Risaralda-Bolívar, Magdalena-Atlántico y Magdalena- Bolívar. Montes et al. (2004) encontraron también que las características morfoagronómicas eran comunes en algunas parejas de departamentos un poco más distanciadas (Valle-Caldas, Cauca-Quindío, Cauca- Caldas) y en otras más distanciadas (Valle-Atlántico, Cauca-Atlántico, Risaralda-Bolívar), con posible efecto antrópico.
Los Fst indicaron gran diferenciación genética entre Valle-Magdalena, Cauca-Magdalena, Quindío-Atlántico, Quindío-Bolívar, Risaralda-Magdalena, Caldas- Magdalena, Caldas-Atlántico y Caldas-Bolívar. Estas parejas conforman grupos diferentes morfoagronómicamente (Montes et al., 2004) y son departamentos muy distantes, uno ubicado en el suroccidente colombiano y el otro en el noroccidente colombiano. Mientras que el Fst de Quindío-Magdalena indicó una diferenciación genética muy grande entre estos dos departamentos y está correlacionado con la gran distancia geográfica existente entre Quindío del suroccidente y Magdalena del noroccidente colombiano. Los valores indicaron que hay una estructura genética entre las introducciones de los ocho departamentos de Colombia y no una estructura continua o unidad panmíctica.
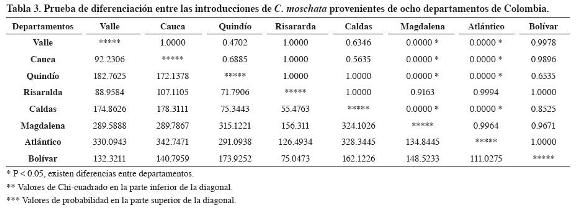
La prueba exacta de diferenciación entre las introducciones (Tabla 3) confirmó diferenciación genética significativa entre los departamentos de la Costa Atlántica y la región andina. Estos resultados están de acuerdo con el índice de diversidad (62%) estimado en el estudio de Montes et al. (2004).
El análisis de varianza molecular (AMOVA) (Tabla 4) mostró diferencias significativas entre los departamentos (P<0.001). El 88.76% de la variación genética total se debió a la que existe entre introducciones dentro de cada departamento.
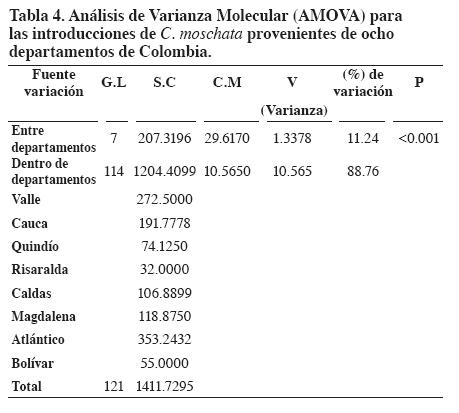
La variación genética entre departamentos fue altamente significativa (P<0.001) y la estructura genética total, Φst: 11.24, difirió significativamente de cero. El porcentaje de variación entre departamentos se asimila como el valor de Fst en todos los casos. Entre el valor de Φst total y el de Fst no se encontró diferencia significativa que confirme que sí existe una variación genética entre las introducciones provenientes de los ocho departamentos, aunque la mayoría se presentó dentro de cada departamento.
La heterogeneidad de la varianza entre departamentos estimada mediante la prueba de Bartlett de homogeneidad de varianzas (Tabla 5) fue de Bp = 0.95653, con un nivel de significancia de P < 0.001, que indica niveles significativos de variabilidad entre las introducciones provenientes de los diferentes departamentos.
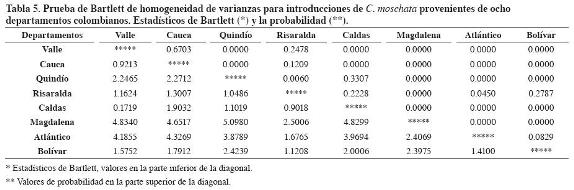
Las parejas de departamentos que no presentaron diferencias entre sus varianzas fueron: Valle-Cauca, Risaralda-Valle, Risaralda-Cauca, Risaralda-Quindío, Caldas-Quindío, Caldas-Risaralda, Bolívar-Risaralda y Bolívar-Atlántico. La mayoría de estas parejas presentaron poca diferenciación genética y se encuentran localizadas geográficamente cerca, a excepción de la pareja Bolívar-Risaralda.
Los valores de distancia genética, con un promedio de 0.0360 (Tabla 6), fluctuaron entre 0.0040 para la pareja Valle-Cauca y 0.0884 para Quindío-Magdalena. El análisis de distancia genética concordó con los resultados aportados por las pruebas de diferenciación entre las introducciones de C. moschata provenientes de los ocho departamentos de Colombia, lo cual confirma que existe una estructura genética.
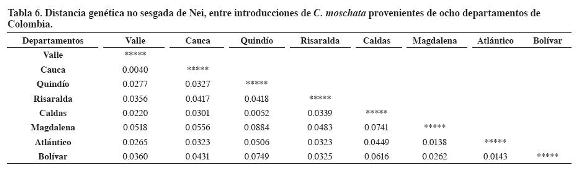
El árbol de distancia genética (Figura 2) presentó siete agrupaciones entre las introducciones de C. moschata. Entre los departamentos de Valle y Cauca, y Quindío y Caldas presentaron valores de distancia cercanos a cero, que indica que están relacionados o que hay alta similitud. Mientras que entre los grupos de la Costa Atlántica y los andinos se destacó la gran diferenciación genética y distancia geográfica a excepción de Risaralda, que a pesar de estar agrupados con departamentos de la Costa Atlántica no comparten características morfológicas (Montes et al., 2004), es probable el efecto antrópico.
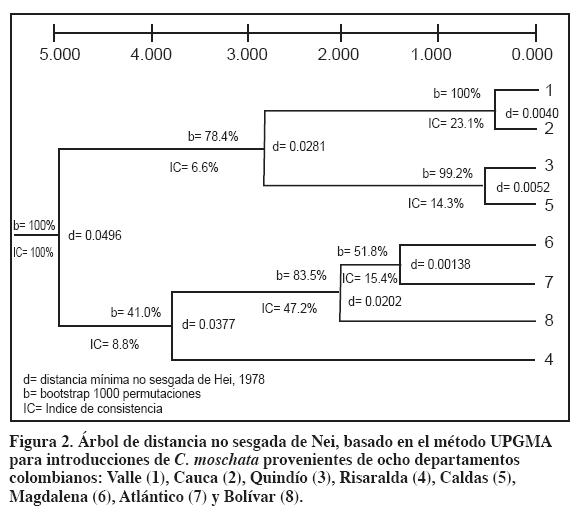
Análisis de correspondencia múltiple y distancia genética de todas las introducciones de C. moschata
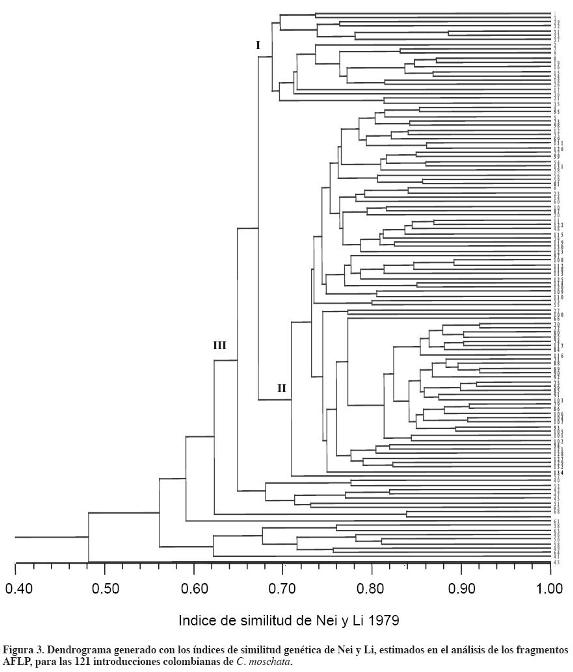
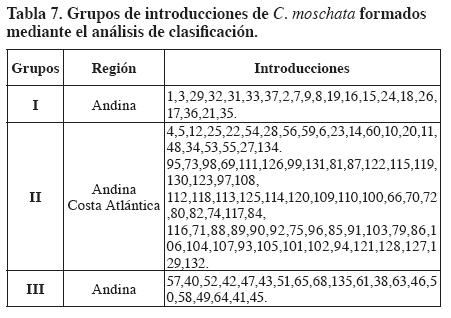
Al realizar el análisis de correspondencia múltiple no se observó tendencia a la conformación de grupos entre las 121 introducciones de C. moschata. Sin embargo, se realizó el análisis de clasificación (Figura 3). En el dendrograma se observó la tendencia a formar tres grandes grupos (Tabla 7). El grupo I con las introducciones provenientes de la región andina, con un índice de similitud de Nei y Li (1979) de aproximadamente 0.68; el grupo II con las introducciones provenientes de la región andina y la Costa Atlántica, pero en su mayoría de esta última con un índice de similitud de 0.71; y el grupo III con otras introducciones provenientes de la región andina, con un índice de similitud entre 0.48 y 0.68. Las introducciones de la Costa Atlántica se agruparon en el grupo II, porque tienen distancias genéticas cercanas, comparten la misma región geográfica noroccidental de Colombia y características morfológicas. En este grupo algunas introducciones andinas se situaron con las de la Costa Atlántica, posiblemente por efecto antrópico o porque comparten características morfológicas cualitativas y cuantitativas (Montes et al., 2004).
La diversidad genética molecular de las 121 introducciones de C. moschata, provenientes de ocho departamentos de Colombia, fue alta (0.2529) y estuvo de acuerdo con la gran diversidad morfoagronómica registrada previamente.
La heterocigosidad promedia de todas las introducciones (25.3%) fue mayor que el promedio de heterocigosidad para cada grupo de introducciones provenientes de los ocho departamentos. Los valores Fst indicaron que hay una estructura genética entre la mayoría de las introducciones provenientes de los ocho departamentos de Colombia y no una estructura continua o unidad panmíctica.
Existió variación genética significativa del 11.24% entre las introducciones provenientes de los ocho departamentos. La mayoría de la variación total se debió a variación entre los individuos de C. moschata dentro de cada departamento (88.76%).
En el análisis de clasificación, las 121 introducciones se agruparon en tres grandes grupos: dos con introducciones de la región andina y otro con introducciones andinas y de la Costa Atlántica, pero la mayoría de la Costa Atlántica.
Escuela de Posgrados de la Universidad Nacional de Colombia Sede Palmira. Al Programa de Investigación Mejoramiento Genético y Producción de Semillas de Hortalizas de la Universidad Nacional de Colombia Sede Palmira, por el financiamiento de la tesis de Maestría en Ciencias con énfasis en Recursos Fitogenéticos Neotropicales del biólogo genetista J. A. Restrepo S. Al Laboratorio de Biología Molecular del Instituto Alexander von Humboldt, y en especial a J. D. Palacio.
1. Baranek, M.; Stift, G.; Vollmann, J.; Lelley, T. 2000. Genetic diversity within and between the species Cucurbita pepo, C. moschata and C. maxima as revealed by RAPD markers. Cucurbit. Genet. Coop. Rep. 23: 73-77. [ Links ]
2. Bassam, B.J.; Caetano Anolles, G.; Gresshoff, P.M. 1991. Fast and sensitive silver staining of DNA in polyacrylamide gels. Anal. Biochem. 196(1): 80-83. [ Links ]
3. Brown, R.N.; Myers, J.E.; Hutton, M.; Miller, P. 1998. A simple protocol for isolating DNA from fresh Cucurbita leaves. Cucurbit Genet. Coop. Rep. 21:46-47. [ Links ]
4. Chen, D.H.; Ronald, P.C. 1999. A rapid DNA minipreparation method suitable for AFLP and other PCR applications. Plant Mol. Biol. Rep. 17: 53-57. [ Links ]
5. Decker-Walters, D.S.; Walters, T.W. 2000. Squash. In: Kiple K. F.; Ornelas K. C. (ed.) The Cambridge world history of food. Cambridge University Press, Cambridge, U. K., pp. 335-351. [ Links ]
6. Esquinas-Alcázar, J.T.; Gulick, P.J. 1983. Genetic resources of Cucurbitaceae: A global report. Rome (Italy): IBPGR Secretariat. 105 p. [ Links ]
7. Excoffier, L.; Smouse, P. E.; Quattro, J. M. 1992. Analysis of molecular variance inferred from metric distances among DNA haplotypes: application to human mitochondrial DNA restriction data. Genetics 131.179-191. [ Links ]
8. Ferriol, M.; Picó, B.; Fernández de Córdova, P.; Nuez, F. 2004. Molecular diversity of a germoplasm collection of squash (Cucurbita moschata) determined by SRAP and AFLP markers. Crop Sci. 44: 653-664. [ Links ]
9. Gwanama, C.; Labuschagne, M.T.; Botha, A.M. 2000. Analysis of genetic variation in Cucurbita moschata by random amplified polymorphic DNA (RAPD) markers. Euphytica 113:19-24. [ Links ]
10. Invitrogen, Life Technologies. 2003. Instruction manual, AFLP® Analysis System I and AFLP® Starter Primer Kit, Version B. 24 p. [ Links ]
11. Jeon, H. J.; Been, C.G.; Hong, K.H.; Om, Y.K.; Kim, B.D. 1994. Identification of cucurbitacea cultivars by using RAPD markers. J. Kor. Soc. Hort. Sci. 35: 449-456. [ Links ]
12. Lee, Y.H.; Jeon, H.J.; Hong, K.H.; Kim, B.D. 1995. Use of random amplified polymorphic DNAs for linkage group analysis in interspecific hybrid F2 generation of Cucurbita. J. Kor. Soc. Hort. Sci. 36: 323-330. [ Links ]
13. Miller, M.P. 1997. Tools for population genetic analyses (TFPGA). Version 1.3. Computer software distributed by author. [ Links ]
14. Miller, M.P. 1998. A program for the preparation of Amova input file from dominant-marker raw data (Amova-PREP). Version 1.01. Computer software distributed by author. [ Links ]
15. Montes, C. 2003. Colección, caracterización morfológica, y evaluación agronómica de germoplasma colombiano de zapallo (Cucurbita moschata Duchesne ex. Poir). Tesis de Maestría en Recursos Fitogenéticos Neotropicales. Universidad Nacional de Colombia. Facultad de Ciencias Agropecuarias. Palmira. 95 p. [ Links ]
16. Montes, R.C.; Vallejo, C.F.A.; Baena, G.D. 2004. Diversidad genética de germoplasma colombiano de zapallo (Cucurbita moschata Duchesne ex Poir). Acta Agron. (Palmira) 53 (3): 43-50. [ Links ]
17. Nee, M. 1990. The domestication of Cucurbita. Econ. Bot. 44:56-68. [ Links ]
18. Nei, M. 1978. Estimation of average heterozygosity and genetic distances from a small number of individuals. Genetics 89: 583- 590. [ Links ]
19. Nei, M. y Li, W. 1979. Mathematical model for studing genetic variation in terms of restriction endonucleases. Proc. Natl. Acad. Sci. USA 79: 5269-5273. [ Links ]
20. QIAGEN. 2004. DNeasy Plant Mini and Dneasy Plant Maxi Handbook, for isolation of DNA from plant tissue. (Disponible en http://www.QIAGEN.com ) 12-10-2007. [ Links ]
21. Raymond, M.L.; Rousset, F. 1995. An exact test for population differentiation. Evolution 49: 1280-1283. [ Links ]
22. Restrepo, J. A. 2005. Caracterización molecular de accesiones colombianas de zapallo Cucurbita moschata, utilizando marcadores moleculares AFLP. Tesis de Maestría en Recursos Fitogenéticos Neotropicales. Universidad Nacional de Colombia. Facultad de Ciencias Agropecuarias. Palmira. 108 p. [ Links ]
23. Robinson, R. W.; Decker-Walters, D.S. 1997. Cucurbits. Crop production science in horticulture. New York: Cab international. [ Links ]
24. Rohlf, F.J. 1997. NTSYS-pc, Version 2.02 K: Numerical taxonomy and multivariate analysis system. New York: Exeter software. [ Links ]
25. Rueda, E. A.; Palacio, J.D.; Muñoz, J.E.; Saavedra, R.; Bravo, E. 2006. Caracterización molecular del banco de germoplasma de guayaba Psidium spp. del centro de investigación Corpoica- Palmira. Fitotecnia Colombiana 6(2):26-32 [ Links ]
26. Sanjur, O.I.; Piperno, D.R.; Andres, T.C.; Wessel-Beaver, L. 2002. Phylogenetic relationships among domesticated and wild species of Cucurbita (cucurbitaceae) Inferred from a mitochondrial gene: Implications for crop plant evolution and areas of origin. Proc. Natl. Acad. Sci. USA 99:535-540. [ Links ]
27. Sneath, P.H.A.; Sokal, R.R. 1973. Numerical taxonomy: the principles and practices of numerical classification. San Francisco: W.H. Freeman. 623 pp. [ Links ]
28. Vallejo, F. A.; Estrada, E. I. 2004. Producción de hortalizas de clima cálido. Palmira: Universidad Nacional de Colombia. 346 p. [ Links ]
29. Vos, P.; Hogers, R.; Bleeker, M.; Reijans, M.; van de Lee, T.; Hornes, M.; Frijters, A.; Pot, J.; Peleman, J.; Kuiper, M. 1995. AFLP: a new technique for DNA fingerprinting. Nucleic Acids Res. 23(21): 4407-4414. [ Links ]
30. Wessel-Beaver, L. 2000. Evidence for the center of diversity of Cucurbita moschata in Colombia. Cucurbit. Gen. Coop. Rep. 23: 54-55 [ Links ]
31. Whitaker, T. W.; Davis, G. N. 1962. Cucurbits: botany, cultivation and utilization. New York: Interscience Publishers. 250 p. [ Links ]
32. Wright, S. 1978. Evolution and the genetics of populations, variability within and among natural populations, Vol. 4, University of Chicago Press, Chicago. 580 p. [ Links ]
33. Youn, S.J.; Chung, H.D. 1998. Genetic relationship among the local varieties of the korean native squashes (Cucurbita moschata) using RAPD technique. J. Kor. Soc. Hortic. Sci. 39:517-521. [ Links ]
34. Zhiteneva, N. E. 1930. The world's assortment of pumpkins. Trudy Prikl. Bot. Genet. Selek. 23: 157-207 [ Links ]














