Services on Demand
Journal
Article
Indicators
-
 Cited by SciELO
Cited by SciELO -
 Access statistics
Access statistics
Related links
-
 Cited by Google
Cited by Google -
 Similars in
SciELO
Similars in
SciELO -
 Similars in Google
Similars in Google
Share
Acta Biológica Colombiana
Print version ISSN 0120-548X
Acta biol.Colomb. vol.14 no.2 Bogotá May/Aug. 2009
DATOS POBLACIONALES DE LOS MICROSATÉLITES
DE ADN HUMANO D2S1338, D19S433,
PENTA D, PENTA E Y SE-33 DE LA REGIÓN CENTRAL COLOMBIANA
Population Data Of Human DNA Microsatellites D2S1338, D19S433, Penta D, Penta E And SE-33 From Central Region In Colombia
MAURICIO REY1*, Bioquímico, M.Sc.; WILLIAM USAQUEN2, Biólogo, M.Sc.; EDWIN ACOSTA3, Médico Veterinario, Ph. D.; JULIO PARRA4, Químico; JUAN PABLO TRONCOSO4, Químico.
1Facultad de Medicina, Instituto de Genética, Universidad Nacional de Colombia.
2Facultad de Ciencias, Instituto de Genética, Universidad Nacional de Colombia.
3(ABD). Facultad de Medicina Veterinaria, Universidad Nacional de Colombia.
4Universidad de Ciencias Aplicadas y Ambientales, UDCA.
*Correspondencia: mrey@unal.edu.co, Instituto de genética, Universidad Nacional de Colombia, Bogotá-Colombia.
Presentado 10 de marzo de 2009, aceptado 1 de julio de 2009, correcciones 13 de julio de 2009.
RESUMEN
Los microsatélites o STR por su sigla en inglés (Short Tandem Repeat) son repeticiones de secuencias cortas de nucleótidos a través del DNA, de gran importancia debido a su carácter polimórfico que permite su utilización en la identificación genética de individuos o poblacionales. En este trabajo se investigaron los perfiles genéticos de una muestra de poblaciones humanas del altiplano cundiboyacense en Colombia; se usaron los marcadores STR’s D2S1338, D19S433, PENTA D, PENTA E y SE-33. Éstos cinco STR’s fueron amplificados mediante reacción en cadena de la polimerasa (PCR), corridos con electroforesis capilar, y tipificados con los programas Genscan y Genotyper. Como resultado se reportan las frecuencias alélicas de los cinco microsatélites (no reportados anteriormente para esta región). Se encontró que los loci D19S433 y SE-33 no están en equilibrio de Hardy-Weinberg; y que el Penta E tiene el mayor poder de discriminación. La distribución de las frecuencias alélicas para los cinco marcadores, en las dos poblaciones analizadas mostró que no existen diferencias estadísticas significativas entre ellas.
Palabras clave: STR, D2S1338, D19S433, PENTA D, PENTA E, SE-33.
ABSTRACT
Microsatellites (STR’s) are short tandem repeat sequences of nucleotides through DNA, very important for their polymorphic character that allow their utilization in population genetic identification. The STR’s markers D2S1338, D19S433, PENTA D, PENTA E y SE33 were used to do the genetic profiles of human populations from the Cundiboyacense region in Colombia. The five STR’s were amplified by PCR (polymerase chain reaction), indentified with capillary electrophoresis, and typified with Genscan and Genotyper software. Allelic frequencies of the five microsatellites are reported (not previously reported for this region). It was found that loci D19S433 y SE-33 are not in Hardy-Weinberg equilibrium; and Penta E provides the greatest power of discrimination. The allelic frequencies distribution to these five markers, in the two populations studied show that it does not exist statistically significant differences between them.
Key words: STR, D2S1338, D19S433, PENTA D, PENTA E, SE-33.
INTRODUCCIÓN
A través del tiempo las sociedades humanas han empleado diversos métodos para conocer la filiación entre las personas cuando hay dudas, especialmente en casos de paternidad. Inicialmente, se establecían paternidades a través de métodos antropométricos, en los cuales se observaban aspectos morfológicos medibles. Con el pasar de los años y avance de la ciencia y tecnología, éstos análisis se eliminaron por su subjetividad y cambiaron por pruebas a partir de grupos sanguíneos, antígenos eritrocitarios y luego por antígenos leucocitarios, proteínas séricas o enzimas de eritrocitos, donde se realizaba la identificación por medio de las isoformas de estás proteínas, siendo éstos análisis mejores que los anteriores pero no del todo confiables, además de costosos y complicados desde el punto de vista técnico (Martínez, 1999). Aparecieron entonces los polimorfismos de longitud de los fragmentos de restricción (RFLPs); pero debido a que la variabilidad genética general de éstos en el ADN hu-mano es baja, su uso en la predicción de paternidad ha sido poca (Wainscoat et al., 1986). En el año de 1985 Jeffreys y colaboradores descubrieron un método de identificación individual que denominaron DNA Fingerprinting o huella genética (Jeffreys et al., 1985) que prometía ser la solución definitiva al análisis de la diversidad humana desde la medicina legal, tanto en la investigación biológica de la paternidad como en criminalística.
En el ADN existen regiones conocidas como minisatélites (VNTR) y microsatélites (STR) de gran variabilidad entre individuos, que permiten utilizarlas como marcadores moleculares en medicina forense, pruebas de paternidad y diagnóstico de enfermedades moleculares (Luque, 2001). Los STR’s son también los marcadores genéticos de elección para la creación de base de datos nacionales de perfiles del ADN con fines de investigación criminal, para estudios poblacionales, para estudios de marcadores ligados a genes de predisposición genética a enfermedades, etc. El desarrollo de dichas bases de datos es ya una realidad en países europeos, estados unidos y países en vías de desarrollo (Alonso, 2001).
En pruebas de paternidad a partir de microsatélites STR’s, se ha encontrado que con los 14 o 16 marcadores actualmente utilizados en las instituciones colombianas dedicadas a los estudios de filiación, en algunos casos tales como ausencia del padre o muerte del mismo entre otros, el valor requerido de probabilidad de paternidad exigido por las autoridades (99,99 %) no es alcanzada (Senado de la república de Colombia, Ley 721, 2001); por lo tanto, el presente estudio consistió en introducir marcadores STR’s adicionales (D2S1338, D19S433, PENTA D, PENTA E y SE -33) con sus condiciones óptimas de amplificación para reacción en cadena de la polimerasa (PCR) y electroforesis capilar. Y así, con estos marcadores adicionales validados lograr alcanzar el valor de dicha probabilidad. Se realizó el estudio poblacional de la distribución alélica de estos marcadores en la ciudad de Bogotá y el departamento de Boyacá, como regiones de influencia del laboratorio. La utilidad y los beneficios de la inclusión de estos marcadores se pueden reflejar en primer lugar en la resolución de casos jurídicos complejos, bien sea en beneficio de un menor que necesita el apoyo económico de su padre o de un hombre que sin ser culpable, se puede ver obligado a responder económicamente por un menor que no le corresponde. Y en segundo lugar conllevaría a la reducción de costos, ya que los usuarios en cuya prueba no alcanzaron la probabilidad mínima exigida no se verán obligados a pagar otra prueba completa con nuevos marcadores, sino que bastaría con incluir los marcadores adicionales a un costo más reducido y así fácilmente se alcanzaría los valores deseados. Por último la resolución de casos de filiación contribuye a evitar conflictos, violencia intrafamiliar e inclusive resentimientos sociales que solo incrementan los niveles de intolerancia en nuestra sociedad.
MATERIALES Y MÉTODOS
Población: región central de Colombia (Bogotá y Boyacá). Procedimiento: se tomaron más de 100 muestras de individuos de Bogotá y más de 100 de Boyacá. Estas muestras reposaban en el laboratorio de paternidades del Instituto de Genética de la Universidad Nacional de Colombia y corresponden a una muestra por conveniencia de usuarios del servicio de paternidad, no relacionados, quienes a través de consentimiento informado autorizan al laboratorio a utilizarlas en estudios poblacionales como muestras ciegas. El ADN de un lote de muestras fue extraído utilizando un kit de purificación (Wizard® Genomic DNA purification), y la otra parte se hizo utilizando el método de salting out (Miller et al., 1988). Las condiciones de PCR para los STR’s D2S1338, D19S433 y SE-33 fueron las recomendadas por los fabricantes (AmpF1STR® Sefiler kit; Rao et al., 2004). La secuencia de los cebadores y condiciones de PCR para los microsatélites Penta D y Penta E fueron de acuerdo con Krenke et al., 2002. Los productos de PCR fueron separados y detectados empleando electroforesis capilar del analizador genético ABI PRISM® 310 (Applied Biosystems). La tipificación y análisis de electroforegramas se realizaron empleando los programas Genscan y Genotyper.
Los parámetros de genética poblacional y forense como: frecuencia mínima(f. Min.), grado de heterocigocidad observada y esperada(Ho, He), desequilibrio de Hardy-Weinberg(Hw) y el estadístico Fst fueron estimados utilizando el programa de Lewis y Zayki, recomendado por GDA -Genetic Data Analysis; además el poder de discriminación (PD), índice típico de paternidad (TPI), información del contenido polimórfico (PIC), el poder de exclusión (PE), probabilidad de coincidencia (MP) se estimaron con el programa PowerStats de Promega http://www.promega.com/geneticid tools/powerstats/.
RESULTADOS
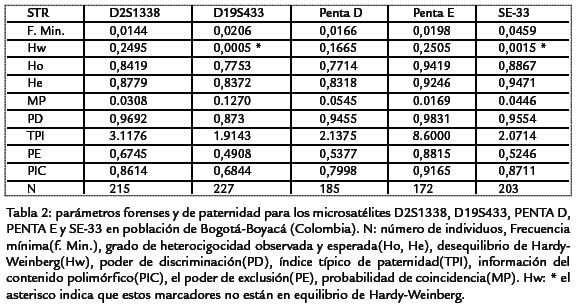
En este trabajo se reportan las frecuencias alélicas de los cinco microsatélites, D2S1338, D19S433, PENTA D; PENTA E -33, que aún no han sido reportados para nuestra región (Tabla 1). Además se estimaron parámetros estadísticos forenses y de paternidad de interés general (Tabla 2).

DISCUSIÓN
En trabajos anteriores se reportaron frecuencias alélicas de otros 13 microsatélites autosómicos (Bustos et al., 2001; Rey et al., 2003) y 13 de STRs de cromosoma Y (trabajo por publicar) para esta región, y estas frecuencias alélicas junto con las de los cinco marcadores de este estudio, continúan demostrando que no hay diferencias significativas entre la población de Bogotá y Boyacá en cuanto a su genética.
Los loci D19S433 y SE-33 no están en equilibrio de Hardy-Weinberg (Hw*), quizás porque son sistemas con un gran número de alelos, algunos de los cuales muestran frecuencias menores a las mínimas (F. Min.). Tal vez el tamaño de la muestra no haya sido lo suficientemente representativo para estos sistemas y por lo tanto para tratar de solucionar esta situación sea necesario tomar una muestra mayor. También es posible considerar una subestructuración de la población, pero los demás estadísticos con los otros sistemas genéticos nos indican que no la hay. Por el momento se recomienda utilizar las frecuencias mínimas para estos marcadores al momento de realizar cálculos de criminalística y pruebas de paternidad.
Con relación al marcador Penta E, la distribución alélica en las dos poblaciones es más homogénea, cuatro alelos suman prácticamente la mitad del porcentaje aportante y los restantes 16 suman prácticamente la otra mitad con frecuencias bajas, que son importantes a tener en cuenta a la hora de realizar pruebas de paternidad debido a que facilitan el logro del porcentaje de probabilidad exigido, pero algunas frecuencias son menores a la mínima lo que sugiere aumentar el tamaño de la muestra.
Los parámetros estadísticos muestran que el microsatélite Penta E tiene el mayor poder de discriminación (PD), además el índice típico de paternidad (TPI), la información del contenido polimórfico (PIC), el poder de exclusión (PE) y el grado de heterocigocidad (H) son los mayores. Como era de esperar de lo anterior, posee la probabilidad de coincidencia (MP) más baja. De todo lo anterior se puede afirmar que de los cinco marcadores estudiados, el Penta E es el de mayor utilidad en la identificación de individuos de la población en estudio.
La distribución de las frecuencias alélicas en estos marcadores tiene el mismo comportamiento cuando se trabajan en conjunto las dos poblaciones que cuando se analizaron por separado, al igual que los estadísticos forenses y de paternidad. El estadístico Fst total (0,000018; P=0,00) calculado para todos los loci y para las dos poblaciones evidencia que no hay subdivisión poblacional, lo cual confirma nuevamente la gran similitud entre las dos poblaciones (Slatkin, 1995).
La similitud en los indicadores estadísticos, forenses y poblacionales así como la distribución de las frecuencias alélicas de las dos poblaciones analizadas muestra que no existen diferencias estadísticas significativas entre ellas y por tanto se pude considerar como una sola población. No se hallaron diferencias significativas entre la población de Bogotá y Boyacá empleando estos marcadores basados en los valores de Fst. Lo anterior puede ser el reflejo de la ubicación geográfica ya que las dos poblaciones se ubican en el mismo altiplano y no ha existido limites para el intercambio de individuos, además durante la época precolombina, colonial y moderna ha existido permanente migración entre las dos regiones. Los parámetros estadísticos de interés forense calculados en este estudio poblacional revelan que estos sistemas genéticos son altamente efectivos y que los datos de sus frecuencias alélicas pueden ser utilizadas con toda confianza en las pruebas de filiación de personas procedentes de las regiones aquí mencionadas, se recomienda aumentar el tamaño de la muestra en aquellos marcadores que presentaron desequilibrio genético y frecuencias alélicas menores a las mínimas, no obstante se pueden utilizar estas últimas en los cálculos en pruebas de identificación y parentesco.
AGRADECIMIENTOS
Este trabajo fue aprobado y apoyado por el Instituto de Genética de la Universidad Nacional Colombia y la empresa Exógena ltda.
BIBLIOGRAFÍA
ALONSO A. Regiones microsatélite del genoma humano (Short Tandem Repeats). Aplicaciones en Genética Forense". La prueba de ADN en medicina forense. María Begoña Martínez Jarreta. Ed. Manson, Barcelona; 1999. [ Links ]
BUSTOS I, ACOSTA MA, BRAVO MLJ, BUILES JJ, CARABALLO LR, et al. Colombia: país genéticamente megadiverso en poblaciones humanas caracterizadas por sistemas STRs. VI jornadas de genética forense. Grupo español-portugués de la sociedad internacional de genética forense. 4 al 7 de octubre. Villa Carlospaz, Córdoba, Argentina; 2001 [ Links ]
JEFFREYS AJ, WILSON V, THEIN SL. Hypervariable minisatellite regions in human DNA. Nature. 1985;314:67-73. [ Links ]
KRENKE B, TEREBA A, ANDERSON S, BUEL E, CULHANE S, FINIS C, et al. Validation of a 16-Locus Fluorescent Multiplex System. J Forensic Sci. 2002;47:773-785. [ Links ]
LEWIS P, ZAYKIN D. Genetic Data Analysis: Computer program for allelic data analysis. Free program distributed by the authors. http://lewis.eeb.uconn.edu/lewishome/software.html. [ Links ]
LUQUE J. Texto ilustrado de biología molecular e ingeniería genética. 1 ed. Madrid: Ediciones Harcourt S.A; 2001. [ Links ]
MARTÍNEZ M. La prueba del ADN en medicina forense: la genética al servicio de la ley en el análisis de indicios criminales y en la investigación biológica de la paternidad. Primera edición. Barcelona: Editorial Masson; 1999. [ Links ]
MILLER S, DYKES D AND POLESKY H. Simple salting out procedure for extracting DNA from human nucleated cells. Nucl Acids Res. 1988;16:1215. [ Links ]
REY M, GUTIERREZ A, SCHROEDER B, USAQUEN W, CARRACEDO A, BUSTOS I, et al. Allele frequencies for 13 STRs from two Colombian populations: Bogotá and Boyacá. Forensic Sci Int. 2003;136:83-85. [ Links ]
RAO C, OLDROYD N AND PHILIPS H. Development of the AmpF1STR®Sefiler amplification kit: a new multiplex containing the highly discriminating ACTBP2 (SE33) locus. Int J Legal Med. 2004;118:224-234. [ Links ]
SENADO DE LA REPUBLICA DE COLOMBIA. Ley 721 de 20001, diciembre 24, por medio de la cual se modifica la ley 75 de 1968. Diario oficial N. 44.661, 29 de diciembre, 2001. [ Links ]
SLATKIN M. A measure of population subdivision based on microsatellite allele frequencies. Genetics. 1995;139:457-462. [ Links ]
WAINSCOAT J, HILL AL, BOYCE J, FLINT M, HERNANDEZ SL, THEIN JM, et al. Evolutionary relationships of human population from an analysis of nuclear DNA polymorphisms. Nature. 1986;319:491-493. [ Links ]














