Services on Demand
Journal
Article
Indicators
-
 Cited by SciELO
Cited by SciELO -
 Access statistics
Access statistics
Related links
-
 Cited by Google
Cited by Google -
 Similars in
SciELO
Similars in
SciELO -
 Similars in Google
Similars in Google
Share
Acta Biológica Colombiana
Print version ISSN 0120-548X
Acta biol.Colomb. vol.15 no.2 Bogotá Mayo/Aug. 2010
ESTRATEGIA DE SILENCIAMIENTO GÉNICO EN YUCA PARA LA VALIDACIÓN DE GENES DE RESISTENCIA
Strategy of Gene Silencing in Cassava for Validation of Resistance Genes.
SIMÓN CORTÉS1, Biólogo; CAMILO LÓPEZ1, Ph. D. 1 Universidad Nacional de Colombia, Facultad de Ciencias,Departamento de Biología. Bogotá, Colombia, celopezc@unal.edu.co
Presentado 7 de diciembre de 2009, aceptado 19 mayo de 2010, correcciones 28 de mayo de 2010.
RESUMEN
La yuca (Manihot esculenta) constituye la base de la alimentación para mas de 1.000 millones de personas en el mundo considerándose por esta razón un cultivo primordial para la seguridad alimentaria. La bacteriosis vascular ocasionada por la bacteria gram negativa Xanthomonas axonopodis pv. manihotis (Xam) es uno de los factores más limitantes para la producción en este cultivo. Un gen de resistencia candidato de yuca a la bacteriosis vascular, denominado RXam1, ha sido previamente identificado. En este trabajo se empleó la estrategia de silenciamiento génico mediado por el geminivirus ACMV (del inglés African Cassava Mosaic Virus) para validar la función del gen RXam1. Como control positivo se utilizó el gen su, cuyo silenciamiento produce blanqueamiento en las hojas. Plantas de la variedad SG10735 fueron bombardeadas con las construcciones ACMV-A-SU + ACMV-B y ACMV-A-RXam1 + ACMV-B. La eficiencia de silenciamiento empleando el gen su fue baja, observándose un fenotipo de blanqueamiento en solo una de siete plantas. En las plantas posiblemente silenciadas en el gen RXam1, no se logró identificar siRNAs correspondientes a este gen, aunque si se observó una leve disminución en la expresión de RXam1 en una de las plantas evaluadas. Las curvas de crecimiento para la cepa Xam CIO136 en plantas de yuca inoculadas mostraron una leve pero no significativa diferencia en la susceptibilidad de las plantas silenciadas con respecto a las no silenciadas.
Palabras clave: Yuca, VIGS, resistencia, bacteriosis vascular.
ABSTRACT
Cassava (Manihot esculenta) is a major source of food for more than 1000 million people in the world and constitutes an important staple crop. Cassava bacterial blight, caused by the gram negative bacterium Xanthomonas axonopodis pv. manihotis, is one of the most important constraints for this crop. A candidate resistance gene against cassava bacterial blight, named RXam1, has been identified previously. In this work, we employed the gene silencing approach using the African Cassava Mosaic Virus (ACMV) to validate the function of the RXam1 gene. We used as positive control the su gen, which produce photoblanching in leaves when is silenced. Plants from the SG10735 variety were bombardment with the ACMV-A-SU+ACMV-B y ACMV-A-RXam1+ACMV-B constructions. The silencing efficiency employing the su gene was low, only one of seven plants showed photoblanching. In the putative silenced plants for the RXam1 gene, no presence of siRNAs corresponding to RXam1 was observed; although a low diminution of the RXam1 gene expression was obtained. The growth curves for the Xam strain CIO136 in cassava plants inoculated showing a little but no significance difference in the susceptibility in the silenced plants compared to not silenced.
Key words: Cassava, VIGS, resistance, cassava bacterial blight.
INTRODUCCIÓN
La base de la resistencia vegetal a los patógenos esta en su capacidad de reconocer moléculas presentes en el patógeno. Las plantas emplean un grupo de receptores localizados en la membrana vegetal llamados PRRs (del inglés pattern recognition receptors) para reconocer moléculas microbianas conservadas llamadas PAMPs o MAMPS (del inglés Pathogen-or Microbe-Associated Molecular Patterns) (Bent y Mackey, 2007). Este reconocimiento enciende la primera rama de la inmunidad vegetal llamada PTI (del inglés PAMP triggered immunity) (Jones y Dangl, 2006). Los PRRs presentan los dominios conservados LRR (del inglés leucine rich repeats) y STK (del inglés serine threonine kinase) (Zipfel, 2008). Algunos patógenos adaptados para infectar plantas huésped han evolucionado un tipo particular de proteínas llamadas efectores, los cuales son introducidos dentro de las células vegetales para de esta manera suprimir la PTI (Jones y Dangl, 2006). Las plantas, a su vez, han evolucionado y han desarrollado las proteínas de Resistencia (proteínas R), las cuales son capaces de reconocer de manera específica algunos de los efectores y encienden la segunda rama de la inmunidad vegetal llamada Resistencia raza específica o ETI (del inglés Effector-TriggeredImmunity). La mayoría de las proteínas R poseen un dominio NBS (del inglés Nucleotide Binding Site) y un dominio LRR. Esta gran clase de proteínas R puede ser subdividida en dos clases dependiendo de si contienen o no un dominio TIR (del inglés Toll Interleukin Related) en su extremo N-terminal (Caplan et al., 2008).
La yuca (Manihot esculenta) es un cultivo estratégico para Colombia; muchas familias campesinas dependen de la yuca para su sustento, además de servir como materia prima en varios procesos industriales y como fuente de alcohol carburante (El-Sharkawy, 2004). La yuca es cultivada en más de 90 países y constituye la base de la alimentación de más de 1.000 millones de personas en el mundo (FAOSTAT, 2008). Según la FAO un aumento en la producción de yuca podría solucionar, al menos parcialmente, el problema de hambre en el mundo (FAOSTAT, 2008). A pesar de su relativa tolerancia a la mayoría de sus potenciales patógenos, la producción de yuca se puede ver severamente afectada por la bacteriosis vascular. La bacteriosis vascular de la yuca o añublo bacteriano (CBB, del inglés Cassava Bacterial Blight) es una enfermedad endémica importante en Latinoamérica y África (Lopez et al., 2006). La bacteriosis vascular es causada por la bacteria Xanthomonas axonopodis pv. manihotis (Xam), un patógeno foliar y vascular (Verdier et al., 2004). Las pérdidas causadas por la bacteriosis pueden alcanzar incluso el 80 o 100% de la cosecha si las condiciones del medio son favorables para su desarrollo y si no se adoptan prácticas agronómicas y fitosanitarias adecuadas para su control (Verdier et al., 2004). A pesar de que existen variedades resistentes, estas no poseen buenas cualidades culinarias y por esta razón no han sido adoptadas por los productores. El desarrollo de variedades resistentes mediante estrategias de mejoramiento convencional ha permitido elevar los niveles de resistencia en ciertos casos (Jorge et al., 2000), sin embargo las características propias de la yuca, tales como su largo ciclo reproductivo, su naturaleza tetraploide y su alta heterocigocidad han dificultado la obtención de mejores resultados.
La identificación y caracterización de genes que codifican para PRRs o proteínas R permitiría contribuir al desarrollo de estrategias de mejoramiento convencionales o de transformación genética para lograr obtener variedades resistentes y con óptimas cualidades culinarias y agronómicas. Hasta el momento no se ha logrado clonar el primer gen de resistencia a alguna de sus enfermedades. Sin embargo, en los últimos años varios genes candidatos de resistencia se han identificado en este cultivo empleando cebadores degenerados complementarios a las secuencias codificantes para el dominio NBS y TIR (Lopez et al., 2003). Adicionalmente un gen candidato fue obtenido en yuca empleando cebadores diseñados a partir del gen de resistencia Xa21 de arroz, el cual confiere resistencia a Xanthomonas oryzae pv. oryzae y codifica para una proteína de tipo LRR-STK (Song et al., 1995). Este gen candidato se encuentra ligado a un QTL que explica 13% de la resistencia a la cepa CIO136 de Xam (Jorge et al., 2000). Este gen ha sido llamado RXam1 (Resistance to Xam 1). Los análisis de secuencia y estudios de expresión de RXam1 entre un cultivar sensible y otro resistente ha permitido identificar: i) la presencia de codones de parada en el gen procedente del cultivar sensible; ii) un marco abierto de lectura en el gen proveniente del cultivar resistente; iii) la inducción de la expresión de RXam1 72 horas post-inoculación con la cepa CIO136 en el cultivar resis-tente y iv) el gen no es expresado en el cultivar sensible (López et al., en prensa). Estos datos sugieren que es un excelente gen de resistencia candidato, sin embargo es necesaria su validación funcional.
Hasta recientemente, la única estrategia para la validación de genes en yuca era mediante transformación genética. Este procedimiento además de largo y dispendioso requiere la obtención y clonación completa del gen, lo cual suele ser difícil para genes de gran tamaño. Alternativamente, la validación funcional puede llevarse a cabo mediante la eliminación de la expresión del gen y la evaluación de su efecto en el fenotipo. Esta estrategia se basa en el proceso de silenciamiento génico, el cual es un mecanismo natural de resistencia de las plantas a la infección viral (Eamens et al., 2008). Al introducir un gen blanco en un vector viral e infectar plantas se producirá temporalmente la eliminación del ARNm en cuestión a causa de la producción de pequeños ARNs de interferencia (siARNs) por parte de la planta, los cuales activan la maquinaria de silenciamiento génico de manera dirigida hacia el gen de interés, y se podrá entonces evaluar su efecto fenotípicamente. Esta estrategia es conocida con el nombre de VIGS (del inglés Virus Induced Gene Silencing), y ha sido extensamente empleada en plantas modelo, principalmente perteneciente a la familia de Solanceaeas (Brigneti et al., 2004). Recientemente se ha reportado la implementación de la estrategia de VIGS para silenciar genes endógenos en yuca (Fofana et al., 2004). Dado que los geminivirus portan dos moléculas de ADN (tipo A y B) (Vanitharani et al., 2005), en el silenciamiento mediado por geminivirus se ha modificado la molécula de tipo A con un sitio de multiclonaje que permite la introducción del gen blanco que se busca silenciar. La aplicación de esta estrategia requiere la inoculación de plantas de yuca con el geminivirus ACMV (del inglés African Cassava Mosaic Virus) (Fofana et al., 2004). La estrategia de VIGS mediada por geminivirus ha mostrado ser efectiva en yuca permitiendo por ejemplo el silenciamiento de un gen que cataliza el primer paso en la síntesis de linamarina, el principal compuesto glucósido cianogénico en yuca (Fofana et al., 2004).
En este trabajo nosotros buscamos implementar la estrategia de VIGS empleando el geminivirus ACMV de yuca para validar la función del gen candidato RXam1, en la variedad SG107-35, la cual es resistente a la bacteriosis vascular.
MATERIALES Y MÉTODOS
ELABORACIÓN DE LAS CONSTRUCCIONES PARA VIGS
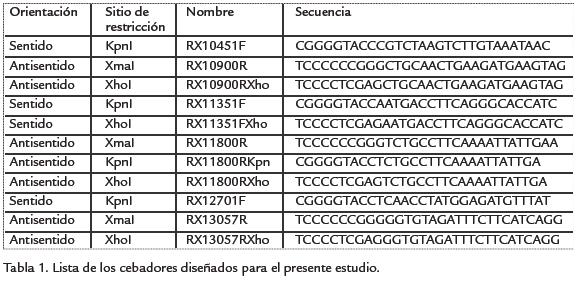
A partir de la secuencia del gen RXam1, se diseñaron cebadores para amplificar fragmentos de 450 pb. En total se generaron once cebadores (Tabla 1). Los cebadores sentido contienen los sitios de corte para la enzima KpnI mientras que los cebadores antisentido contienen el sitio de corte para la enzima XhoI. Adicionalmente se incluyeron tres y cuatro nucleótidos adicionales en los cebadores para facilitar la digestión enzimática de los productos de PCR. Esta disposición de sitios de restricción permite la inserción en antisentido de los fragmentos amplificados. La reacción de PCR se llevó a cabo empleando el siguiente protocolo de PCR: 2 min a 95 ºC; 35 ciclos de 30 seg a 95 ºC, 30 seg a 55 ºC, 30 seg 72 ºC; 5 min a 72 ºC. Se empleó el kit GoTaq green mastermix (Promega), con 400 nM de cebadores y 80 ng de ADN genómico de plantas de yuca de la variedad SG 107-35. Los productos de amplificación fueron digeridos con las enzimas KpnI y XhoI, al igual que el vector ACMVΔCP, el cual corresponde al ADN-A silvestre viral, al que se le ha reemplazado la secuencia que codifica para la proteína de la cápside por un sitio de multiclonaje (Fofana etal., 2004). La reacción de ligación se realizó con T4 ADN ligasa (Promega) siguiendo las recomendaciones del fabricante. Se tomó 1 µL de la reacción para transformar mediante choque térmico bacterias de E. coli DH5αy se platearon en medio LB con ampicilina 100 µg/mL. Se seleccionaron dos colonias de cada transformación y se extrajo ADN plasmídico empelando el kit de purificación de plásmidos de Qiagen. El plásmido fue digerido con KpnI y XhoI siguiendo las recomendaciones del fabricante (Promega). Cultivos de las colonias positivas se almacenaron en stock de glicerol al 40% a -80 ºC y las muestras de ADN plasmídico se enviaron a secuenciar a un laboratorio de servicios certificado.
Adicionalmente se empleó como control la construcción que contiene 476 bp del gen sulfur (su) de N. tabacum clonado en antisentido. El silenciamiento de este gen resulta en un fenotipo de moteado amarillo-blanco en las hojas (Fofana et al., 2004). También se realizó la extracción del ADN viral ACMV-A y B mediante purificación empleando el kit de Qiagen.
BOMBARDEO DE PLANTAS CON LAS CONSTRUCCIONES
A 30 mg de oro particulado de 0,6 micrones de diámetro (InBio Gold) se le realizó tres lavados con etanol al 100%, se resuspendió en H2O y se realizaron alícuotas de 50ul, conteniendo 3 mg de oro. Posteriormente a cada alícuota se le adicionó 5 µg de ADN (ACMV-A con la construcción + ACMV-B) gota a gota mientras se aplicaba vortex y 20 µL de espermidina 0,1 M. A continuación se adicionó 50 µL de CaCl2 2,5 M. Se dejó a temperatura ambiente por 10 minutos, se centrifugó por dos minutos, se removió el sobrenadante y se agregó 50 µL de etanol al 100% para resuspender. Se tomó 9 a 10 µL de la suspensión de oro para agregarla al centro del macrocargador (Bio-rad) insertado en el respectivo soporte. La preparación se dejó secar en cámara de flujo laminar. El bombardeo se realizó con el dispositivo PDS-1000 He System (Bio-Rad). Se emplearon plantas de la variedad SG107-35 y TMS60444 propagadas in vitro y endurecidas durante 3-4 semanas en suelo. Las plantas bombardeadas se mantuvieron en cámara de crecimiento, con una humedad relativa de 60%, temperatura de 28 ºC y nivel de luz de 600 µmol, con un fotoperiodo de 16 horas de luz y 8 horas de oscuridad.
EVALUACIÓN DE SILENCIAMIENTO Y DETECCIÓN DE SIARNS
El ARN de plantas de yuca se extrajo empleando el método de Trizol siguiendo las recomendaciones del fabricante (Invitrogen, Carlsbad, Calif.). El ARN fue separado mediante electroforesis en geles de poliacrilamida al 15% con urea (15%). La parte superior del gel fue cortada y teñida con bromuro de etidio para documentar la integridad del ARN. La parte inferior del gel se transfirió a una membrana de nylon mediante transferencia capilar por 24 horas y el ARN se fijó a la membrana mediante UV crosslinking. Para la generación de la sonda, se diseñaron cebadores que permiten amplificar un producto de 2607 pb correspondiente al gen RXam1. Estos cebadores contenían los sitios de corte para KpnI en el extremo 5’ y XmaI en el 3’. Este producto de PCR fue clonado en el vector pCR®2.1-TOPO® (Invitrogen, Carlsbad, Calif.), el cual tiene sitio promotor para la RNA polimerasa T7. La ligación y transformación se realizó bajo los mismos procedimientos descritos anteriormente. A partir de las colonias positivas se extrajo el ADN plasmídico y se comprobó la inserción del fragmento de RXam1 mediante digestión con KpnI. Sobre esta construcción se realizó una reacción de transcripción in vitro con el kit DIG RNA Labeling kit (SP6/T7) (Roche), siguiendo las recomendaciones del fabricante. La reacción se diluyó hasta un volumen final de 100 µL con H2O tratada con DEPC para llegar a una concentración de 100 ng/µL. Se tomaron 50µL de sonda y se mezclaron con 50 µL de buffer de hidrólisis. La reacción de hidrólisis se llevó a cabo por 10 minutos a 95 ºC, se detuvo con 100 µL de Tris 0,1 M pH 7,0 y se puso en hielo por dos minutos. La hibridación se llevó a cabo siguiendo las recomendaciones del kit -DIG application manual for filter hybridization- (Roche molecular biochemicals). En resumen, se adicionó 500 µL de solución de hibridación (Roche) a la sonda, se denaturó por ebullición durante 5 minutos y se adicionaron 10 mL de solución de hibridación. La sonda se agregó a la membrana prehibridada por una hora a 42 ºC con 5 mL de buffer de hibridación. La hibridación se llevo a cabo toda la noche a 42 ºC. La membrana se lavó dos veces con 2X SSC+0,1% SDS por 5 minutos a 42 ºC, posteriormente se lavó dos veces con 0.1X SSC+ 0,1% SDS por 15 minutos a 42 ºC. Finalmente se realizó la detección quimioluminiscente empleando el reactivo CDP-Star (Roche).
SÍNTESIS DE ADNC Y RT-PCR
A partir del ARN se realizó la síntesis de ADNc empleando el kit RevertAid™ First Strand cDNA Synthesis (Fermentas), utilizando una mezcla de cebadores al azar. Para las reacciones de PCR se empleó 5 µL de la síntesis de ADNc en un volumen final de 50 µl. Se emplearon los cebadores para RXam1 y para tubulina. La reacción se alicuotó en cuatro reacciones de 10 µL, se realizó el PCR y se retiraron muestras del termociclador a los 15, 20, 25 y 30 ciclos. Se sirvieron 8 µL de producto de PCR y se compararon los rangos de expresión de RXam1 respecto a tubulina entre las diferentes plantas.
CURVAS DE CRECIMIENTO
Plantas de yuca de la variedad SG107-35 propagadas in vitro y endurecidas en suelo fueron inoculadas con la cepa de Xam CIO136. A partir de un cultivo bacteriano fresco crecido en medio LPGA se realizaron diluciones a DO de 0,2 y se inocularon en las hojas mediante punción. Con un sacabocados se tomó el tejido vegetal del punto de inoculación a los tiempos 0, 3, 6 y 10 días post inoculación. El tejido vegetal se maceró y se realizaron diluciones seriadas a partir de las cuales se tomó 10 µl para crecer en medio LPGA. El número de unidades formadoras de colonias se contó después de crecimiento a 28 ºC por dos días.
RESULTADOS
ELABORACIÓN DE LAS CONSTRUCCIONES PARA RXAM1
A partir de la secuencia conocida del gen RXam1 se sintetizaron diferentes cebadores que permitieron la amplificación de diferentes regiones del gen (Fig. 1), con el fin de determinar cuál de las regiones permitiría una mayor eficiencia en el silenciamiento. inicialmente se diseñaron los cebadores conteniendo el sitio de corte para la enzima XmaI en el cebador antisentido. Sin embargo, los análisis de restricción demostraron que el vector de silenciamiento para VIGS, ACMV-A, carece del sitio de corte para la enzima XmaI, a pesar de que la presencia de este sitio ha sido reportado en la literatura (Fofana et al., 2004). En consecuencia fue necesario rediseñar estos cebadores conteniendo el sitio de corte para la enzima XhoI, el cual también está presente en el sitio de multiclonaje del vector y cuya secuencia de reconocimiento no se encuentra en los fragmentos del gen RXam1 que se buscaba amplificar.
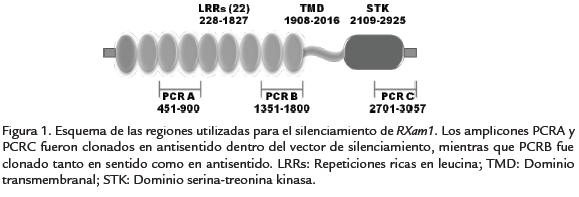
Las amplificaciones realizadas sobre el ADN genómico de la variedad SG107-35 con las diferentes combinaciones de cebadores resultaron exitosas, obteniéndose amplicones de los tamaños esperados (Fig. 2). Además de las tres regiones seleccionadas para la elaboración de las construcciones, se amplificó la región central con los sitios de restricción intercambiados para clonar el fragmento en sentido y no en antisentido como los demás. Esta estrategia permitiría evaluar si el fragmento en sentido proporcionaría una mayor inducción del silenciamiento.

Los productos de PCR fueron digeridos con las enzimas correspondientes y clonados independientemente en el vector ACMV-A previamente digerido. Las construcciones obtenidas fueron secuenciadas confirmándose de esta manera la correcta inserción de los fragmentos correspondientes al gen RXam1 en el vector ACMV-A.
BOMBARDEO DE PLANTAS CON LAS CONSTRUCCIONES
Los primeros experimentos de silenciamiento génico se llevaron a cabo sobre la variedad de yuca 60444, la cual ha sido el modelo de laboratorio para transformación genética y para los primeros estudios de silenciamiento génico (Fofana et al., 2004). Empleando la construcción que contiene el gen su (ACMV A-SU+ACMV B), el cual produce un fenotipo moteado amarillo-blanco en las hojas, se bombardearon siete plantas de la variedad 60444 y siete de la variedad SG107-35. Como control negativo se bombardearon plantas de las dos variedades con el vector vacío (ACMVΔCP+ACMV B). En las plantas infectadas con el vector vacío no se observó ningún fenotipo (Fig. 3C), lo cual concuerda con los reportes previos (Fofana et al., 2004). Para el caso de las plantas infectadas con ACMV-SU, el fenotipo de amarillamiento de las hojas se presentó de manera consistente en la variedad 60444 a los siete días post infección en cuatro de las siete plantas, y en cerca del 40% de las hojas, es decir, el silenciamiento no es completamente sistémico en las plantas en las que se produjo, y solo se presentó en el 60% de las plantas bombardeadas (Fig. 3A). Este comportamiento se mantuvo incluso hasta el día 21 (Fig. 3B). De las siete plantas de la variedad SG107-35 que se bombardearon con el constructo para el silenciamiento del gen su solo se observó fenotipo de silenciamiento en una de ellas, siendo consistente el fenotipo a los 15 días post bombardeo (Fig. 3D), sugiriendo que la eficiencia de silenciamiento es dependiente de la variedad de yuca que se emplee. Sin embargo se consideró que a pesar de no observarse un fenotipo contundente de silenciamiento en plantas de esta variedad si podría haberse producido un silenciamiento del gen su, aunque éste no fuera tan fuerte como para alcanzar a observarse un fenotipo a nivel macroscópico.

SILENCIAMIENTO DEL GEN RXAM1
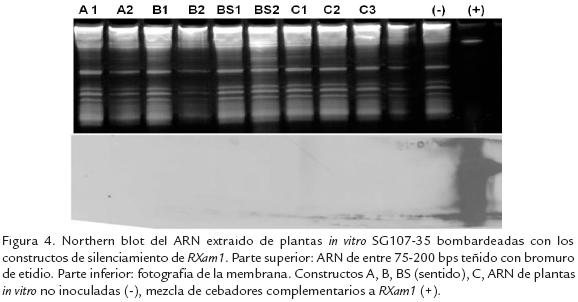
Para determinar cuál de las construcciones conteniendo los fragmentos correspondientes a las diferentes regiones del gen RXam1 producía un mayor nivel de silenciamiento, se procedió a realizar un bombardeo con cada construcción independiente sobre plántulas de yuca crecidas in vitro en cajas de petri. Siete días posterior al bombardeo se extrajo el ARN de cada grupo de plantas para la detección de siARNs. El ARN fue separado en un gel de poliacrilamida y la parte inferior del gel, donde se deben encontrar los siARNs, fue transferida a una membrana de nylon e hibridada con una sonda de ARN de 2609 pb correspondiente al gen RXam1 y obtenida mediante transcripción in vitro. Como control positivo del experimento se cargó una mezcla de los cebadores empleados y complementarios a RXam1 en el gel. Después de la hibridación, solo se observó una señal positiva en el control positivo (Fig. 4) y aunque la membrana se sometió a mayores tiempos de exposición no se observó señal positiva para ninguna muestra, indicando posiblemente que el silenciamiento en este tipo de plántulas no se llevo a cabo. En consecuencia se decidió emplear una mezcla con todas las construcciones para realizar el bombardeo sobre las plantas de yuca de la variedad SG107-35.
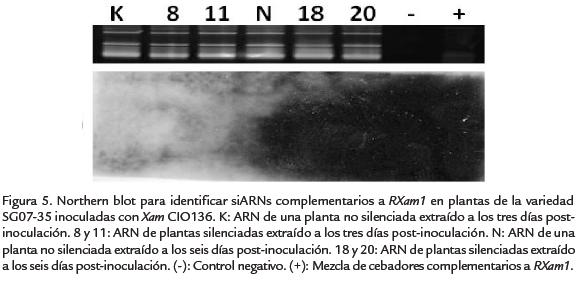
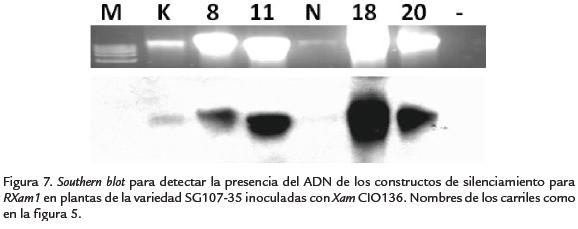
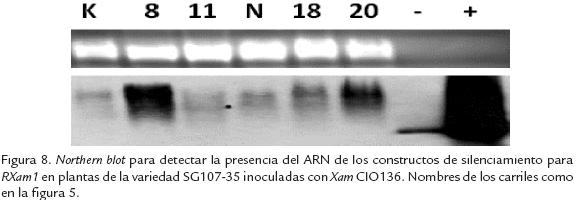
Para el silenciamiento del gen RXam1 se emplearon 21 plantas de 26 días de endurecimiento en suelo. Paralelamente se dejaron 15 plantas sin bombardear para realizar las comparaciones de crecimiento de bacterias entre plantas silenciadas y no silenciadas. A los 10 días después del bombardeo se realizó la inoculación con la cepa CIO136 de Xam. Se realizó una extracción de ARN de las plantas posiblemente silenciadas y de las plantas control, obtenido a los días tres y seis días post inoculación. Sobre este ARN se trató de determinar la presencia de siARNs, siguiendo la misma estrategia que se describió anteriormente. Sin embargo no se logró identificar siARNs en ninguna de las muestras de plantas (Fig. 5). Para comprobar la presencia de las construcciones virales en las plantas bombardeadas y control se extrajo ADN de estas mismas plantas y se determinó la presencia de los fragmentos de RXam1 mediante southern-blot, empleando como sonda una mezcla de los productos de PCR A y C de RXam1 marcados con digoxigenina (DIG) (Fig. 6). Como se observa en la figura 7, tanto en las plantas silenciadas y no silenciadas se detectó señal, siendo esta un poco más fuerte en las muestras de plantas silenciadas en comparación con las no silenciadas (Fig. 7). Estos resultados sugieren la presencia de las construcciones en estas plantas, aunque parte de la señal puede ser producto de la presencia endógena del gen RXam1 en el genoma de las plantas de yuca. Para evaluar la expresión de las construcciones, se realizó un Northern-blot empleando el ARN obtenido de estas plantas, y se observó una mayor presencia del transcrito RXam1 en las plantas posiblemente silenciadas (Fig. 8). Una vez más es imposible diferenciar si estos transcritos corresponden a la transcripción del gen endógeno o a la expresión de los fragmentos de RXam1 durante la replicación del geminivirus.

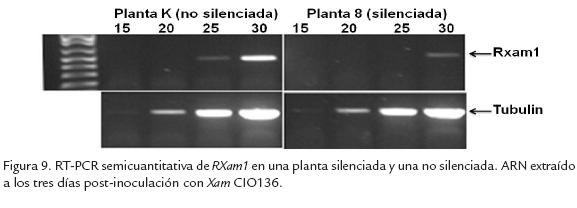
Para comprobar si se presentó silenciamiento génico de RXam1 mediado por las construcciones hechas sobre el geminivirus se realizó una RT-PCR semicuantitativa a partir de las plantas posiblemente silenciadas y no silenciadas. Para una de las plantas posiblemente silenciadas se observó una leve disminución en la expresión del gen RXam1 con respecto a una de las plantas no silenciadas (Fig. 9), sugiriendo que posiblemente si se presentó un leve silenciamiento génico.
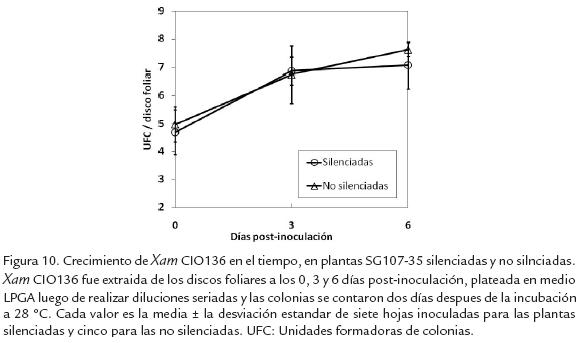
Las curvas de crecimiento realizadas sobre las plantas posiblemente silenciadas inoculadas con la cepa CIO136 mostraron un crecimiento continuo hasta el día tres, el cual se mantuvo relativamente constante hasta los seis días post-inoculación. En las plantas no silenciadas, las bacterias mantuvieron su crecimiento de manera continua hasta los seis días post-inoculación. Solo se observó una pequeña diferencia de incremento de susceptibilidad, no estadísticamente significativa, en las plantas silenciadas (Fig. 10). Si realmente se presentó silenciamiento génico en las plantas de SG107-35 y si el gen RXam1 efectivamente confiere resistencia a la cepa CIO136, hubiésemos esperado un mayor crecimiento bacteriano en las plantas silenciadas.
DISCUSIÓN
Uno de los principales factores que afectan la producción de yuca en el mundo es la bacteriosis vascular, ocasionada por la bacteria Xanthomonasaxonpodis pv. manihotis. Hasta el momento no existen genes de resistencia reportados en yuca para esta enfermedad, aunque algunos genes candidatos se han reportado. En particular, el gen RXam1, el cual está asociado a un QTL que explica el 13% de la resistencia a la cepa deXam CIO136. Para validar la función de genes en yuca se puede emplear la estrategia de transformación genética, en la cual se introduce el gen completo en una variedad susceptible esperando que ésta se vuelva resistente. Este tipo de estrategias en yuca es dispendioso y largo pues requiere la clonación completa del gen, que para el caso de RXam1 es particularmente complicado dado su gran tamaño (3.600 pb). Adicionalmente el proceso de transformación y regeneración de plantas transgénicas en yuca puede tardar cerca de dos años y no se ha establecido para todas las variedades. Recientemente se ha reportado la estrategia de silenciamiento génico mediado por geminivirus en yuca, la cual abre la posibilidad de validar la función de genes en yuca mediante silenciamiento génico (Fofana et al., 2004). En esta estrategia, la infección de un vector viral conteniendo un fragmento del gen blanco a silenciar, en plantas de yuca, permite desencadenar la respuesta de defensa frente al virus, generando siARNs contra las regiones virales y también contra el inserto que contiene el vector viral, trayendo como consecuencia el silenciamiento del gen endógeno. Nosotros buscamos desarrollar esta estrategia para la validación de genes de resistencia candidatos en yuca a la bacteriosis vascular empleando como modelo el gen RXam1.
La estrategia de VIGS reportada por Fofana et al. (Fofana et al., 2004) se estableció sobre plantas de la variedad 60444. Para validar la función de RXam1, nosotros buscamos establecer el sistema sobre una variedad resistente, de tal forma que el silenciamiento génico, provocará la pérdida de parte de la resistencia o incluso puede generar susceptibilidad. La variedad 60444 parece ser susceptible a la cepa CIO136 (datos no mostrados), razón por la cual no la empleamos en este estudio. La variedad SG107-35 es altamente resistente a la bacteriosis vascular y en particular a la cepa CIO136 (Verdier, comunicación personal). Por esta razón nosotros decidimos evaluar si la estrategia de silenciamiento génico empleando el vector ACMV podría funcionar sobre esta variedad. El silenciamiento génico para el gen marcador su, el cual produce un fenotipo claramente visible de amarillamiento en las hojas, nos mostró que en nuestras manos el sistema funcionaba adecuadamente ya que las plantas 60444 silenciadas con este gen mostraron un claro amarillamiento. Sin embargo, solo una de las siete plantas de la variedad SG107-35 silenciadas con el gen su mostró un claro fenotipo, aunque el amarillamiento fue menos extenso sobre la superficie foliar y también tardó más en presentarse. Estos datos sugieren que el silenciamiento génico en yuca es dependiente de la variedad que se emplee. En tal sentido, es necesario realizar un tamizaje para determinar cuáles son las variedades más susceptibles de ser silenciadas empleando el vector ACMV. Es posible que SG107-35 presente también cierta resistencia al geminivirus, haciendo que éste no pueda replicarse y moverse dentro de los tejidos vegetales trayendo como consecuencia una reducción en las posibilidades de silenciamiento génico. En Arabidopsis por ejemplo, se ha visto que el VIGS no es una estrategia muy eficaz porque ha sido difícil encontrar un virus que permita replicarse lo suficiente como para inducir el silenciamiento génico pero que no cause enfermedad en la planta (Robertson, 2004).
Nosotros buscamos identificar cual de los fragmentos del gen RXam1 podría generar un mayor silenciamiento, sin embargo no pudimos identificar siARNs en una prueba piloto realizada sobre plantas crecidas in vitro en cajas de petri. Es posible que en este estadio la capacidad infectiva del geminivirus sea menor para replicarse e inducir siARNs o que las plantas de la variedad SG107-35 no tengan la capacidad de desencadenar una respuesta de silenciamiento. Esto explicaría posiblemente la ausencia de siARNs en las muestras evaluadas. Sin embargo decidimos realizar el silenciamiento mezclando los diferentes fragmentos, con la idea de que algunos o todos fueran suficientes para inducir el silenciamiento.
A pesar de que solamente una de las siete plantas SG107-35 silenciadas para el gen su mostró fenotipo, decidimos realizar los experimentos de silenciamiento génico de RXam1 en esta variedad, asumiendo que al igual que con el gen su, algunas de las plantas hubiese sido silenciada en el gen RXam1. Los análisis de Southern y Northern-blot sugieren que en las plantas silenciadas se encuentran y se expresan los fragmentos del gen RXam1 insertados en el vector viral ECMV. Los análisis de PCR semicuantitativo sobre el ADNc muestran que para una de las plantas silenciadas se presentó una tenue disminución en la expresión del gen RXam1 comparadas con las plantas no silenciadas. Sin embargo las curvas de crecimiento no permitieron demostrar una significativa pérdida de la resistencia en la variedad de yuca SG107-35 a la cepa CIO136, como habría de esperarse si el gen RXam1 hubiese sido realmente silenciado y/o fuese responsable de la resistencia a esta cepa. Es importante destacar que la resistencia explicada por este gen es solo del 13%, razón por la cual es bastante difícil poder detectar una disminución en este porcentaje en la resistencia a pesar de que pudiese haberse presentado silenciamiento. Las curvas de crecimiento pueden dar un estimativo cuantitativo de una diferencia de este orden de magnitud entre variedades resistentes y susceptibles, pero es posible que los niveles de silenciamiento no sean tan altos como para detectar estas diferencias.
CONCLUSIÓN
Nuestros resultados no permiten demostrar (o refutar) que el gen RXam1 esté implicado en la resistencia a la cepa CIO136. Sin embargo logramos demostrar que la estrategia de VIGS empleando el geminivirus ECMV funciona de manera adecuada, pero que debe considerarse la diferencia varietal a la hora de realizar estudios funcionales en variedades particulares. El geminivirus no se ha reportado en Colombia, por lo que por razones de bioseguridad este tipo de experimentos no se pueden desarrollar en el país. Sería interesante poder desarrollar vectores para VIGS a partir de los virus que se encuentran en Colombia y que infectan la yuca, aunque su incidencia es baja o casi nula en los cultivos de yuca en el país. Continuar con este tipo de estudios sobre otras variedades de yuca y con otros genes candidatos permitirá validar y contar con genes de resistencia a la bacteriosis vascular, los cuales podrían ser introducidos en las variedades comerciales para lograr una mayor producción de yuca en el país, más limpia y amigable con el medio ambiente.
AGRADECIMIENTOS
A la división de investigación de la Universidad Nacional de Colombia sede Bogotá. Al Dr. Patil Basavaprabhu por su colaboración en la realización de los experimentos de Biología Molecular, al Dr. Nigel Taylor por su colaboración en las áreas de cultivo de tejidos, propagación y mantenimiento de plantas adultas. Al Dr. Claude Fauquet por poner a nuestra disposición las instalaciones del International Laboratory for Tropical Agricultural Biotechnology (ILTAB) en el Donald Danforth Plant Science Center. Este trabajo fue financiado por la DIB a través de la convocatoria nacional de investigación 2008, proyecto número 7915: -Validación de genes de resistencia candidatos a la bacteriosis vascular en yuca mediante VIGS-.
BIBLIOGRAFÍA
BENT AF, MACKEY D. Elicitors, Effectors, and R Genes: The New Paradigm and a Lifetime Supply of Questions. Annu Rev Phytopathol. 2007;45:399-436.
[ Links ]BRIGNETI G, MARTIN-HERNANDEZ AM, JIN H, CHEN J, BAULCOMBE DC, et al. Virus-induced gene silencing in Solanum species. Plant J. 2004;39:264-272.
[ Links ]CAPLAN J, PADMANABHAN M, DINESH-KUMAR SP. Plant NB-LRR immune receptors: from recognition to transcriptional reprogramming. Cell Host Microbe. 2008;3:126-135.
[ Links ]EAMENS A, WANG MB, SMITH NA, WATERHOUSE PM. RNA silencing in plants: yesterday, today, and tomorrow. Plant physiol. 2008;147:456-468.
[ Links ]EL-SHARKAWY MA. Cassava biology and physiology. Plant Mol Biol. 2004;56:481-501.
[ Links ]FAOSTAT. FAO database. Food and Agriculture Organization of the United Nations, Rome: FAO; 2008. Disponible en http://faostat.fao.org/site/567/default.aspx
[ Links ]FOFANA IB, SANGARE A, COLLIER R, TAYLOR C, FAUQUET CM. A geminivirus -induced gene silencing system for gene function validation in cassava. Plant Mol Biol. 2004;56:613-624.
[ Links ]JONES JD, DANGL JL. The plant immune system. Nature. 2006;444:323-329.
[ Links ]JORGE V, FREGENE MA, DUQUE MC, BONIERBALE MW, TOHME J, et al. Genetic mapping of resistance to bacterial blight disease in cassava (Manihot esculenta Crantz). Theor Appl Genet. 2000;101:865-872.
[ Links ]LOPEZ CE, ZULUAGA AP, COOKE R, DELSENY M, TOHME J, et al. Isolation of Resistance Gene Candidates (RGCs) and characterization of an RGC cluster in cassava. Mol Genet Genomics. 2003;269:658-671.
[ Links ]LÓPEZ C, RESTREPO S, VERDIER V. Limitaciones en la Bacteriosis Vascular de la Yuca: Nuevos Avances. Acta biol Colomb. 2006;11;21-45.
[ Links ]ROBERTSON D. VIGS Vectors for gene silencing: Many Targets, Many Tools. Ann Rev Plant Biology. 2004;55:495-519.
[ Links ]SONG WY, WANG GL, CHEN LL, KIM HS, PI LY, et al. A receptor kinase-like protein encoded by the rice disease resistance gene, Xa21. Science. 1995;270:1804-1806.
[ Links ]VANITHARANI R, CHELLAPPAN P, FAUQUET CM. Geminiviruses and RNA silencing. Trends Plant Sci. 2005;10:144-151.
[ Links ]VERDIER V, RESTREPO S, MOSQUERA G, JORGE V, LOPEZ C. Recent progress in the characterization of molecular determinants in the Xanthomonas axonopodis pv. manihotis-cassava interaction. Plant Mol Biol. 2004;56:573-584.
[ Links ]ZIPFEL C. Pattern-recognition receptors in plant innate immunity. Current opinion in immunology. 2008;20:10-16.
[ Links ]













