Services on Demand
Journal
Article
Indicators
-
 Cited by SciELO
Cited by SciELO -
 Access statistics
Access statistics
Related links
-
 Cited by Google
Cited by Google -
 Similars in
SciELO
Similars in
SciELO -
 Similars in Google
Similars in Google
Share
Acta Biológica Colombiana
Print version ISSN 0120-548X
Acta biol.Colomb. vol.17 no.3 Bogotá Sept./Dec. 2012
ANÁLISIS GENÓMICO-FUNCIONAL DE PROTEÍNAS CON DOMINIOS TIR EN YUCA
Functional Genomic Analysis of Cassava Proteins with TIR domains
VERÓNICA ROMÁN REYNA1, Bióloga; CAMILO LÓPEZ1, Ph. D.
1 Grupo Manihot biotec, Departamento de Biología, Facultad de Ciencias. Universidad Nacional de Colombia. Bogotá, Colombia. Correspondencia: Camilo López, celopezc@unal.edu.co
Presentado el 23 de agosto de 2012, aceptado el 9 de octubre de 2012, correcciones el 16 de octubre de 2012.
RESUMEN
Dentro de las proteínas implicadas en inmunidad de plantas y animales se encuentran aquellas que poseen un dominio TIR (Toll Interleukin Receptor). El objetivo de este trabajo fue realizar un análisis genómico global de las proteínas que presentan un dominio TIR en yuca y discernir su posible función en la resistencia a la bacteriosis vascular. En el proteoma de yuca se logró identificar 46 proteínas con dominios TIR, los cuales fueron divididos en cuatro categorías según la presencia o no de otros dominios: TIR (T), TIR- NB (TN), TIR-LRR (TL) y TIR-NB-LRR (TNL). El 56,5 % de las 46 proteínas corresponde a la categoría TNL. Mediante alineamientos múltiples se encontró que no todos los dominios TIR de yuca presentan la región aE implicada en la dimerización y activación de las respuestas de inmunidad. Tres de las cuatro categorías de proteínas (T, TNL y TN) presentan un mayor número de sustituciones sinónimas, sugiriendo que no están implicadas en procesos de reconocimiento. Por medio de doble híbrido de levadura y agroinfiltración se analizaron dos dominios TIR que no presentan la región aE, encontrando que ambos son capaces de formar homo y heterodímeros pero no desencadenan respuestas de defensa. Con este trabajo se pudo concluir que algunas proteínas que poseen dominios TIR pueden funcionar como adaptadores en la transducción de la señal con otras proteínas de resistencia. Además, se puso en evidencia que no siempre la región aE es importante para la dimerización, pero sí para activar las señales de respuestas de defensa.
Palabras clave: bacteriosis vascular, dominio TIR, genómica, resistencia, yuca.
ABSTRACT
Proteins containing a TIR domain (Toll Interleukin Receptor) are involved in plant and animal immunity. The aim of this work was to carry out an overall genomic analysis of cassava proteins with a TIR domain and discern their possible role in resistance to cassava bacterial blight. In total 46 proteins with a TIR domain were identified in the cassava proteome and were classed in four categories according the presence or absence of other domains: TIR (T), TIR-NB (TN), TIR-LRR (TL) and TIR-NB-LRR (TNL). 56.6 % of these 46 proteins have TIR, NB and LRR domains. Using multiple alignments it was possible to demonstrate that not all cassava TIR domains contain the aE region, involved in dimerization and activation of immune responses. Three of the four proteins categories (T, TNL and TN) presented a higher number of synonymous substitutions suggesting that they are not involved in recognition process. Two TIR domains not presenting the aE region were analyzed by yeast two hybrid assays and by agroinfiltration, finding that both are able to form homo and heterodimers, but they do not trigger defense responses. With this study it was possible to conclude that TIR domains can function as adaptors in the signal transduction with other resistance proteins. In addition, it became clear that not always the aE region is important for TIR dimerization but it seems necessary to activate defense responses signals.
Keywords: Bacterial blight, cassava, genomics, TIR domain, resistance.
INTRODUCCIÓN
La evolución de la inmunidad de plantas y animales está sujeta a una relación dinámica entre los cambios de las plantas y animales para mejorar el reconocimiento y por otro lado, del patógeno para evadir su detección. Las bases moleculares del reconocimiento y respuesta frente a patógenos por parte de plantas y animales son similares puesto que comparten proteínas (dominios y funciones) involucradas en el reconocimiento y activación de las respuestas inmunes (Ronald y Beutler, 2010). La primera fase de las respuestas inmunes en plantas y animales es el reconocimiento de patrones moleculares asociados a microorganismos (MAMPs, por sus siglas en inglés, Microbe Associated Molecular Patterns) por medio de receptores transmembranales denominados PRRs (del inglés Pattern Recognition Receptor). La segunda rama de la inmunidad en plantas, emplea proteínas de resistencia (R) que reconocen un grupo particular de proteínas de patógenos secretadas al citoplasma de la planta que son denominadas efectores (Gassmann y Bhattacharjee, 2012).
En plantas y animales algunos de los dominios conservados presentes en las proteínas de inmunidad son NB-ARC (del inglés Nucleotide Binding - adaptor shared by APAF-1, R proteins and CED-4), TIR (del inglés Toll-Interleukine-1 Receptor), LRR (del inglés Leucine Rich Repeats) y quinasas, entre otros, (Maekawa et al., 2011). El dominio TIR puede estar presente tanto en receptores intracelulares como de membrana. En receptores animales denominados TLR (del inglés Toll-like receptors), el dominio TIR está acompañado del dominio extracelular LRR (Tapping, 2009; Jenkins y Mansell, 2010). Por otro lado, en plantas el dominio TIR hace parte de la región N-terminal de algunas proteínas de resistencia, denominadas TNL (TIR-NB-LRR) por presentar los dominios NB-ARC y LRR (Dodds y Rathjen, 2010). El dominio TIR está implicado tanto en el reconocimiento como en la transducción de señales de defensa mediante su dimerización. En animales, existe evidencia de homo y heterodimerización y en plantas, solamente homodimerización (Mestre y Baulcombe, 2006; Jenkins y Mansell, 2010).
Algunas respuestas de defensa relacionadas con receptores TLRs consisten en la interacción con adaptadores para la activación corriente abajo de cascadas de señalización con el objetivo de inducir la transcripción de genes que respondan a la infección (Kawai y Akira, 2010). Por otro lado, cuando el dominio TIR es sobrexpresado en lino, tabaco y Arabidopsis, se generan respuestas espontáneas de muerte celular o respuesta hipersensible (HR, del inglés Hypersensitive Response) (Swiderski et al., 2009; Krasileva et al., 2010; Bernoux et al., 2011b). En el caso del dominio TIR presente en la proteína de resistencia N de tabaco, se ha evidenciado que es él quien cumple el papel de reconocimiento de la proteína p50 del TMV (Tobacco Mosaic Virus) (Burch-Smith et al., 2007). Las secuencias del dominio TIR en plantas y animales presentan residuos y estructuras secundarias conservadas. Las estructuras cristalinas obtenidas para varios dominios TIR indican la presencia de cinco regiones a-hélice (denominadas aA - aE) y cinco láminas b (denominadas bA - bE). Como característica única del dominio TIR de las plantas, la región aD es más extensa y se denomina aD3 (Chan et al., 2009). Estudios empleando la proteína de resistencia de lino L6, la cual posee un dominio TIR en la región N-terminal, muestran que al remover la región aE este no puede dimerizarse ni generar muerte celular o HR (Bernoux et al., 2011b).
Existen varios estudios del dominio TIR en lino, Arabidopsis y tabaco, pero pocos estudios en cultivos de importancia alimentaria. La yuca (Manihot esculenta Crantz) ocupa el quinto lugar en la producción mundial, después del maíz, el arroz, el trigo y la papa (FAOSTAT, 2011). Varios países de África y Asia ocupan los primeros diez lugares en producción de yuca. Dentro de los países de América Latina, Brasil ocupa el segundo lugar y Colombia el 22 (FAOSTAT, 2011). Para estos países, la yuca representa un soporte económico para varios agricultores y para la industria por ser una fuente importante de almidón, el cual puede ser empleado en la producción de biocombustibles. Dentro de las limitantes más importantes de este cultivo se encuentra la bacteriosis vascular causada por la bacteria Xanthomonas axonopodis pv. manihotis (Xam) (López y Bernal, 2012). Para generar cultivos resistentes frente a esta enfermedad mediante biotecnología es necesario comprender los mecanismos moleculares de las respuestas inmunes en esta planta, gobernados por proteínas con dominios conservados como el TIR. Con miras a evaluar el papel que cumplen ciertos dominios relacionados con defensa y en un futuro explotar esta información para generar resistencia exaltada, en este estudio se realizó un análisis genómico-funcional de los dominios TIR presentes en el proteoma de yuca lo que permitió identificar 46 proteínas de tipo TIR, las cuales se subdividieron en cuatro clases según la presencia de dominios conservados adicionales. Mediante la técnica de doble híbrido de levadura (Y2H, del inglés Yeast Two Hybrid), se identificaron una serie de proteínas que interactúan con RXam2, una proteína candidata de resistencia a la bacteriosis vascular de yuca (Román, 2012). Dentro de los interactores aislados se encontraron dos proteínas que presentan el dominio TIR. Los análisis estructura-función permitieron discernir la función de la región aE del dominio TIR en la dimerización y activación de las respuestas inmunes en yuca.
MATERIALES Y MÉTODOS
ANÁLISIS BIOINFORMÁTICO
Para la búsqueda de los dominios TIR en yuca se realizó un BLAST sobre la secuencia del genoma de yuca (http://www.phytozome.net) empleando el dominio TIR del gen L6 (Numero de accesión Q9XEH0) de Linum usitatissimum (Bernoux et al., 2011b) con parámetros default; excepto para el valor "Expect (E) threshold" que fue de 10. Para comprobar las anotaciones de cada gen según Phytozome, se utilizó el conjunto de base de datos de dominios proteicos presentes en el programa InterProScan del EBI (Instituto Europeo de Bioinformática) (http://www.ebi.ac.uk/Tools/pfa/iprscan/).
Para el alineamiento de las secuencias en aminoácidos, se analizó solamente el dominio TIR, para lo cual se utilizó la región correspondiente al perfil Pfam (http://pfam.sanger.ac.uk/) más 30 residuos en cada extremo. El alineamiento se realizó con el algoritmo ClustalW en MEGA v5.0 (parámetros default) y con algunas modificaciones manuales. El alineamiento fue modificado para ser empleado con el programa ESPript (http://espript.ibcp.fr/ ESPript/ESPript/) y comparar con otras especies que presentan la estructura secundaria del dominio TIR.
Con el alineamiento generado en MEGA se construyó un árbol filogenético, basado en el método Neighbor-joining, bootstrap de 1000 y Pairwise deletion. Para ello se emplearon genes de Arabidopsis y Ricinus communis.
Para determinar el tipo de selección a la cual se encuentran sometidos los dominios TIR de yuca, se empleó la herramienta codon-based Z-test of Selection de MEGA v5.0 y el método Nei-Gojobori (1986), con bootstrap de 1000 y Pairwise deletion. La herramienta emplea como hipótesis nula que hay igual cantidad de sustituciones no-sinónimas (dN) y sinónimas (dS) y como hipótesis alterna un mayor dS que dN. El nivel significancia fue de 5 %.
CLONACIÓN EN VECTORES GATEWAY®
Para el desarrollo de la técnica de doble híbrido se emplearon los vectores pLAW11 (contiene el dominio de activación, Activation Domain AD, del activador GAL4) y pLAW10 (contiene el dominio de unión al ADN, Binding Domain-BD, del activador GAL4), los cuales fueron diseñados para ser compatibles con el sistema Gateway® por Luis A Williams (University Davis, CA, USA), a partir de los vectores pGAP6H y pGBKT7 respectivamente (Clontech, Palo Alto, CA, USA). Para la agroinfiltración y expresión transitoria del dominio TIR se empleó el vector binario pBAV139 (Vinatzer et al., 2006). Los genes que codifican las proteínas con los dominios TIR, 2TN y 3T fueron clonados en el vector pLAW11 el cual presenta los sitios attB, por lo tanto para poder clonarlos en los vectores pLAW10 o pBAV139, se utilizó como intermediario el plásmido pDONR207 (Invitrogen, Carlsbad, CA, USA). Para la clonación en los diferentes vectores se emplearon las enzimas LR clonaseTM o BP clonaseTM (Invitrogen, Carlsbad, CA, USA). En cada caso se utilizó 100 ng de vector de destino, 150 ng del plásmido con el gen de interés, 1 µL de buffer 1X TE y 1 µL de la enzima. Después de cada reacción de clonación, se transformó en células electrocompetentes de Escherichia coli cepa DH10BTM (Invitrogen, Carlsbad, CAa, USA) con un electroporador Micro PulserTM BioRad® siguiendo las condiciones de voltaje, resistencia y capacitancia recomendadas para E. coli por la casa comercial. Las células se incubaron una hora a 37 °C en 1 mL de medio LB a 200 rpm. Las bacterias se sembraron en medio LB (extracto levadura 0.5 %, triptona 1 %, cloruro de sodio 1 % y agar 1.5 %) con gentamicina (50 µg/mL) para pDONR207 o kanamicina (50 µg/mL) para pLAW10 y pBAV139. Se incubaron a 37 °C por 12 horas. Los transformantes se comprobaron por PCR de colonia. Cada reacción de PCR contenía 1X de buffer DreamTaqTM con MgCl2, 0.5 µM de los cebadores 2TN_F (5'-CACCATGG CTTCCACCGTTGAAAA) y 2TN_R (5'-AAATCACTTGACGG CATATGA), o 3T_F (5'- CACCATGGAGGCTACTTCTTCAACC) y 3T_R (5'-CAGCAG AAAGGCAGCCAAAA), 0,2 mM de dNTPs y 0,25 U de enzima DreamTaqTM ADN polimerasa (Fermentas, Glen Burnie, MD, USA).
Después de confirmar cada reacción de clonación por PCR de colonia sobre el respectivo inserto, se realizó miniprep con el kit GeneJETTM Plasmid Miniprep Kit (Fermentas, Glen Burnie, MD, USA). Los vectores pLAW10 y pBAV139 conteniendo los genes que codifican las proteínas con los dominios TIR fueron secuenciados por la compañía MacrogenTM, Corea. Para la amplificación de los insertos en el vector pBAV139 se utilizaron los ce- badores de los dominios TIR y para el vector pLAW10 los cebadores LAW23 R (5'- TTTTCGTTTTAAAACCTAAGAGTC) y LAW22 F (5'-TAATACGACTCACTATAGGGC).
DOBLE HÍBRIDO DE LEVADURA
Material biológico. Para implementar la técnica Y2H se emplearon colonias de Saccharomyces cerevisiae cepas Y187 y AH109 (Clontech, Palo Alto, CA, USA), proporcionadas por el Dr. R. Michelmore, UC Davis. Para su crecimiento se empleó el medio YPDA (extracto levadura 1 %, peptona 2 %, dextrosa 2 %, adenina 0.04 % y agar 2 %). Transformación de los vectores a levadura. Se obtuvo cepas competentes de levadura con el método de acetato de litio descrito por Clontech (Palo Alto, CA, USA). Los dominios TIR, 2TN y 3T, clonados en el vector pLAW10 se transformaron a la cepa Y187. Las levaduras se transformaron siguiendo el protocolo Matchmaker descrito por Clontech (Palo Alto, CA, USA, 2009). El medio de selección para las levaduras transformadas fue SD (extracto de levadura sin aminoácidos 0,67 %, adenina 0,004 %, dextrosa 2 %, agar 2 % y suplemento de aminoácidos). Para seleccionar levaduras que poseen el vector pLAW10 se utilizó el medio SD sin triptófano (suplemento de aminoácidos sin triptófano 0,074 %,) y para seleccionar aquellas que incorporaron el vector pLAW11 se utilizó el medio SD sin leucina (suplemento de aminoácidos sin leucina 0,069 %). Prueba de auto activación del dominio TIR en pLAW10. Algunos dominios de proteínas unidas al BD de GAL4 pueden llegar a transcribir los genes reporteros HIS3 y ADE2 sin la reconstitución del factor de transcripción con AD. Este fenómeno se controló con el uso de 3AT (3-amino-1, 2, 4-triazol) el cual es un inhibidor competitivo de la síntesis de HIS3. Para regular este proceso, primero las levaduras transformadas con los vectores conteniendo los dominios TIR, 2TN y 3T, se crecieron en medio SD sin histidina ni triptófano (SD-WH). De presentarse crecimiento, las levaduras transformadas se plaquearon en el medio SD-WH con diferentes concentraciones de 3-AT (5, 10, 15 y 20 mM).
Mating 1:1. Las evaluaciones de las interacciones se realizaron mediante un segundo mating con colonias de levadura seleccionadas. Primero se inocularon en 5 mL de medio YPDA una colonia de la cepa AH109 (transformada con el constructo pLAW11::3T o pLAW11::2TN) y una colonia de levadura cepa Y187 (con el constructo pLAW10::3T o pLAW10::2TN). Se dejó crecer por 24 h a 30 °C y 75 rpm. Se realizaron tres lavados con agua destilada y se plaqueó en medio SD/QDO (medio SD con suplemento de aminoácidos sin triptófano, leucina, histidina ni adenina 0,070 %) con o sin 3-AT dependiendo si es autoactivo el dominio. Si hubo crecimiento de colonias blancas en el medio SD/ QDO se confirma la interacción. Los controles negativos son los mating 1:1 de pLAW11 vacío con los dominios TIR en pLAW10 y el mating de pLAW10 vacío con los dominios TIR en pLAW11.
AGROINFILTRACIÓN Y EXPRESIÓN TRANSITORIA
Material biológico. Para la agroinfiltración y expresión transitoria de los dominios TIR en plantas se empleó A. tumefaciens cepa GV3101 (A.t GV3101). Para su crecimiento y aislamiento se utilizó medio LB con rifampicina (50 µg/mL). Se utilizó el vector pBAV139, el cual permite clonar el gen o dominio a expresar bajo el control del promotor constitutivo 35SCaMV (Vinatzer et al., 2006). El material vegetal empleado fue Nicotiana benthamiana, Nicotiana tabacum y plantas de yuca de 4 o 5 semanas de crecimiento de las variedades SG107-35, MBRA685 y MCOL2215.
Transformación de los constructos a Agrobacterium. Para generar A.t GV3101 competente se utilizó el protocolo estandarizado en el grupo de investigación Manihot Biotech (Román, 2012). Para la transformación de pBAV139 portador de los dominios a analizar se empleó 28 µL de células electrocompetentes A.t GV3101. Se utilizó el electroporador MicroPulserTM BioRad® siguiendo las condiciones de voltaje, resistencia y capacitancia recomendadas para Agrobacterium por la casa comercial. Se incubó por 3 h en 1 mL de LB a 250 rpm 30 °C y se plaqueó en medio LB kanamicina (50 µg/mL). Tres días después las colonias se plaquearon en medio LB rifampicina (50 µg/mL) y kanamicina (50 µg/mL).
Evaluación de constructos. Para la agroinfiltración se creció una colonia de A.t GV3101 transformada con los constructos, pBAV139:2TN y pBAV139:3T, en 2 mL de LB líquido con rifampicina (50 µg/mL) y kanamicina (50 µg/mL) a 300 rpm, 30 °C por 20 h. Como controles negativos se utilizaron células de A.t GV3101 transformadas con el vector pBAV139 vacío. El cultivo líquido se centrifugó a 3.000 rpm por 15 min y se lavó con solución de agroinfiltración a pH 5,6 (10 mM MES, 10 mM de MgCl2 y 150 M de acetosiringona). Se resuspendió de nuevo en solución de agroinfiltración y se midió la densidad óptica a 600 nM hasta alcanzar un valor aproximado de 0,6. Se incubó a temperatura ambiente por 4 h. Con jeringa de 1 mL, se realizó una punción entre los haces vasculares principales y se agroinfiltró aproximadamente 1 mL de solución (agroinfiltración con Agrobacterium). Se evaluó presencia de HR a los tres y seis días post infiltración.
RESULTADOS Y DISCUSIÓN
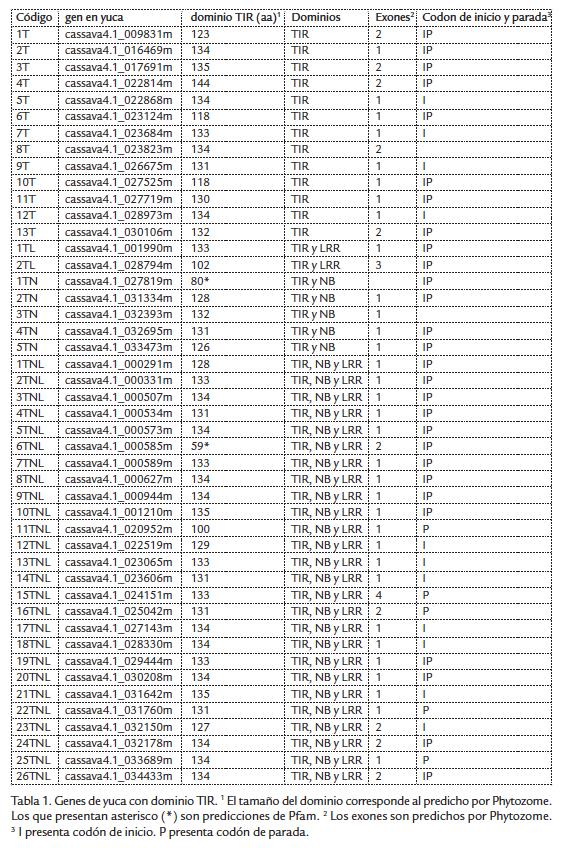
Con el fin de determinar el posible número de genes que codifican dominios TIR en el genoma de yuca, se realizó un Blast empleando el dominio TIR de la proteína L6 de lino. Con el algoritmo anterior, se identificaron 46 genes en el genoma de yuca. La anotación de estos 46 genes se verificó mediante el programa InterProScan que permitió corroborar la presencia del dominio TIR en todas estas proteínas. Según la predicción del Phytozome, el 31 % de las proteínas que presentan el dominio TIR posee al menos un intrón antes de la región aE. De acuerdo a la anotación de la base de datos Pfam (http://pfam.sanger.ac.uk/), el tamaño de los dominios varía entre 59 y 144 aminoácidos (Tabla 1). El número de genes obtenido en yuca es relativamente bajo cuando se compara con otras especies de plantas cuyos genomas han sido secuenciados en su totalidad, como Arabidopsis thaliana y Populus trichocarpa, en donde se han reportado 169 y 171 genes respectivamente, según la base de datos de cada especie en Phytozome. Un bajo número de genes que codifican proteínas con dominios implicados en inmunidad también se ha reportado en especies como papaya (Porter et al., 2009), estos valores pueden estar relacionados con condiciones ambientales, como la diversidad de potenciales patógenos que atacan cada especie en particular, o a una dinámica de plasticidad y evolución particular de cada genoma. Se podría considerar que de manera global y general genomas más pequeños poseen menor número de genes en general. Sin embargo, se ha estimado que los transcritos que codifican proteínas en el genoma de yuca corresponde aproximadamente a 34,151 siendo mayor que los transcritos del genoma de Arabidopsis (32,670) y menor al de P. trichocarpa (45,033). Adicionalmente, el considerando que el 97 % del genoma de yuca secuenciado corresponde a secuencias expresadas, es probable que el porcentaje que falta por secuenciar, incremente el tamaño del genoma, más no el número de genes. De esta forma al comparar entre las especies nombradas, se puede concluir que el genoma de yuca posee un bajo número de genes que codifican proteínas que poseen el dominio TIR.
Las proteínas que poseen el dominio TIR pueden presentar algunos dominios adicionales. Dentro de las 46 proteínas de yuca que presentan el dominio TIR se identificaron subgrupos dependiendo de la presencia o no de dominios adicionales. El 28,2 % (13 genes) codifican proteínas que presentan solo un dominio TIR (T), mientras que el 10,8 % (5 proteínas) presentan un dominio NB-ARC adicional (TN). Solamente el 4,3 % (2 proteínas) poseen un dominio LRR adicional en el extremo C-terminal (TL). La mayor parte de las proteínas, 56,5 % (26) representa el subgrupo que posee los tres dominios: TIR, NB-ARC y LRR (TNL). En A. thaliana se han descrito proteínas que poseen más de un dominio TIR (Meyers et al., 2002), situación que no se logró identificar en el genoma de yuca. En Arabidopsis la mayor parte de proteínas que presentan dominios TIR también poseen los dominios NB y LRR (Meyers et al., 2002). Se ha postulado que solo las proteínas de tipo TNL son funcionales y que las proteínas que presentan únicamente el dominio TIR o no son funcionales o pueden actuar como adaptadores de los receptores de membrana (Takeda y Akira, 2005; O'Neill y Bowie, 2007). Otra posible función recientemente adjudicada al dominio TIR es la de la regular las vías de señalización (Bernoux et al., 2011b).
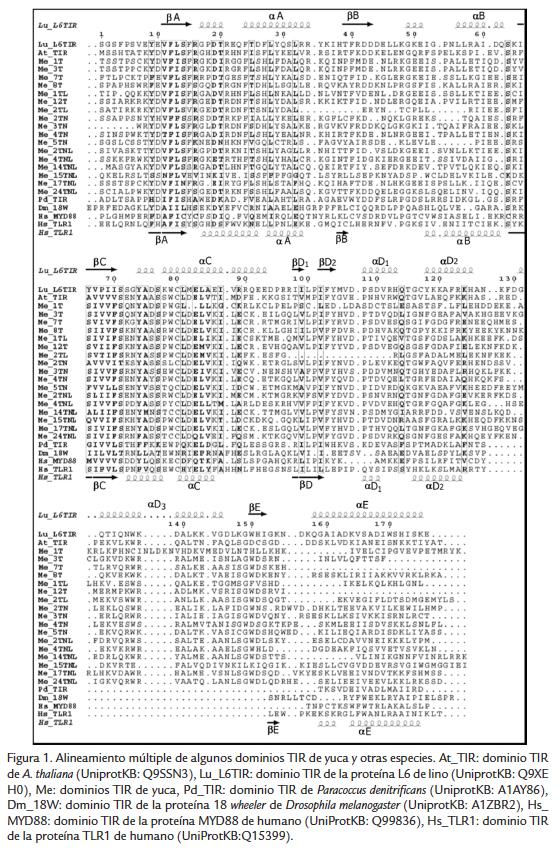
Un alineamiento preliminar de la estructura primaria de dominios TIR de Arabidopsis (PDB: 3JRN) y lino (PDB: 3OZI), cuya estructura tridimensional ha sido determinada por difracción de rayos X (Chan et al., 2009; Bernoux et al., 2011b), permitió identificar que la anotación y predicción de este dominio por Pfam no incluye en su totalidad la región aE. Con el fin de realizar un análisis comparativo entre los diferentes TIR identificados en yuca se realizó un alineamiento múltiple y para cada dominio TIR se incluyó la región anotada por Pfam y 30 residuos adicionales de la región C-terminal. Los resultados del alineamiento por CLUSTALW fueron modificados manualmente basándose en previos artículos donde se analizan las regiones conservadas del dominio TIR (Chan et al., 2009; Bernoux et al., 2011b). Al comparar este alineamiento con las estructuras secundarias de 3JRN y 3OZI, solamente las secuencias de lino, Arabidopsis y yuca presentan la región aD3, característica única de plantas. Mientras que en las secuencias TIR de humanos (Hs_Myd88, Hs_TLR1), de Drosophila melanogaster (Dm_18W) y de Paracoccus denitrificans (Pd_TIR) esta región no está presente (Fig. 1). En las regiones bA, aA, aB, bC, aC, bD, aD, se puede observar la presencia de al menos un aminoácido similar (Fig. 1). Algunas secuencias de yuca, presentan porcentajes de identidad con Arabidopsis máximo de 47,2 % y con lino de 23,96 %. Estudios previos empleando el dominio TIR han mostrado que el ácido aspártico (D) de la posición 19 es un residuo estrictamente conservado (Chan et al., 2009; Bernoux et al., 2011b). Sin embargo, los TIR de yuca 15TNL, 17TNL y 4TNL presentan un aminoácido diferente con una cadena lateral hidrofílica (ácido glutámico (E) o lisina (K)). Los codones que codifican para los aminoácidos D y E se diferencian solamente por un nucleótido en la tercera posición del codón, por lo tanto es probable que exista más de un estructura primaria para el dominio de manera natural o los cambios observados se expliquen por una mutación puntual de tipo sustitución. Además es muy probable que este tipo de cambios no afecte la actividad de la proteína porque ambos presentan carga negativa. Por otro lado, el TIR de yuca 15 TNL, que presenta una lisina en esta posición, los codones que lo codifican son diferentes al del ácido aspártico, por lo tanto es probable que este cambio se haya generado como consecuencia de un cambio puntual. Asimismo, al ser la lisina un aminoácido con carga positiva, es factible que el plegamiento y/o función del dominio TIR sean afectadas por este cambio. La función específica del ácido aspártico en la posición 19 no se ha establecido, aunque su alto grado de conservación sugiere que juega un papel importante en la estructura o función del dominio TIR. Para complementar los análisis anteriores, por medio de las estructuras 3D de los dominios TIR de Arabidopsis (PDB: 3JRN), lino (PDB: 3OZI) y TLR2 (PDB: 1FYW), se encontraron los residuos que interactúan con el ácido aspártico 19. Se evaluaron sus características de carga y polaridad y se buscó sus equivalentes en los cambios D19E y D19K. Con este análisis no se observó un efecto compensatorio (en carga o polaridad) frente al cambio por lisina. Por ejemplo, en la secuencia del dominio TIR de lino comparado con el TIR de yuca 15TNL, los residuos presentan las mismas características, no están cargados y son no polares, a pesar de que el primero presenta D y el otro K. Con los diferentes análisis realizados, es posible concluir que los TIR de yuca 15TNL, 17TNL y 4TNL no sean funcionales. Al analizar los dominios TIR se observó que el 87% de las secuencias de yuca y las de Arabidopsis, lino, P. denitrificans, animales (MYD88 y TLR1) y Drosophila, presentan la región aE, sin embargo en las proteínas de yuca 12T, 9T, 7T, 3T, 5T y 10T no está presente. Previos estudios han determinado que la presencia de la región aE del dominio TIR es primordial para la dimerización y activación de la respuesta hipersensible (Bernoux et al., 2011b) por lo que es probable que estos seis genes de yuca no sean funcionales, o tengan otro tipo de mecanismo de acción.
Con el fin de determinar si existe alguna relación filogenética entre los dominios TIR y alguna agrupación de ellos de acuerdo a la presencia de dominios adicionales en las proteínas que los contienen (NB o LRR), se construyó un árbol filogenético con varios dominios TIR de plantas y animales. En este análisis se incluyeron algunas proteínas de Ricinus communis, especie que pertenece a la misma familia que la yuca, Euphorbiaceae. Los resultados indican una clara separación entre los dominios TIR de animales y plantas (Fig. 2). Las proteínas que poseen el dominio TIR de yuca fueron agrupadas con algunas proteínas de R. communis resultado esperado teniendo en cuenta la cercanía evolutiva de estas dos especies. Una situación diferente se presentó con los TIR de Arabidopsis y lino que fueron agrupados en clados separados. Los resultados del árbol filogenético muestran el agrupamiento de algunas proteínas de yuca, las cuales poseen diferentes combinaciones de dominios adicionales. Por ejemplo, se presentó un clado que agrupó las proteínas 5T, 13TNL y 1TL, las cuales pertenecen a diferentes categorías.
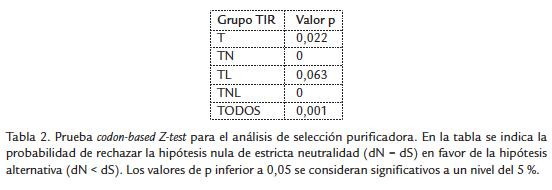
Para conocer un poco más en detalle el comportamiento evolutivo de los dominios TIR, se realizó un alineamiento con las secuencias codificantes de los genes de yuca y mediante el programa MEGA v5.0 se evaluó si los grupos de genes que codifican proteínas de tipo T, TN, TL y TNL presentan un comportamiento similar en cuanto al número de sustituciones sinónimas frenta a no sinónimas (hipótesis nula) o mayores (hipótesis alterna). Las sustituciones sinónimas fueron más frecuentes en todos los casos excepto para el grupo TL (Tabla 2). Según estos resultados, no parece existir una presión selectiva sobre los dominios TIR de yuca. Un alto número de sustituciones no sinónimas se ha identificado en las regiones LRR de varias proteínas implicadas en inmunidad, que se relaciona con la función de reconocimiento de proteínas del patógeno (Wang et al., 2011). El hecho de que la tasa de sustituciones sinónimas en los TIR de yuca sea mayor que la de no sinónimas sugiere que estos dominios en yuca no poseen un papel importante en el reconocimiento directo o indirecto de patógenos y que más bien pueden funcionar como co-adaptadores de otro tipo de receptores de inmunidad. El hecho de que los dominios TIR presenten gran cantidad de sustituciones sinónimas sugiere la necesidad de un alto grado de conservación en su secuencia para mantener una función de pivot en las respuestas inmunes. Esto coincide con los resultados del alineamiento y del árbol filogenético, donde los dominios TIR presentan regiones altamente conservadas y se agrupan independientemente de la categoría (T, TN, TL o TNL).
DOBLE HÍBRIDO DE LEVADURA
La proteína RXam2 de yuca posee dominios NB-LRR y se considera una proteína candidata de resistencia al estar asociada con un QTL que explica el 62 % de la resistencia a la cepa CIO151 de Xam (López et al., 2007). En un estudio previo, se empleó RXam2 como carnada sobre una librería de ADNc de yuca, previamente inoculada con Xam CIO151. Como interactores se encontraron los genes 3T y 2TN (Román, 2012). Estos resultados sugieren y dan apoyo a la hipótesis de que los dominios TIR en yuca, y en particular estos dos, funcionan como co-adaptadores de proteínas receptoras de inmunidad.
A partir de la información de transcriptómica de plantas de yuca obtenida en nuestro laboratorio, se pudo demostrar que los genes 3T y 2TN son reprimidos en la variedad de yuca susceptible MCOL1522 durante la infección con la cepa de Xam CFBP. Es posible que la infección exitosa en esta variedad sea producto de la represión de estos genes. Sin embargo, para dilucidar esta posibilidad será importante evaluar la expresión de estos y otros genes que codifican proteínas con dominios TIR en variedades de yuca resistentes.
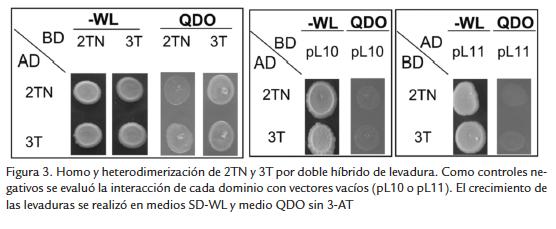
Estudios recientes han demostrado que varios dominios TIR de plantas y animales presentan homo y heterodimerizaciones durante la transducción de la señal de defensa y la activación de la HR (Bernoux et al., 2011a). La dimerización y la activación de las respuestas son procesos dependientes de la presencia de la región aE (Bernoux et al., 2011b). Mediante experimentos de doble híbrido de levadura, se evaluó la autointeracción de los dominios TIR de 3T y 2TN encontrando que ambos tienen la capacidad de homodimerizar (Fig. 3). También se pudo demostrar que estos dos dominios son capaces de interactuar formando heterodímeros (Fig. 3), no obstante presentar entre sí porcentajes de similitud e identidad bajos, 59,7 % y 40,3 % respectivamente. La secuencia de los genes 3T y 2TN fue obtenida a partir de clones de una librería de ADNc y se pudo establecer que ninguno de los dos presenta la región aE completa. Adicionalmente, este resultado se confirmó al comparar con las secuencias reportadas en el genoma de yuca. Dado que las proteínas 3T y 2TN de yuca, a pesar de no presentar la región aE retienen su capacidad de interactuar, contrario a lo establecido previamente para otras plantas, es necesario considerar con precaución la generalización del reque- rimiento de la región aE para la dimerización de los dominios TIR en plantas.
AGROINFILTRACIÓN Y EXPRESIÓN TRANSITORIA
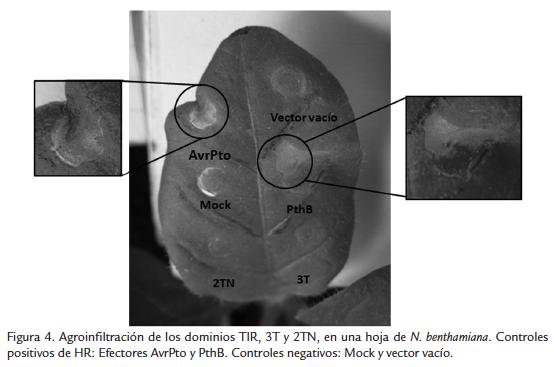
Una vez determinado que los dominios TIR 2TN y 3T, a pesar de no poseer la región aE, son capaces de dimerizar, la siguiente pregunta de investigación fue si la ausencia de esta región tiene algún efecto en la actividad y función de 2TN y 3T. Para determinar si los dominios TIR de 2TN y 3T pueden activar por si mismos las respuestas inmunes y desencadenar una respuesta HR, se expresaron transitoriamente en hojas de N. benthamiana, N. tabacum y en diferentes variedades de yuca mediante agroinfiltración. En ninguna de las variedades de yuca evaluadas ni las especies de Nicotiana se observó un tipo de respuesta tipo HR (Fig. 4) Por lo tanto se puede concluir que si bien los TIR 2TN y 3T de yuca, conservan la posibilidad de dimerizar a pesar de no presentar la región aE, son incapaces de activar las respuestas de defensa mediante expresión transitoria.
La reciente liberación de la secuencia completa del genoma de yuca ha permitido realizar un análisis genómico global de las secuencias de tipo TIR en esta planta. Mediante estudios funcionales de doble híbrido y de expresión transitoria se ha podido inferir el posible papel de dos de estas secuencias TIR durante las respuestas inmunes en yuca y el requerimiento de la región aE para la activación de las respuestas de defensa pero no para su dimerización. Profundizar en la estructura genómica global y en la función de los TIR y de otras proteínas que poseen dominios conservados caracteristicos de las proteínas de inmunidad en yuca permitirá contar con nuevos genes y proteínas que pueden ser introducidos en los programas de mejoramiento genético de yuca con miras a lograr una resistencia exaltada a la bacteriosis vascular.
AGRADECIMIENTOS
Los autores agradecen a todos los integrantes del grupo Manihot biotec por el constante apoyo. Este proyecto fue financiado por la Dirección de Investigación de la Universidad Nacional de Colombia, sede Bogotá (DIB) ficha quipu 201010016922. Agradecimientos especiales a Luis Williams y Richard Michelmore de la Universidad de California (Davis) por suministrar las cepas y vectores para los experimentos de Y2H.
BIBLIOGRAFÍA
BERNOUX M, ELLIS JG, DODDS PN. New insights in plant immunity signaling activation. Curr Opin Plant Biol. 2011a;14(5):512-518. [ Links ]
BERNOUX M, VE T, WILLIAMS S, WARREN C, HATTERS D, VALKOV E, ZHANG X, et al. Structural and functional analysis of a plant resistance protein TIR domain reveals interfaces for self-association, signaling, and autoregulation. Cell Host Microbe. 2011b;9(3):200-211. [ Links ]
BURCH-SMITH TM, SCHIFF M, CAPLAN JL, TSAO J, CZYMMEK K, DINESH- KUMAR SP, et al. A novel role for the TIR domain in association with pathogen-derived elicitors. PLoS Biol. 2007;5(3):e68. [ Links ]
CHAN SL, MUKASA T, SANT ELLI E, LOW LY, PASCUAL J. The crystal structure of a TIR domain from Arabidopsis thaliana reveals a conserved helical region unique to plants. Protein Sci. 2009;19:155-161. [ Links ]
DODDS PN, RATHJEN JP. Plant immunity: towards an integrated view of plant- pathogen interactions. Nat Rev Genet. 2010;11(8):539-548. [ Links ]
FAOSTAT. 2011. FAO Statistics Division 2011. Disponible en: URL: http://faostat.fao.org/site/567/default.aspx#ancor [ Links ]
GASSMANN W, BHATTACHARJEE S. Effector-triggered immunity signaling: from gene-for-gene pathways to protein-protein interaction networks. Mol Plant- Microbe Interact. 2012;25(7):862-868. [ Links ]
JENKINS KA, MANSELL A. TIR-containing adaptors in Toll-like receptor signaling. Cytokine. 2010;49(3):237-244. [ Links ]
KAWAI T, AKIRA S. The role of pattern-recognition receptors in innate immunity: update on Toll-like receptors. Nat Immunol. 2010;11(5):373-384. [ Links ]
KRASILEVA KV, DAHLBECK D, STASKAWICZ BJ. Activation of an Arabidopsis resistance protein is specified by the in planta association of its leucine-rich repeat domain with the cognate oomycete effector. Plant Cell. 2010;22(7):2444-2458. [ Links ]
LÓPEZ C, BERNAL A. Cassava bacterial blight: using genomics for the elucidation and management of an old problem. Trop Plant Biol. 2010;5(1):117-126. [ Links ]
LÓPEZ CE, QUESADA-OCAMPO LM, BOHORQUEZ A, DUQUE MC, VARGAS J, TOHME J, et al. Mapping EST-derived SSRs and ESTs involved in resistance to bacterial blight in Manihot esculenta. Genome. 2007;50(12):1078-1088. [ Links ]
MAEKAWA T, KUFER TA, SCHULZE-LEFERT P. NLR functions in plant and animal immune systems: so far and yet so close. Nat Immunol. 2011;12(9):817-826. [ Links ]
MESTRE P, BAULCOMBE DC. Elicitor-mediated oligomerization of the tobacco N disease resistance protein. Plant Cell. 2006;18(2):491-501. [ Links ]
MEYERS BC, MORGANTE M, MICHELMORE RW. TIR-X and TIR-NBS proteins: two new families related to disease resistance TIR-NBS-LRR proteins encoded in Arabidopsis and other plant genomes. Plant J. 2002;32(1):77-92. [ Links ]
NEI M, GOJOBORI T. Simple methods for estimating the numbers of synonymous and non synonymous nucleotide substitutions. Mol Biol Evol. 1986;3(5):418-426. [ Links ]
O'NEILL LA, BOWIE AG. The family of five: TIR-domain-containing adaptors in Toll-like receptor signalling. Nat Rev Immunol. 2007;7(5):353-364. [ Links ]
PORTER B, PAIDI M, MING R, ALAM M, NISHIJIMA W, ZHU Y. Genome-wide analysis of Carica papaya reveals a small NBS resistance gene family. Molecular Genetics and Genomics. 2009;281(6):609-626. [ Links ]
ROMÁN V. Identificación de interactores proteicos de RXam2, una proteína candidata de resistencia, implicados en la ruta de señalización de defensa contra la bacteriosis vascular de la yuca [tesis de maestría]. Bogotá: Instituto de Biotecnología- IBUN, Facultad de Ciencias, Universidad Nacional de Colombia; 2012. [ Links ]
RONALD PC, BEUTLER B. Plant and animal sensors of conserved microbial signatures. Science. 2010;330(6007):1061-1064. [ Links ]
SWIDERSKI MR, BIRKER D, JONES JD. The TIR domain of TIR-NB-LRR resistance proteins is a signaling domain involved in cell death induction. Mol Plant Microbe Interact. 2009;22(2):157-165. [ Links ]
TAKEDA K, AKIRA S. Toll-like receptors in innate immunity. Int Immun. 2005;17(1):1-14. [ Links ]
TAPPING R. Innate immune sensing and activation of cell surface toll-like receptors. Semin Immuno. 2009;21(4):175-184. [ Links ]
VINATZER BA, TEITZEL GM, LEE MW, JELENSKA J, HOTTON S, FAIRFAX K, et al. The type III effector repertoire of Pseudomonas syringae pv. syringae B728a and its role in survival and disease on host and non-host plants. Mol Microbiol. 2006;62(1):26-44. [ Links ]
WANG J, TAN S, ZHANG L, LI P, TIAN D. Co-variation among major classes of LRR-encoding genes in two pairs of plant species. J Mol Evol. 2001;72(5-6):498-509. [ Links ]