Services on Demand
Journal
Article
Indicators
-
 Cited by SciELO
Cited by SciELO -
 Access statistics
Access statistics
Related links
-
 Cited by Google
Cited by Google -
 Similars in
SciELO
Similars in
SciELO -
 Similars in Google
Similars in Google
Share
Revista Colombiana de Cardiología
Print version ISSN 0120-5633
Rev. Col. Cardiol. vol.13 no.3 Bogota Nov./Dec. 2006
(1) Summer Research Program, The Ohio State University, Columbus - USA.
(2) Neuroproteomics Center, Department of Neurobiology, Duke University Medical Center, Durham N.C. - USA.
(3) Grupo de Dinámica Cardiovascular, Universidad Pontificia Bolivariana, Medellín, Colombia.
(4) Parque Tecnológico de Antioquia, Medellín, Colombia.
Correspondencia: Óscar Alzate, Ph.D. 258 Bryan Research Building, Duke University Medical Center. Box 3209, Durham, NC. 27710 - USA. Telephone: 1-919-6815855, E-mail: alzate@neuro.duke.edu
John Bustamante, MD., Ph.D. Bl. 7 Escuela de Formación Avanzada, Universidad Pontificia Bolivariana. A.A. 56006, Medellín, Antioquia - Colombia. Teléfono: 57-4-4159015, Correo electrónico: john.bustamante@upb.edu.co
Recibido: 30/08/06. Aprobado: 04/09/06.
Se purificaron proteínas cardiacas a partir de ratas diabéticas y sanas de tipo Sprague-Dawley. Las proteínas fueron fraccionadas por medio de gel de electroforesis de dos dimensiones (2D-PAGE). La separación resultante fue visualizada por tinción con Coomassie azul. Luego de ser convertidas en imagen digital, las proteínas del grupo diabético y del grupo control fueron comparadas y correlacionadas para determinar los niveles de expresión diferenciada. Sesenta de las ciento ochenta proteínas en el gel fueron removidas y digeridas en fragmentos pequeños de péptidos, los cuales se analizaron por medio de espectrometría de masas para determinar la estructura primaria de los péptidos resultantes (secuencia de los aminoácidos). Esta información se registró en una base de datos (http://www.ncbi.nlm.nih.gov/) para determinar la identidad de las proteínas precedentes a los péptidos. Se determinó la identidad de las proteínas expresadas diferencialmente en el tejido cardiaco de ambos grupos; se encontraron varias proteínas expresadas en diferentes niveles a los normales cuando se analizaron los corazones de ratas diabéticas, incluyendo fosfatasa de tiroxina (PTP, Q60998), receptores de lipoproteínas de muy baja densidad (VLDL-R, P98156), perioxidasa de glutation (PHGPx, O70325), transferasa de serina hidroxilamina (SHMT, P50431), adenylyl cyclasa proteína 1 asociada (CAP1, P40124) y teletonina (TELT, O70548).
Palabras clave: proteínas cardiacas, diabetes mellitus, modelo murino, proteómica.
Cardiac proteins were isolated from diabetic and wild type Sprague-Dawley rats, then fractionated by two dimensional gel electrophoresis (2D-PAGE) using isoelectric focusing and molecular weight. The resulting protein spots were stained to facilitate detection. After being converted into a digital image, the proteins on the diabetic and wild type gels were matched to each other then compared to determine levels of expression. Sixty of the one hundred and eighty proteins on the gel were removed and digested to produce peptide fragments, which were analyzed by mass spectrometry to determine their amino acid sequence. This information was entered into a protein database (http://www.ncbi.nlm.nih.gov/) to determine the identity of the corresponding proteins. The identity of proteins differentially expressed in cardiac tissue of both groups was determined: several proteins were found to be expressed at different levels than normal in the hearts of diabetic rats, including protein tyrosine phosphatase (PTP, Q60998), very low-density lipoprotein receptor (VLDL-R, P98156), glutathione peroxidase (PHGPx, O70325), serine hydroxymethyl transferase (SHMT, P50431), adenylyl cyclase-associated protein 1 (CAP1, P40124), and telethonin (TELT, O70548).
Key words: cardiac proteins, diabetes mellitus, mouse model, proteomics.
Introducción
La diabetes mellitus es una condición patológica en la cual se conoce que el organismo no es capaz de regular efectivamente el nivel de glucosa en la sangre, pero al mismo tiempo hay otros efectos, no todos esclarecidos, que afectan los órganos blanco de esta disfunción hormonal entre los cuales se encuentra el sistema cardiovascular (1-7). Esta patología puede ocurrir por varias razones, entre las que se encuentran la inhabilidad de producir insulina y de otro lado, la resistencia a los efectos de la insulina. La insulina es una hormona que se distribuye a través del organismo por el sistema circulatorio y que está involucrada en el metabolismo de la glucosa, pero que también puede afectar otros productos metabólicos. En la diabetes tipo I, el sistema inmune ataca, a temprana edad, las células que producen insulina; en la diabetes tipo II la enfermedad se relaciona con algún tipo de resistencia adquirida en edades más avanzadas. Hay alrededor de 150 millones de personas con diabetes en el mundo, y este número crece de forma importante (8) por lo que se vislumbra como una patología de gran repercusión social.
Aunque en la patología diabética se reconoce un potencial riesgo de enfermedad isquémica cardiaca, no se conoce de manera acertada cómo la diabetes causa alteraciones cardiacas independientemente de la aterosclerosis coronaria. La hipertrofia ventricular, los diferentes tipos de cardiomiopatía, las alteraciones en la micro circulación y el incremento del estrés cardiaco, que conllevan reducción en el comportamiento contráctil (performance), no se explican completamente sólo por los efectos celulares de la hiperglicemia. La diabetes mellitus abarca más que una mera anormalidad en la homeostasis de la glucosa, y se debe explorar y entender el impacto del complejo disturbio metabólico sobre la estructura cardiaca, afectando tanto la actividad sistólica como la diastólica.
Un tema actual de estudio es la relación que tiene la diabetes con la manifestación en el nivel de proteínas específicas involucradas tanto en la estructura como en el metabolismo celular. Las proteínas se relacionan con todos los biosistemas del organismo humano, siendo el resultado primario de la información codificada por el genoma; esto hace que cuando se alteran los niveles de expresión de algunas proteínas, haya un cambio correspondiente en la funcionalidad de la célula (9-12). Así, la expresión de varias proteínas puede usarse como marcador para fenotipos específicos de enfermedad, incluyendo la patología cardiovascular (12-17), haciendo prever la importancia que pueda tener la patología diabética en la morbilidad y la mortalidad relacionada con patología cardiovascular, y de ello su impacto en la salud pública.
La proteómica, término introducido en 1995, es la disciplina que estudia la dinámica de una célula a través de la observación del contenido proteico (18). Una manera de determinar dicho contenido proteico en una muestra, es analizando la trascripción en el citosol ya que éste es usado por los ribosomas como una plantilla para guiar la construcción de las cadenas peptídicas que constituyen las proteínas. En este sentido, la proteómica expresional, que estudia los niveles relativos de la expresión de proteínas, permite monitorear muchas proteínas simultáneamente para detectar diferenciaciones en la expresión, como podría ser en el caso de la diabetes. La electroforesis por gel de dos dimensiones (2-DE) o la cromatografía líquida multidimensional de proteínas (MD-HPLC) (19), constituyen métodos convencionales en proteómica expresional. Estas dos aproximaciones tienen sus ventajas y desventajas: 2-DE es capaz de separar miles de proteínas en un corto tiempo, sin embargo requiere excesivo esfuerzo y dedicación, y no es lo suficientemente sensible para detectar proteínas expresadas a niveles muy bajos. Con la técnica cromatográfica se puede cuantificar la presencia de proteínas, pero toma más tiempo para desarrollarse y se hace a su vez una técnica más costosa; además, no permite la separación de moléculas expresadas como varios isoformos de la misma proteína. Por esta razón, 2-DE fue seleccionada para caracterizar la expresión diferencial de la proteína en el presente trabajo.
El objetivo de este estudio fue identificar proteínas que pudiesen estar expresadas diferencialmente en el corazón de ratas modelos de diabetes mellitus. Para ello se usó la técnica 2-DE, por medio de la cual se separaron las proteínas cardiacas. Las proteínas relevantes fueron removidas del gel y posteriormente digeridas en péptidos más pequeños que fueron analizados por espectrometría de masas. La digestión produjo fragmentos de péptidos cortos con pesos moleculares entre 900 y 3.000 Daltons, y entre 10 y 30 aminoácidos, lo que se diferenció fácilmente porque cada cadena de péptidos tenía una masa característica que dependía de la cadena de aminoácidos. Se usaron varios de los fragmentos de péptidos que resultaron de la digestión de las proteínas para identificar las proteínas correspondientes usando las bases de datos «NCBI» y «SwissPro» (http://www.ncbi.nlm.nih.gov; http://us.expasy.org).
Los resultados de este proyecto arrojan datos preliminares sobre la relación de algunas proteínas solubles y el corazón de ratas del tipo Sprague-Dawley afectadas con diabetes mellitus.
Materiales y métodos
Se evaluaron ocho corazones de ratas del tipo Sprague-Dawley (muestras aportadas por el Dr. Muthu Periasamy, Chairman, del Departamento de Fisiología y Biología Celular de «The Ohio State University», de los cuales se consideraron cuatro corazones de ratas transgénicas diabéticas y cuatro corazones de ratas sanas. Se siguió un meticuloso protocolo para realizar cada experiencia y limitar errores experimentales significativos. A continuación se detallan los pasos que se siguieron.
Separación de la proteína total
El tejido ventricular fue separado del corazón de las ratas Sprague-Dawley. Las muestras se conservaron congeladas en nitrógeno líquido a -190ºC; posteriormente, se trituraron hasta lograr un macerado fino y acto seguido se homogenizó en ocho volúmenes de buffer constituido por 50 mM TrisHCl (pH 7,5), 150 mM NaCl, 1 mM PMSF, 1mM pirofosfato de sodio, 5 mM ortovanadate de sodio, 1 mM menzamidine, 10 mM fluoride de sodio, 0,5% NP-40 y 10 µL/mL cocteles inhibidores de proteasa (Sigma, Cat. #P8340). El homogenizado resultante se incubó en hielo por 30 minutos y se centrifugó a 12.000 RPM, para descartar el pellet restante. El sobrenadante se guardó en alícuotas con glicerol 10% y se preservó a -80oC.
Separación de membranas SR
El tejido ventricular fue homogenizado con ocho volúmenes de buffer A que contenía 10 mM imidazole, 300 mM sucrosa, 0,5 mM DTT, 40 µM CaCl2 e inhibidores de proteasa, dos veces por cada 30 segundos. El producto obtenido de la homogenización se centrifugó a 4.000 RPM durante 20 minutos, para posteriormente descartar el pellet. El sobrenadante se centrifugó por 20 minutos a 10.000 RPM, con lo que se removió la contaminación de la mitocondria. Se agregó KCl sólido a la concentración final de 0,5 mM y se incubó en hielo por 15 minutos. Esta suspensión se centrifugó a 40.000 RPM durante 30 minutos en una ultracentrifugadora Beckman.Preparación de la muestra para 2D
Se limpió el total de la proteína para la electroforesis de 2D usando el protocolo recomendado por el PlusOne 2D Clean-Up Kit (Amersham Biosciences, Cat. No 80-6484-51). La proteína purificada se suspendió en SBII (buffer de solubilización) (19) y se incubó durante 30 minutos a temperatura ambiente. Después de centrifugarla a 10.000 RPM por 5 minutos, se guardó el sobrenadante en alícuotas a -20ºC para usarlo posteriormente.
Enfocamiento isoeléctrico
El enfocamiento isoeléctrico fue desarrollado con una cinta de gradientes de pH inmovilizados (IPG) de 11 cm, pH 3-10 (Bio-Rad, Hercules, California). Alrededor de 500 µg de proteína solubilizada se combinaron con SBII para un volumen final de 200 µL. La muestra precipitada fue depositada en una bandeja de enfocar y la cinta IPG fue rehidratada por 16 horas a 50 mA. El protocolo para el enfocamiento isoeléctrico fue: 15 minutos a 250 V, 2,5 horas a 5.000 V, seguido por 8.000 V, para un total de 40 kVh. Después del enfocamiento la cinta IPG fue equilibrada en 6M de urea, 100% de glicerol, 20% de SDS, 1,5 de M TrisHCl (pH 8,8) y 0,2% de DTT por 10 minutos. Después de 10 minutos, la cinta IPG fue incubada nuevamente durante 10 minutos en la misma solución, pero el DTT fue reemplazado por 45 mg/mL de iodoacetamide. Para la segunda dimensión, la cinta IPG fue montada en un gel con gradiente de 10,5% a 14% de archilamida (SDS-PAGE) usando el equipo de geles «Criterion» por 1 hora a 200 V. El gel fue fijado con 50% de etanol y 10% de ácido acético, y teñido con azul brillante R 250 Coomassie.
Adquisición y análisis de las imágenes
Las imágenes de los geles fueron adquiridas con un sistema Versadoc 3000 (Biorad). Las imágenes de los geles se analizaron con un programa de computador especializado para el procesamiento de imágenes de geles llamado PDQuest (Biorad, Hercules, California). Este programa permite analizar y comparar simultáneamente varios geles, detectando y comparando automáticamente en cada uno de ellos todas las proteínas presentes. Cada imagen fue re-analizada de forma manual para eliminar errores en el análisis automático y para remover partículas contaminantes de las imágenes. Este análisis produce una imagen digital del gel y determina la cantidad de la proteína, la posición en el gel y la calidad de la mancha.
La cantidad de una proteína se define como la intensidad total de una mancha en particular, comparada con un patrón estándar de proteínas de concentración conocida. Todos los geles fueron normalizados para que la calidad y la cantidad de las manchas (proteínas) tuvieran el mismo significado para cada muestra analizada.
Análisis de Maldi e identificación de proteínas
Las manchas de proteínas en el gel de dos dimensiones, fueron extraídas con el Proteomeworks spot cutter (BioRad); los fragmentos extraídos del gel que contenían las proteínas aisladas, fueron transferidos a la estación de Massprep (Perkin-Elmer) para la digestión-en-gel de la proteína, siguiendo el protocolo incluido con el programa WinPREP Multiprobe II. La digestión de las proteínas fue desarrollada con 6 ng/µL tripsina en 50 mM bicarbonato de amonio por 5 horas a 37ºC. Los péptidos resultantes de la digestión fueron extraídos con una mezcla de 1% de ácido fórmico y 2% de acetonitrilo, y se aplicaron en una placa de acero MALDI (Micromass). Los péptidos resultantes se analizaron con espectrometría de masa usando un espectrómetro MALDI-TOF (Micromass) en modo reflectrónico. La apropiada calibración se llevó a cabo con angiotensina I, renina y «ACTH 18-39 Clip». La calibración fue verificada identificando conalbumina tipo I, albúmina de suero bovino, actina de músculo bovino y gliceraldehído 3-fosfato dehidrogenasa muscular de conejo (BioRad). La precisión en la identificación de las proteínas evaluadas fue superior al 95%. Para la identificación, los pesos moleculares de los péptidos se correlacionaron con sus respectivas proteínas usando el programa de computador ProteinLynx (Micromass) y el servidor en línea Protein Prospector (http://prospector.ucsf.edu). Estos dos programas investigan bases de datos de proteínas no redundantes para identificar proteínas, correlacionando los pesos moleculares de los péptidos determinados por medio de espectrometría de masa con pesos moleculares teóricos que se obtienen a partir de la secuencia del gen correspondiente: NCBi (http://www3.ncbi.nlm.nih.gov) y el SwissPro (http://us.expasy.org). Se usaron los siguientes parámetros para investigar: tolerancia de masa = 0.2 Da, máximo número permitido de digestión incompleta = 1, acetilación de los N-términos; carbamidometilación de cysteína y oxidación de metionina; fueron considerados como posibles modificaciones.
Resultados
Las proteínas presentes en las muestras de tejido cardiaco fueron separadas por su punto isoeléctrico y peso molecular. Las bandas de proteínas fueron analizadas usando el programa PDQuest para identificar las proteínas de interés: aquellas que fueron expresadas en diferentes niveles entre los sujetos diabéticos de estudio y los controles. Se corrieron dos geles para cada grupo y se compararon para asegurarse que mostraban idénticas proteínas en los mismos lugares. Una vez que el software de análisis hizo la comparación preliminar de las manchas proteicas entre el grupo de diabéticos y el control, se verificó cada uno de los pares por observación. Tanto el corte de las proteínas del gel como su digestión, se monitorearon con cuidado para asegurar que la extracción ocurriera de manera adecuada y que las técnicas usadas durante la digestión de tripsina fueran las correctas. De igual forma, antes de iniciar el análisis de las muestras de péptidos, se realizó un chequeo final en los procedimientos experimentales cuando se calibró el espectrómetro de masas.
De las cincuenta y cuatro proteínas que se analizaron, siete se identificaron fácilmente debido al puntaje de MOWSE del buscador de proteínas de la base de datos NCBi, donde las proteínas de estudio fueron cientos de veces más grandes que las restantes; esto significa que existe alrededor de un 100% de probabilidad de que éstas se identifiquen de manera adecuada entre las demás proteínas. Las siete proteínas identificadas se presentan en la tabla 1.
En la figura 1 se presentan dos geles típicos obtenidos en este experimento. Estas proteínas no son necesariamente las mismas que se aíslan para analizar por espectroscopia de masas, ya que se requieren valores estadísticos y reproducibilidad de los experimentos.
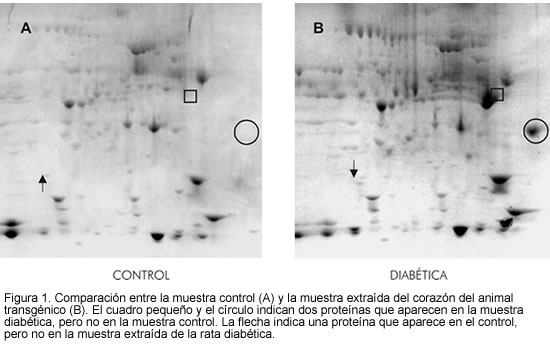
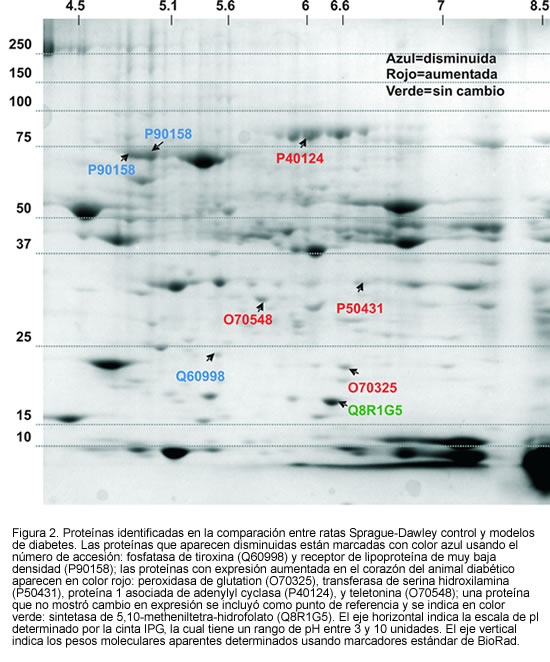
Las proteínas aisladas del gel e identificadas por MS, se muestran en la figura 2, y son el resultado de varios geles en los cuales se han analizado muestras provenientes de diferentes animales.
Discusión
En esta investigación preliminar se destaca el hallazgo de las proteínas transferasa de serina hidroxilamina y receptor de lipoproteína de muy baja densidad, cuya regulación y expresión parece afectada por la presencia de diabetes. Ya hay estudios que demuestran cómo la diabetes mellitus conlleva mayor riesgo de contraer enfermedades cardiovasculares; por ejemplo, la identificación de un aumento de expresión de la capa de titina (llamada teletonina) en el músculo cardiaco de las ratas diabéticas, proteína estabilizadora de la miosina, que causa un aumento en la rigidez del tejido cardiaco, puede incrementar las causas de estrés en el corazón, lo que podría enmarcarse dentro de la cardiomiopatía diabética (20). La proteína VLDL-R ha sido identificada como una de las mayores causas de patología cardiovascular por su capacidad para transportar lípidos. Los cambios en VLDL-R sugieren una posible causa de aterotrombosis, los cuales han mostrado que inducen agregación plaquetaria mediada por colágeno, ya que estos receptores se relacionan con los niveles de VLDL y la agregación de placas (21). Otro factor relacionado con la patología cardiovascular es el efecto de la diabetes sobre el sistema antioxidante (22-24). Se ha observado que la concentración de perioxidasa de glutation, proteína fundamental de este sistema antioxidante, se afectó en las ratas diabéticas.
De los resultados preliminares se deduce que en el grupo de ratas diabéticas se expresan dos proteínas involucradas en la función celular: fosfato de tiroxina y proteína 1 asociada adenylyl cyclasa. Debido a que las señales celulares son una función muy importante para todas las células que existen en un medio altamente complejo tal como el corazón, su disbalance puede jugar un papel importante en la viabilidad de las células miocárdicas (25).
Los mecanismos de disfunción se relacionan con disturbios metabólicos y procesos proteicos que afectan la funcionalidad celular y los cuales se pueden estudiar por medio de la proteómica y metabolómica. Los datos encontrados sobre la regulación de proteínas cardiacas en ratas diabéticas, con expresión por encima de veinte por ciento, son un hallazgo importante para los próximos pasos en la presente investigación, unos de los cuales será determinar la identidad de las restantes cincuenta y cuatro proteínas. El uso de ratas genéticamente modificadas ha probado ser una versátil herramienta experimental para conocer los mecanismos relacionados que pueden ser responsables de los efectos deletéreos de la diabetes sobre la función cardiaca.
Conclusiones
El resultado de este proyecto relacionado con el estudio y aplicación de técnicas de la proteómica en las afecciones cardiovasculares, es muy promisorio. Contar con herramientas más sensibles y específicas que permitan diferenciar distintos marcadores de compromiso cardiaco, será en un futuro una meta de las actuales investigaciones. Si otras técnicas diagnósticas complejas no se pueden aplicar en amplios estudios poblacionales, los biomarcadores sí pueden ser muy útiles en estudios de poblaciones especialmente en patologías que, como la presente, se caracterizan por largos periodos de tiempo de progresión silente de la enfermedad, permitiendo diagnósticos más tempranos y subsecuentemente el manejo terapéutico precoz.
Se hace necesaria una anotación acerca del alcance y validez de estos resultados. Como se ha indicado, éstos son preliminares y se requiere más investigación para determinar varios aspectos:
1. Cómo se relacionan estas proteínas dentro del cuadro molecular que asocia diabetes y patología cardiaca.
2. Cuáles de estos cambios de expresión resultan de verdaderos efectos moleculares producidos por la enfermedad y cuáles resultan de factores no asociados.
3. Cuáles cambios en la expresión de las proteínas pueden ser explicados por condiciones relacionadas con el modelo animal tales como la dieta, las condiciones de mantenimiento, el estrés o los métodos quirúrgicos.
4. Qué otras proteínas y posiblemente otras biomoléculas tales como ácidos nucleicos y lípidos, resultan afectadas por esta enfermedad, y cómo todas ellas están relacionadas, si es que lo están.
Queda establecido que estos resultados son muy preliminares y que se presentan con una doble intención: reportar resultados relevantes en cuanto a la patología cardiaca en relación con la diabetes y compartir con la comunidad médica el uso de la proteómica como metodología de la biotecnología moderna en el estudio de la patología cardiaca, que están siendo utilizadas en el estudio de nuevos marcadores biológicos.
Agradecimientos
Agradecimientos y reconocimientos muy especiales a los Drs. Gopal Babu y Debra Wheeler, por su apoyo incondicional en la realización de este trabajo.
Bibliografía
1. Anand-Srivastava MB, Wang R, Liu YY. Alterations in g-protein-linked signal transduction in vascular smooth muscle in diabetes. Adv Exp Med Biol 2001; 498: 263-271. [ Links ]
2. Fang ZY, Prins JB, Marwick TH. Diabetic cardiomyopathy: evidence, mechanisms, and therapeutic implications. Endocr Rev 2004; 25 (4): 543-567. [ Links ]
3. Hashim S, Liu YY, Wang R, Anand-Srivastava MB. Streptozotocin-induced diabetes impairs G-protein linked signal transduction in vascular smooth muscle. Mol Cell Biochem 2002; 240 (1-2): 57-65. [ Links ]
4. Netherton SJ, Jimmo SL, Palmer D, Tilley DG, Dunkerley HA, Raymond DR, et al. Altered phosphodiesterase 3-mediated cAMP hydrolysis contributes to a hypermotile phenotype in obese JCR:LA-cp rat aortic vascular smooth muscle cells: implications for diabetes-associated cardiovascular disease. Diabetes 2002; 51 (4): 1194-1200. [ Links ]
5. Poornima IG, Parikh P, Shannon RP. Diabetic cardiomyopathy: the search for a unifying hypothesis. Circ Res 2006; 98 (5): 596-605. [ Links ]
6. Severson DL. Diabetic cardiomyopathy: recent evidence from mouse models of type 1 and type 2 diabetes. Can J Physiol Pharmacol 2004; 82 (10): 813-823. [ Links ]
7. Yamanouchi J, Takatori A, Nishida E, Kawamura S, Yoshikawa Y. Expression of lipoprotein receptors in the aortic walls of diabetic APA hamsters. Exp Anim 2002; 51 (1): 33-41. [ Links ]
8. O’Brien JA, Patrick AR, Caro J. Estimates of direct medical costs for microvascular and macrovascular complications resulting from type 2 diabetes mellitus in the United States in 2000. Clin Ther 2003; 25 (3): 1017-1038. [ Links ]
9. Alzate O, Osorio C, Herbstreith M, Hjelmeland M, Buechler R, Ehlers M, et al. Differential protein expression analysis of transforming growth factor beta (TGF-b) signaling and the impact of a low molecular weigth TGF-b inhibitor in human malignant glioma cell lines. Neuro-oncology 2005: 255. [ Links ]
10. Alzate O, Hussain SR, Goettl VM, Tewari AK, Madiai F, Stephens RL, et al. Proteomic identification of brainstem cytosolic proteins in a neuropathic pain model. Brain Res Mol Brain Res 2004; 128 (2): 193-200. [ Links ]
11. Goettl VM, Hussain SR, Alzate O, Wirtz DJ, Stephens RL, Jr., Hackshaw KV. Differential change in mRNA expression of p75 and Trk neurotrophin receptors in nucleus gracilis after spinal nerve ligation in the rat. Exp Neurol 2004; 187 (2): 533-536. [ Links ]
12. Sheikh A, Barrett C, Villamizar N, Miller S, Alzate O, Shelburne J, et al. Proeomics of brain injury in a neonatal model of deep circulatory arrest. In 86th. Annual Meeting AATS: April 29 2006; Philadelphia. Edited by: Surgery AAfT; 2006. [ Links ]
13. Barglow KT, Cravatt BF. Discovering disease-associated enzymes by proteome reactivity profiling. Chem Biol 2004; 11 (11): 1523-1531. [ Links ]
14. Faber MJ, Agnetti G, Bezstarosti K, Lankhuizen IM, Dalinghaus M, Guarnieri C, et al. Recent developments in proteomics: implications for the study of cardiac hypertrophy and failure. Cell Biochem Biophys 2006; 44 (1): 11-29. [ Links ]
15. Gallego-Delgado J, Lazaro A, Osende JI, Barderas MG, Blanco-Colio LM, Duran MC, et al. Proteomic approach in the search of new cardiovascular biomarkers. Kidney Int Suppl 2005 (99): S103-107. [ Links ]
16. Mayr M, Mayr U, Chung YL, Yin X, Griffiths JR, Xu Q. Vascular proteomics: linking proteomic and metabolomic changes. Proteomics 2004; 4 (12): 3751-3761. [ Links ]
17. Vivanco F, Martin-Ventura JL, Duran MC, Barderas MG, Blanco-Colio L, Darde VM, et al. Quest for novel cardiovascular biomarkers by proteomic analysis. J Proteome Res 2005; 4 (4): 1181-1191. [ Links ]
18. Sanchez JC, Corthals GL, Hochstrasser DF. Biomedical applications of proteomics. Weinheim: Wiley-VCH; 2004. [ Links ]
19. Babu GJ, Wheeler D, Alzate O, Periasamy M. Solubilization of membrane proteins for two-dimensional gel electrophoresis: identification of sarcoplasmic reticulum membrane proteins. Anal Biochem 2004; 325 (1): 121-125. [ Links ]
20. Hsu KL, Tsai CH, Chiang FT, Lo HM, Tseng CD, Wang SM, et al. Myocardial mechanics and titin in experimental insulin-resistant rats. Jpn Heart J 1997; 38 (5): 717-728. [ Links ]
21. Englyst NA, Taube JM, Aitman TJ, Baglin TP, Byrne CD. A novel role for CD36 in VLDL-enhanced platelet activation. Diabetes 2003; 52 (5): 1248-1255. [ Links ]
22. Maritim AC, Sanders RA, Watkins JB. Diabetes, oxidative stress, and antioxidants: a review. J Biochem Mol Toxicol 2003; 17 (1): 24-38. [ Links ]
23. Palanduz S, Ademoglu E, Gokkusu C, Tamer S. Plasma antioxidants and type 2 diabetes mellitus. Res Commun Mol Pathol Pharmacol 2001; 109 (5-6): 309-318. [ Links ]
24. Sailaja YR, Baskar R, Saralakumari D. The antioxidant status during maturation of reticulocytes to erythrocytes in type 2 diabetics. Free Radic Biol Med 2003; 35 (2): 133-139. [ Links ]
25. Portela-Gomes GM, Grimelius L, Johansson H, Efendic S, Wester K, Abdel-Halim SM. Increased expression of adenylyl cyclase isoforms in the adrenal gland of diabetic Goto-Kakizaki rat. Appl Immunohistochem Mol Morphol 2002; 10 (4): 387-392. [ Links ]














