Introducción
La hibridación in situ fluorescente (FISH, por sus siglas en ingles Fluorescence in situ hybridization) es una técnica de citogenética molecular desarrollada aproximadamente hace 40 años1,2. Esta herramienta molecular detecta anomalías cromosómicas, tanto numéricas como estructurales en locus específicos de protooncogenes o genes supresores de tumores. La FISH utiliza fragmentos de ADN incorporados con nucleótidos acoplados a fluoróforos (sondas) para examinar la presencia o la ausencia de secuencias complementarias3,4. Existen diferentes tipos de sondas: las sondas centroméricas son útiles para la detección de alteraciones numéricas y como control de referencia de sondas locus específico y las sondas locus específico se usan para la detección de translocaciones, delecciones o amplificaciones. Estas pueden ser sondas de fusión o sondas Break apart3 , 4.
La FISH tiene una alta sensibilidad y especificidad para detectar secuencias de ADN o ARN en comparación con la citogenética convencional; esto ha convertido esta técnica como una herramienta fundamental para confirmar el diagnóstico de algunas patologías, al igual que determinar el pronóstico y el tratamiento de algunas neoplasias hematológicas y no hematológicas3,5.
El objetivo del presente estudio es describir la experiencia del Instituto Nacional de Cancerología de Colombia (INC) con la técnica de FISH en las diferentes neoplasias hematológicas y los tumores sólidos para conocer el comportamiento molecular en población colombiana.
Materiales y métodos
Se realizó un estudio descriptivo retrospectivo de todos los resultados de FISH que se han realizado en el Laboratorio de Genética y Oncología Molecular del INC entre 2012 y 2016. Se han utilizado 39 sondas para cada patología y cabe destacar que una misma sonda se puede utilizar en diferentes patologías. Todas las pruebas fueron estandarizadas y validadas según las indicaciones del fabricante, se calcularon los valores de cut-off normal para cada tipo de prueba. Para el análisis en muestras de médula ósea y sangre periférica se observaron un mínimo de 200 núcleos que no estuvieran sobrepuestos y con señales claras y para tejidos embebidos en parafina se seleccionó la zona tumoral por parte del patólogo. Se seleccionaron filtros específicos para las longitudes de onda generadas por cada sonda en un microscopio AX70 de Olympus adaptado con lámpara ultravioleta, las imágenes fueron capturadas y digitalizadas con el programa FISHview de Applied Spectral Imaging. La interpretación fue realizada por dos expertos: un experto en citogenética molecular FISH con 12 años de experiencia y un médico genetista con más de 30 años de experiencia. Los resultados fueron descritos según las guías del Sistema Internacional de Nomenclatura para Citogenética Humana (ISNC, por su sigla en inglés)6. Para el análisis del estudio, los resultados fueron divididos en neoplasias hematológicas y tumores sólidos.
Resultados
En total se realizaron 1.713 pruebas de FISH, 1.010 (59%) fueron desarrolladas en neoplasias de origen hematolinfoide (tabla 1 y 2) y 703 (41%) en tumores sólidos, de estos 428 (61%) correspondieron para HER2 de cáncer de seno.
Neoplasias hematológicas
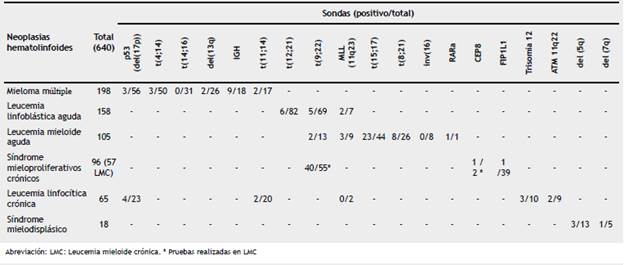
La entidad hematológica donde se realizó el mayor número de pruebas fue el mieloma múltiple (MM). En total fueron ejecutadas 198 pruebas (30%), principalmente para la detección de pérdida p53 (del(17p)) (n:56) y t(4;14) (n:50) observando positividad en tres pacientes para cada prueba. El IGH fue positivo en el 50%, seguido de del(13q) en el 15% (tabla 1).
Se realizaron: 158 pruebas en leucemia linfoblástica aguda (LLA) (24,7%); 105 pruebas en leucemia mieloide aguda (LMA) (16,4%); 96 pruebas en síndromes mieloproliferativos crónicos (SMPC); 57 pruebas en leucemia mieloide crónica (LMC) (14%), y 65 pruebas en leucemia linfocítica crónica (LLC) (10%).
En una menor proporción se ha desarrollado en síndrome mielodisplásico (SMD) (3%). La prueba con mayor porcentaje de positividad en leucemias fue t (9; 22) (72%) en LMC seguido de t(15;17) (44%) en LMA (tabla 1).
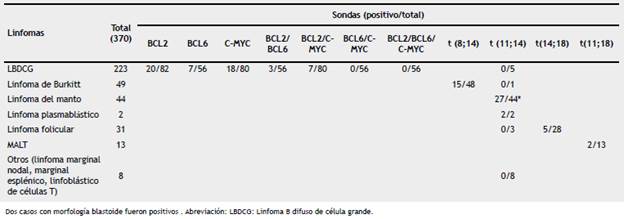
En linfomas más de la mitad de las pruebas (60%, n: 223) correspondieron para diagnóstico y pronóstico de linfoma B difuso de célula grande (LBDCG). Se reconoció positividad en: el 24% casos para BCL2, el 23% positivos para c-MYC, el 12,5% positivos para BCL6, el 8% de positividad de BCL-2/c-MYC y el 5% presentaron positividad para BCL2/BCL6 (fig. 1). No se reconocieron casos con positividad para BCL-6//c-MYC, ni triple hit (BCL-2/BCL-6//c-MYC) (tabla 2). Además se observó positividad para t(8;14) en el 31% de 48 linfomas de Burkitt y positividad de t(11;14) en el 61% de 46 linfomas de células del manto. En una menor frecuencia se reconoció positividad de t (14; 18) en el 18% de linfomas foliculares y 15% de los linfomas tipo MALT mostro positividad para t(11;18).
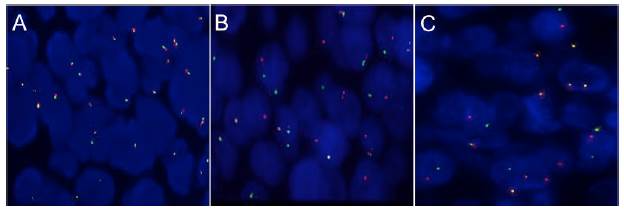
Figura 1 LBDCG positivo doble hit con las sondas Break Apart (Vysis-Abbott) BCL6 (3q27), BCL2 (18q21), CMYC (8q24). A. FISH BCL6 negativo. Los núcleos muestran dos señales de fusión (amarilla) normal. B. FISH BCL2 positivo. Los núcleos muestran una señal de fusión, una verde y una roja independientes correspondientes a rearreglos de gen. C. FISH C-MYC positivo. Los núcleos muestran una señal de fusión, una verde y una roja independientes correspondientes a rearreglos de gen. Las imágenes fueron capturadas y digitalizadas con el programa FISHview de Applied Spectral Imaging.
Tumores sólidos
Cáncer de seno (HER2)
Se realizaron de 428 pruebas para detectar HER2 en cáncer de seno: 126 pruebas fueron positivas (29,4%), 281 pruebas fueron negativas (65,7%), 3 pruebas fueron equívocas (0,7%) y en 18 casos (4,2%) se reconoció material no óptimo y muestras que no hibridaron. Un total de 59 casos fueron polisómicos (13,8%), de los cuales: 26 casos fueron polisómicos positivos (6,07%) y 33 casos fueron polisómicos negativos (7,7%) (fig. 2).
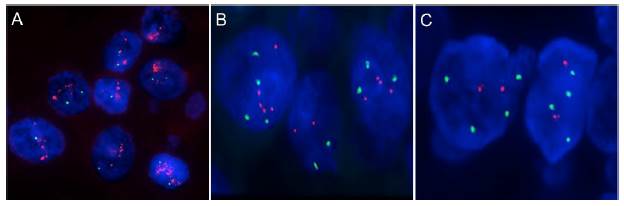
Figura 2 FISH HER2 para cáncer de seno con sondas específicas para el locus HER2 en la región 17q11.2-12 (señal roja) y la región centromérica CEP17 (señal verde) (Kit pathvysion-Vysis-Abbott) Aprobado por la FDA. A. HER2 positivo. Amplificación del gen HER2 con un radio mayor a 2.0. B. HER-2 polisómico equívoco. Con ganancia del CEP17 con un número de copias entre 3-4 C. FISH 17. Con la sonda LSI (17p13.1). Los núcleos muestran 2 señales rojas (17p13.1) y 4 señales verdes (CEP17), descartando una verdadera polisomía. Las imágenes fueron capturadas y digitalizadas con el programa FISHview de Applied Spectral Imaging.
Hasta 2013 se efectuaron 197 pruebas, de las cuales: 55 fueron positivas y 142 negativas. Después de la reclasificación AC20137, se han realizado 231 pruebas: 71 fueron positivas, 138 negativas y 3 equívocos (tabla 3).
Tabla 3 FISH en tumores sólidos (cáncer de seno, tumores de tejidos blandos, cáncer de pulmón, melanoma y otros tumores)
Tumores de tejidos blandos
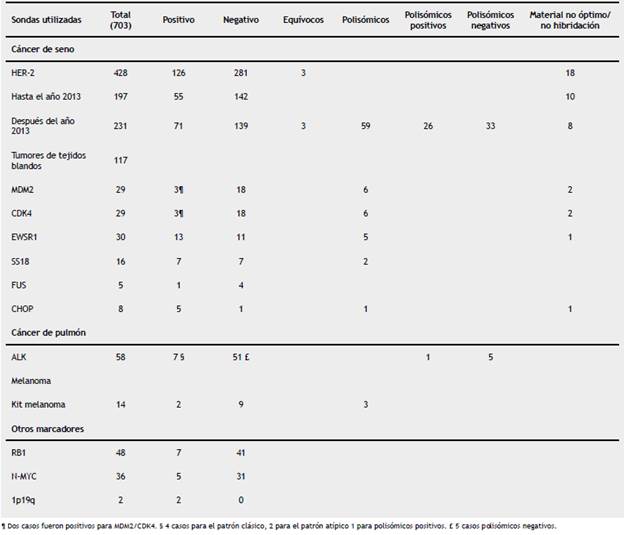
Se efectuaron 111 pruebas para sarcomas de hueso y tejidos blandos. En estos tumores se utilizaron sondas para la detección de MDM2/CDK4, EWSR1, SS18, FUS, CHOP y se observó positividad en el 10%, el 43%, el 44%, el 20% y el 63% respectivamente (tabla 3) (fig. 3).
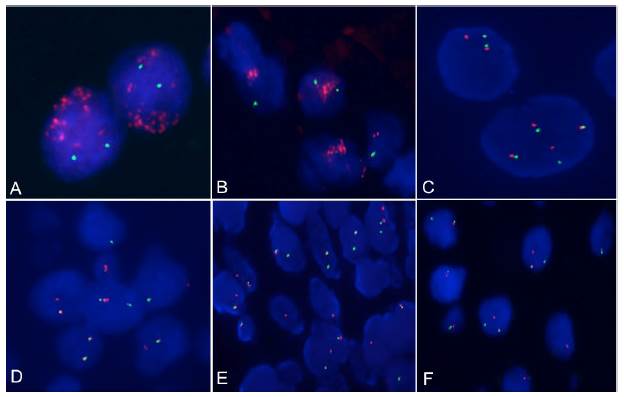
Figura 3 A y B. Liposarcoma bien diferenciado FISH MDM2 (12q15) y CDK4 (12q13) positivos. Los núcleos muestran amplificación con un radio mayor a 2.0. C. MDM2 polisómico se observan 4 señales del MDM2 (12q15) y control CEP12. D. Sarcoma de Ewing. FISH EWSR1 (22q12) positivo con sonda dual color fusion Break Apart (Abbott Molecular). E. Sarcoma Sinovial. FISH SS18(18q11.2) positivo con sonda dual color fusion Break Apart (Abbott Molecular). F. Liposarcoma mixoide de células redondas. CHOP (DDIT3) en la región 12q13 positivo sonda dual color tfusion Break Apart (Abbott Molecular). Las imágenes fueron capturadas y digitalizadas con el programa FISHview de Applied Spectral Imaging.
Cáncer de púlmon (ALK)
De las 58 pruebas realizadas para la detección de ALK con el KIT Vysis® ALK Break Apart FISH Probe (aprobado por la FDA): 7 casos fueron positivos (12%), 4 casos mostraron patrón clásico, 2 patrón atípico y un caso fue polisómico positivo. De los 51 casos negativos, 5 casos mostraron polisomía (9, 8%) (tabla 3) (fig. 4).
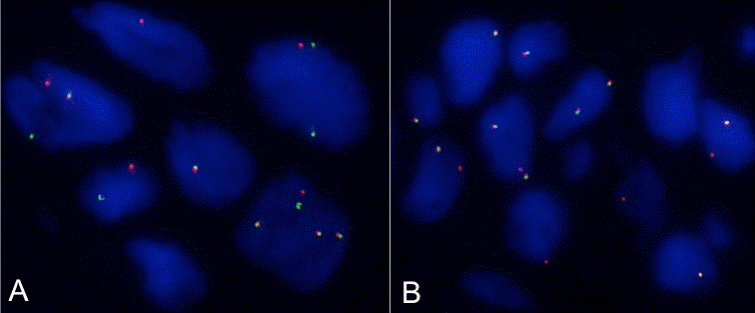
Figura 4 Carcinoma de pulmón de célula no pequeña. FISH LSI ALK dual color, break-apart (Abbott Molecular) A. ALK positivo patrón clásico. Se observa una señal de fusión (native ALK), una verde y una roja independientes en más del 15% de las células tumorales, correspondientes a rearreglos de gen. B. ALK positivo patrón atípico. Se observa una señal de fusión (native ALK) y una señal roja. Las imágenes fueron capturadas y digitalizadas con el programa FISHview de Applied Spectral Imaging.
Melanoma
Con el KIT MELANOMA FISH Abbott Molecular que comprende un panel de 4 sondas (RREB1 (6p25), MYB (6q23), CCND1 (11q13)).
Se analizaron 14 casos, encontrando criterios de positivad en 2 casos (los criterios fueron basados en los criterios y puntos de corte de análisis establecidos por la Universidad de California en UCSF / Universidad San Francisco de Northwestern (Chicago, Illinois) propuestos por Gerami et al8. Todos los casos tuvieron una adecuada correlación histopatológica. Se observaron 3 casos con tendencia a la tetraploidía, uno de ellos con células grandes en una paciente de 9 años9(tabla 3) (fig. 5).
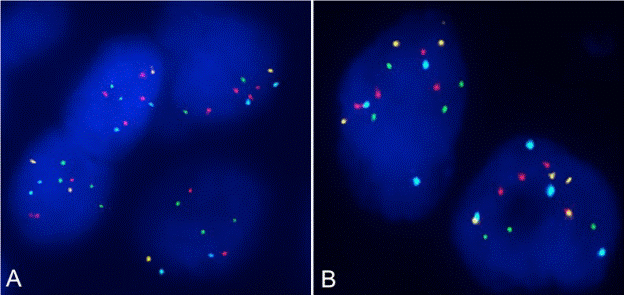
Figura 5. KIT MELANOMA FISH Abbott Molecular. Gen RREB1 6p25 (señal roja), gen MYB 6q23 (señal amarilla), gen CCND1 11q13 (señal verde), control CEN6 (señal aguamarina). A. Melanoma Maligno, FISH positivo, los núcleos muestran aumento en el número de señales de las sondas RREB1, CCND1 y disminución en el número de señales de la sonda MYB, indicando desequilibrio cromosómico clonal con relación al control de centrómero del cromosoma 6. B. Melanoma Spitzoide FISH tetraploide, se muestran 4 señales de las sondas RREB1, CCND1 MYB incluyendo la sonda control CEP6. Las imágenes fueron capturadas y digitalizadas con el programa FISHview de Applied Spectral Imaging.
Otros tumores
Además de las sondas para los tumores que se han mostrado anteriormente, también se han realizado en otros tumores. Por ejemplo, se observó positividad en el 15% de los retinoblastoma para RB1 y el 14% de los neuroblastoma mostraron positividad para N-MYC. Además 2/2 casos con características morfológicas de oligodendriogliomas mostraron codeleción del 1p/19q (tabla 3).
Discusión
En la actualidad se dispone de un gran número de sondas comerciales para la detección de alteraciones citogenéticas relevantes y frecuentes en hematología y oncología. Nuestro laboratorio cuenta con paneles específicos principalmente para cada tipo de neoplasias hematológicas y tumores sólidos, que se han asociado con mal pronóstico considerando las recomendaciones de las guías internacionales en oncohematología.
En hematopatología el MM fue la patología donde se realizó el mayor número de pruebas. Esta entidad se caracteriza por múltiples anormalidades citogenéticas que ocurren a lo largo del curso de la enfermedad, desde estadios premalignos de gammapatía monoclonal de significado indeterminado hasta MAM latente y MM en estadios finales.
Las principales anomalías citogenéticas son trisomías y translocaciones asociadas al gen de la cadena pesada de la inmunoglobulina (IgH). Las trisomías son caracterizadas por una copia extra de uno o más cromosomas (3,5,7,9,11,15,17) y las translocaciones incluyen diferentes subtipos, donde los más comunes son t(11;14), t(4;14), t(6;14), t(14;16) y t(14;20). En cada una de estas translocaciones, un oncogén de un cromosoma asociado se transloca a la región IgH en el cromosoma 14q32; estos genes son: ciclina D1 (11q13), ciclina D3 (6p21) FGFR y MMSET (4p16.3), c-MAF (16q23) y MAF-B (20q11)10.
La detección de anormalidades citogenéticas en MM tiene importancia en el pronóstico y en la estratificación del riesgo, y este último ha sido clasificado en estándar, intermedio y alto, basado en la Mayo stratification for myeloma and risk-adapted therapy classification (mSMART)11,12. Dentro de las alteraciones de riesgo estándar está: t(11;14) y t(6;14), intermedia t(4;14) y ganancia de 1q21, y de las de alto riesgo son Del(17p) (p53), t(14;16), t(14;20) y Del(1p). La positividad de IgH se ha reportado en el 30% de pacientes con MM, seguido de t(11;14) en el 15%, t(4;14) en el 6%, y t(14;16) en el 4%10.
En nuestra población reconocimos positividad en el 50%, el 2%, el 6%, el 0%, respectivamente. Adicionalmente observamos positividad de del (13q) en el 15%, esta otra alteraciones se ha asociado con peor pronóstico13.
En leucemia se han estudiado diferentes anormalidades citogenéticas, en nuestra población la LLA es la entidad con mayor número de pruebas (n: 158). La translocación más frecuente es t (9; 22) en adultos y t (12; 21) en niños respectivamente. Se encontró positividad de t (9; 22) y t (12; 21) en el 7% (tabla 1) y la presencia de t (9; 22) se ha asociado con peor pronóstico5.
En LMA las translocaciones más frecuentes son: t (8;21) (q22;q22), t(15;17) (q22;q12) e inv(16) (p13.1q22) o t(16;16) (p13.1q22)14. En nuestra población encontramos positividad de t (15;17) (q22;q12) en el 44%, t(8;21) (q22;q22) en el 31%, y ningún caso positivo para inv (16) (p13.1q22).
Se han observado que alteraciones en t(8;21) (q22;q22) / RUNX1-RUNX1T1; t(15;17) (q22;q12) / PML-RARa; inv(16) (p13.1q22) o t (16;16) (p13.1;q22) / CBFB-MYH1 y la mutación en ambos genes CEBPA y NPM1 se han asocian con un buen resultado clínico, mientras que t(1;22) (p13;q13) / RBM15 - MKL1; inv(3) (q21q26.2) o t (3;3) (q21; q26.2) RPN1-EVI1; t (6;9) (p23;q34) / DEK-NUP214, reordenación del gen MLL, los cariotipos complejos y las mutaciones, tanto en KIT como en FLT3, se asocian con un pronóstico menos favorable5,14,15.
En neoplasias crónicas como LMC y LLC se han desarrollado 57 y 65 pruebas respectivamente. La t (9; 22) ha sido la prueba con mayor positividad en el 72% en los pacientes con LMC. La positividad de esta alteración es fundamental para el diagnóstico de la LMC y su seguimiento se realiza con RT-PCR para los genes ABL-BCR16. En LLC las anormalidades cromosómicas recurrentes más comunes son la trisomía 12, del (13q), del (11q), del(17p) y del(6q)16.
La información del FISH es fundamental para la respuesta al tratamiento, puesto que pacientes que han recibido fludarabina, ciclofosfamida y rituximab (FCR) tienen una mejor respuesta al tratamiento cuando presentan alteraciones del cromosoma del(11q) y trisomía 12, mientras que los pacientes con del(17p) no se benefician del tratamiento FCR17,18.
Por otro lado, en el SMD se ha reconocido que alteraciones en -5/del (5)(q31), -7/del(7)(q31)- se asocian con el pronóstico international prognostic scoring system (IPSS-R) y la WHO prognostic scoring system (WPSS) y a la respuesta a la quimioterapia19-21. Estas alteraciones citogenéticas asociado a +8, del (20)(q2), -17/del (17) (p3.1), y -Y, se ha encontrado en la mitad de los pacientes5, en nuestra población se reconoció en el 23% y el 20% de -5/del(5)(q31) y -7/del(7)(q31), respectivamente.
La FISH en linfomas se ha convertido en una herramienta fundamental para el diagnóstico y el pronóstico para los LBDCG. Rearreglos en BCL6 corresponden a la anormalidad citogenética más frecuente en los LBDCG, reportada en aproximadamente el 30% y el 40% de los casos22.
En el presente estudio encontramos una positividad menor en el 12,5% y este valor puede ser probablemente por el tamaño de muestra (tabla 2). El BCL2 puede reconocerse positivo del 20 al 30% de los casos23, al igual que este estudio (24%), mientras que el c-MYC entre el 5% y 14%24-26, interesantemente encontramos positividad en el 23%, esto puede ser por el tamaño de muestra, sin embargo consideramos que es interesante conocer la verdadera prevalencia en nuestra población.
La presencia de alteraciones en c-MYC/BCL2 y/o BCL6 se le ha atribuido la definición de doble hit y la presencia de rearreglo de los tres genes de triple hit27. Este grupo de tumores son más agresivos y se han asociado con mal pronóstico, principalmente los triple hit28,29. La translocación de c-MYC asociado con BCL2 o BCL6 puede encontrarse en el 5% de los LBDCG28. De estos, la combinación más frecuente es el c-MYC/BCL2 en el 80% de los casos, mientras que el 20% son positivos para c-MYC/BCL6 30. En este estudio se reconoció positividad de BCL-2/c-MYC en el 8%.
Por otro lado, desde que en 2013 la ASCO/CAP (American Society of Clinical Oncology/College of American Pathologists) modificó el punto de corte para reportar los resultados de HER2, con el objetivos dve minimizar los falsos negativos7. Nosotros evaluamos los resultados de HER2 obtenidos antes de la modificación ASCO/CAP 20 0731, y después del 20137. Observamos que hubo un ligero incremento en los casos positivos (28% vs. 31%) como reportan algunos estudios31.
En 2014 los casos polisómicos equívocos fueron más frecuentes y ese mismo año algunos estudios establecieron una aparente "polisomía" relacionada con ganancias pericentroméricas focales en lugar de polisomía verdadera32. Con respecto a estas publicaciones y siguiendo las recomendaciones de ASCO/ CAP 2013, se empezó a utilizar la sonda 17p13 (p53) como prueba alternativa para reclasificar aquellos casos polisómicos equívocos. En 10 casos polisómicos equívocos de 231 casos (4,3%) se realizó FISH 17p13 (p53) donde se encontraron: HER2 positivos 5 (50%), HER2 negativos 4 (40%) y un caso (10%) permaneció equívocos. Cabe destacar que el HER2 ha sido uno de los pioneros en la oncología personalizada del cáncer de seno y además de ser útil para la clasificación molecular y con esta conocer su pronóstico33, también es fundamental para el tratamiento con trastuzumab; este tratamiento ha mostrado resultados sobresalientes como remisión completa del tumor a lo largo del tiempo, incluso en tumores avanzados34,35.
Con respecto a los tumores de tejidos sólidos cabe señalar que las características moleculares de estos son muy útiles para su clasificación diagnóstica36. Fusiones del gen EWS-FLI1 se detectan en aproximadamente más del 90% de los tumores de Ewing36-38. Además, un gen análogo a EWS, FUS, está implicado con CHOP (DDIT3) en fusiones génicas en el 90% de los casos de liposarcoma mixoide/de células redondas (FUS-CHOP), la t(X; 18) que origina una fusión entre el gen SS18 (SYT) en el cromosoma 18, con el gen SSX asociada a sarcoma sinovial. Diferentes estudios han demostrado que la amplificación de la región 12q13-15 (la cual incluye los genes MDM2 y CDK4) evaluada por FISH está presente en algunos tipos de sarcomas incluyendo liposarcomas36.
Desde 2011 la FDA aprobó el crizotinib para el tratamiento de pacientes con carcinoma de pulmón de célula no pequeña que fueran positivos para FISH ALK con la sonda Vysis39. En nuestra experiencia hemos observado una mayor positividad (12%) con relación a lo previamente reportado por estudios previos de 4,5% a 10,5%40-42. Con respecto a los patrones de FISH ALK positivo, fueron similares a los publicados principalmente mostrando un patrón clásico y en menor proporción el patrón atípico40-42. Adicionalmente se evidenció un 9,8% de casos polisómicos negativos.
Los recientes avances en la comprensión de la patogénesis molecular de proliferaciones melanocíticas han revelado diferencias anormalidades genéticas entre los nevus benignos y el melanoma. La FISH se ha convertido en una ayuda complementaria valiosa para el diagnóstico de melanoma por su alta especificidad. Esta prueba consta de un panel de 4 sondas (fragmentos de ADN pequeños) originalmente establecido por Gerami et al., en el cual incluye un análisis de los genes RREB1 (6p25), MYB(6q23), CCND1 (11q13) y centrómero del cromosoma 68.
En el INC de Colombia la FISH se ha convertido en una herramienta fundamental como complemento en el diagnóstico, el tratamiento y el pronóstico de los pacientes con cáncer. Nuestro laboratorio cuenta con una variedad de sondas (algunas únicas en el país) y la alta sensibilidad y especificidad de la técnica de FISH permite identificar un gran número de reordenamientos cromosómicos en regiones que contengan genes implicados en el desarrollo de neoplasias hematológicas y que no se detectaban con la citogenética convencional.
En la actualidad están disponibles numerosas sondas comerciales para detectar alteraciones cromosómicas recurrentes y que permiten también evaluar cambios en el número de copias de genes específicos en tumores sólidos, lo que mejora la sensibilidad del diagnóstico clínico.
Finalmente, se destaca que la prevalencia de alteraciones evaluadas en el FISH son similares a las reportadas en la literatura. Sin embargo, cabe resaltar que el C-MYC en LBDCG y ALK en cáncer de pulmón es mayor a la reportada en la literatura científica, por lo que es necesario realizar estudios con mayor tamaño de muestra para conocer la prevalencia en la población colombiana debido a que estas pruebas son fundamentales para el diagnóstico, el pronóstico y el tratamiento de estas neoplasias.