Introducción
Para el año 2016, se reportó en Colombia cerca de 120.000 personas infectadas con el virus de inmunodeficiencia humana tipo 1 (VIH-1) y 2.800 muertes asociadas al virus1; sumado a lo anterior, el análisis epidemiológico del comportamiento de la infección en el país muestra una tendencia al aumento anual en el número de casos1, por lo que se requieren programas de intervención que aporten al control de la infección en el país.
En la actualidad, la estrategia con mayor impacto en la salud de los pacientes infectados por VIH-1 es la terapia antirretroviral altamente activa (TARAA), la cual busca inhibir diversos pasos del ciclo replicativo viral2. Sin embargo, las mutaciones asociadas con resistencia a medicamentos antirretrovirales (ARV) comprometen la eficacia de la TARAA3, no sólo en pacientes que han sido previamente tratados sino también en aquellos individuos no previamente tratados o naive, cuya infección es iniciada por una variante viral resistente a ARV lo que se define como resistencia primaria4.
La reciente introducción de los inhibidores de integrasa (INI), o más específicamente, los inhibidores de la transferencia de cadena de integrasa (InSTI) se ha convertido en una alternativa tanto en esquemas de tratamiento inicial como en terapias de rescate para la infección por VIH-1, dada su capacidad para suprimir la integración del ADN viral al genoma humano5. Aunque todos los InSTI significativamente reducen la replicación viral, estudios clínicos de resistencia a ARV han reportado que los InSTI de primera generación, raltegravir (RAL) y elvitegravir (EVG), presentan una baja barrera genética a la resistencia comparados con los inhibidores de proteasa6. A la fecha, se han reportado las mutaciones de resistencia Y143R/C, N155H y Q148K/R/H en el dominio catalítico de la enzima integrasa para RAL cuando se encuentran acompañadas de al menos una de las siguientes mutaciones: L74M/I, E92Q, T97A, E138K/A/T, G140S, Y143H, entre otras7,8; de otro lado, las mutaciones T66I/A/K, E92Q/G, T97A, N155H y Q148H/K/R se han asociado con resistencia a EVG9. En el caso de dolutegravir (DTG), un InSTI de segunda generación, se han reportado raras variantes virales resistentes10 con un perfil de mutaciones limitado al residuo G148 acompañado de L74I, E138A/K/T o G140A/C/S8.
Adicionalmente, se han reportado mutaciones aminoacídicas accesorias cuya sola presencia no aporta a la resistencia al medicamento pero en combinación con otras mutaciones disminuye la susceptibilidad a los InSTI y/o incrementa la replicación viral9. Sumado a lo anterior, los polimorfismos naturales en la integrasa viral pueden favorecer el desarrollo de resistencia a estos medicamentos; un ejemplo es la mutación V72I, la cual puede tener un impacto en el desarrollo de resistencia al RAL, EVG y al DTG11.
Las mutaciones descritas en la integrasa son clasificadas en tres grandes grupos dentro de la base de datos de resistencia a VIH de Stanford: i) mutación mayor, ii) mutación accesoria y iii) mutaciones misceláneas. Las mutaciones mayores son substituciones no polimórficas que juega un papel importante en la reducción de la susceptibilidad a uno o más InSTI. Las mutaciones accesorias se definen como substituciones en posiciones no polimórficas o mínimamente polimórficas que contribuyen a reducir la susceptibilidad en combinación con una o más mutaciones mayores. También se incluyen substituciones altamente inusuales y mal caracterizadas en las principales posiciones de resistencia a los fármacos y finalmente las mutaciones misceláneas son aquellas que no están asociadas con la resistencia a los medicamentos; incluye mutaciones en sitios polimórficos que pueden estar débilmente asociadas con resistencia a los fármacos. Se describe otro grupo de mutaciones definidas como Otras que son mutaciones no reportadas por la base de datos de Stanford pero que, en ensayos in vitro, se han asociado con resistencia a InSTI.
Teniendo en cuenta la baja barrera genética de algunos InSTI, la tendencia creciente en el uso de este tipo de medicamentos y la transmisión potencial de variantes virales resistentes a INI12, se hace necesario la caracterización de mutaciones en la integrasa en individuos naive para poder optimizar los esquemas iniciales de tratamiento ARV. En Colombia, los reportes de frecuencias de resistencia se han limitado a los inhibidores de la transcriptasa reversa y de la proteasa, excluyendo mutaciones asociadas a InSTI, por lo cual el objetivo de este estudio fue identificar y estimar las frecuencias de mutaciones mayores y accesorias, y de polimorfismos adicionales asociados con resistencia a este grupo de fármacos.
Materiales y métodos
Tipo de estudio, diseño muestral y población de estudio
Este es un estudio descriptivo de corte transversal en el que se reclutaron 96 individuos infectados con VIH-1 del programa de atención integral de la entidad prestadora de salud SURA (EPS SURA) de Medellín, Colombia, captados entre 2013 y 2015. Los pacientes se seleccionaron con base en los siguientes criterios de inclusión: i) ser mayor de 18 años, ii) no haber recibido terapia antirretroviral, iii) tener carga viral detectable y iv) residir en Medellín al menos en los últimos 5 años.
De cada participante se obtuvo consentimiento informado, datos relacionados con conductas de riesgo (compañeros sexuales, tipo de relación sexual que incluía las siguientes opciones: hombres que tienen sexo con hombres (HSH), hombres que tienen sexo con hombres y mujeres (HSHM), hombres que tienen sexo con mujeres (HSM) y mujeres que tienen sexo con hombres (MSH); además de otros datos como uso de preservativo, uso de drogas alucinógenas entre otros) y se garantizó la confidencialidad de la información. El proyecto fue avalado por el comité de bioética de la Sede de Investigaciones Universitarias (CBEIH-SIU) de la Universidad de Antioquia (Acta 15-08-449), y por el comité de Investigaciones de la entidad EPS SURA, Medellín.
Extracción de ARN viral y síntesis del ADNc
A partir de plasma obtenido de sangre anticoagulada con EDTA, se extrajo el ARN viral siguiendo las instrucciones del estuche comercial Qiamp Viral Mini Kit (QIAGEN, Hilden, Alemania). Para la síntesis del ADNc se utilizó el estuche comercial RevertAid H Minus First Strand cDNA Synthesis Kit (Thermo Scientific), utilizando el cebador UNINEF específico para VIH, reportado por Nadai y colaboradores13 (Tabla 1).
Amplificación de la integrasa a partir gen pol del VIH-1 de ARN viral
La amplificación se realizó por medio de la técnica de PCR anidada utilizando cebadores específicos para el gen pol y el protocolo reportado por Nadai y colaboradores13 (Tabla 1), modificando la temperatura de alineamiento a 60ºC en los primeros 10 ciclos y el tiempo de elongación a 5 minutos en todos los ciclos, en ambas rondas de amplificación. El tamaño del amplificado fue de aproximadamente 900 pb, correspondiente a las posiciones 4001 pb - 5112 pb de la secuencia HXB2.
Secuenciación, ensamblaje, edición y alineamiento de secuencias
Los productos de PCR fueron secuenciados por el método de 2-dideoxinucleótidos, con el sistema ABI3730XL en un servicio comercial (Macrogen Inc. Corea). Se utilizaron los juegos de cebadores mostrados en la tabla 1 y reportados por Malet y colaboradores7.
Las secuencias parciales obtenidas a partir de una misma muestra fueron ensambladas y editadas en “contigs” individuales en el programa Seqman II versión 5.01 de DNASTAR (Lasergene, Madison, WI USA), utilizando como guía la secuencia HXB2 (Genbank: K03455.1). Las secuencias consenso obtenidas de cada “contig” fueron alineadas utilizando el programa MEGA 7.0.1414 (http://www.megasoftware.net/) bajo el algoritmo MUSCLE15. Las inserciones que no se encontraran en la secuencia de referencia HXB2 fueron eliminadas. Todos los nucleótidos, incluyendo los ambiguos, y sus aminoácidos derivados fueron denominados de acuerdo con los códigos IUPAC (http://www.bioinformatics.org/sms/iupac.html).
Identificación de mutaciones asociadas a resistencia Antirretroviral
Con las secuencias alineadas se realizó la construcción de un árbol filogenético por el método de Máxima Verosimilitud basado en el modelo General de Tiempo Reversible (GTR) utilizando el programa MEGA716 con un soporte de 1000 replicaciones bootstrap17. Para dicho árbol filogenético se incluyeron secuencias homologas de subtipo B, secuencias no-B y formas recombinantes circulantes aisladas en Suramérica. El porcentaje de adenina-timina, la diversidad nucleotídica y la prueba de neutralidad de Tajima D se realizó en el programa DnaSP618
La frecuencia de sitios polimórficos fue realizada por conteo directo, mientras que las mutaciones asociadas a resistencia fueron identificadas en la base de datos de la Universidad de Stanford19, disponible en https://hivdb.stanford.edu/hivdb/by-mutations/. Además, se revisó literatura para identificar otras mutaciones asociadas con resistencia que no se encontraban en la base de datos mencionada. Las frecuencias de polimorfismos y de mutaciones asociadas a resistencia fueron calculadas como el número de secuencias que poseían el residuo mutado sobre el total de secuencias que incluían dicho residuo.
Resultados
Las características de los 96 individuos elegibles para el estudio, 95% de sexo masculino, se detallan en la figura 1. En general, estos individuos exhibían comportamientos de alto riesgo: 21% tenían un compañero sexual seropositivo para VIH, 28% tenían historia de relaciones sexuales con extranjeros y 34% tuvieron episodios previos de otras enfermedades de transmisión sexual. La mediana de número de parejas sexuales totales reportadas por individuo fue de 10 y el uso de preservativo fue ocasional en la mayoría de la población estudiada. La mediana de la carga viral fue de 33.121 copias/ mL y de 471,5 células/μL para los linfocitos T CD4+.
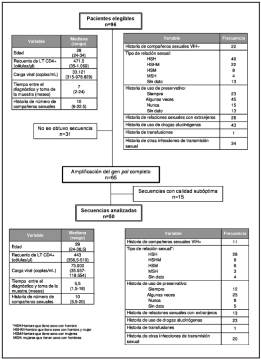
Figura 1 Diagrama de flujo de los pacientes elegibles. Se muestran las características clínicas y epidemiológicas, así como las causas de exclusión de las secuencias.
De las 96 muestras obtenidas en el estudio se logró la amplificación del gen pol en 65 de ellas, pero sólo de 50 se obtuvo secuencias de buena calidad en la mayor parte del segmento de la integrasa, y sólo estas fueron analizadas.
El árbol filogenético realizado utilizando el método de máxima verosimilitud muestra la topología característica de ramas terminales largas y ramas basales cortas de secuencias de VIH (figura 2). Todas las secuencias de este estudio se agruparon con secuencias del Subtipo B, mas no con formas recombinantes circulantes (CRF). Las secuencias colombianas no forman un grupo monofilético sino que están entremezcladas con secuencias de referencia del Subtipo B aisladas en otros países de Suramérica. Sin embargo, la mayoría de los soportes de rama son bajos (<70), lo cual impide hacer inferencias sobre número de introducciones del virus en la población estudiada.
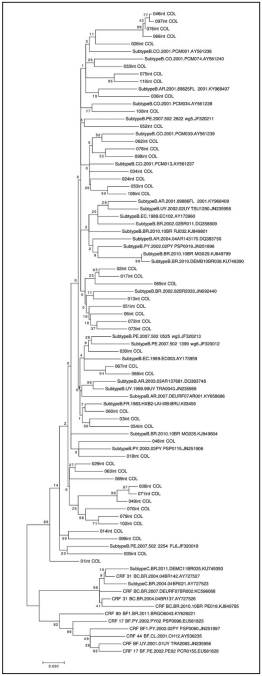
Figura 2 Análisis flogenético molecular de 50 secuencias del gen integrasa de VIH-1. El árbol flogenético fue inferido por el método de Máxima Verosimilitud basado en el modelo General de Tiempo Reversible utilizando las secuencias de integrasa obtenidas en este estudio y otras secuencias reportadas en Suramérica, incluyendo formas recombinantes circulantes.
Los resultados de la prueba de neutralidad de Tajima D, incluyendo los sitios segregantes, el índice de polimorfismo nucleotídica y la diversidad nucleotídica, se muestran en la tabla 2, donde se presentan 222 sitios segregantes y una diversidad nucleotídica baja (0.049). La D de Tajima arrojó un valor negativo sin diferencia estadísticamente significativa.
Tabla 2 Estimaciones de diversidad nucleotídica del gen de integrasa de 50 pacientes naive crónicamente infectados con VIH-1 en Medellín, Colombia
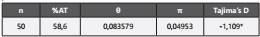
N: número de secuencias; %AT: porcentaje de adenina-timina, θ: índice de polimorfsmo nucleotídico; π: índice de diversidad nucleotídica; *p>0,05.
De igual forma, se identificaron 150 sitios polimorfismos en las secuencias evaluadas (Tabla 3). Las mutaciones observadas y potencialmente asociadas a resistencia a los InSTI, con su respectiva frecuencia y fenotipo asociado, se muestran en la Tabla 4. El 2,2% de las secuencias presentan la mutación mayor E138K; además, se encontraron tres mutaciones accesorias mayores de resistencia: G163E, L74I y E157Q, con frecuencias del 6,4%, 6,0% y 4,2%, respectivamente. La mutación no polimórfica seleccionada in vitro por EVG, A128T, fue observada con frecuencia del 2,0%.
Tabla 3 Perfl de mutaciones aminoacídicas en el gen de integrasa de 50 pacientes naive crónicamente infectados con VIH-1 en Medellín, Colombia

Tabla 4 Mutaciones detectadas asociadas con resistencia a los inhibidores de integrasa (InSTI).
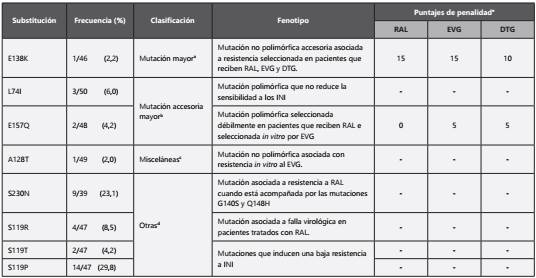
a Mutación mayor: substitución no polimórfca que juega un papel importante en la reducción de la susceptibilidad a uno o más InSTI.. b Mutación accesoria mayor: substitución en posiciones no polimórfcas o mínimamente polimórfcas que contribuyen a reducir la susceptibilidad en combinación con una o más mutaciones mayores. También se incluyen substituciones altamente inusuales y mal caracterizadas en las principales posiciones de resistencia a los fármacos. C Misceláneas: mutaciones que no están asociadas con la resistencia a los medicamentos, incluye mutaciones en sitios polimórfcos que pueden estar débilmente asociadas con resistencia a los fármacos. d Otras: mutaciones no reportadas por la base de datos de Stanford pero que, en ensayos in vitro, se han asociado con resistencia a InSTI. e Puntaje de penalidad: Nivel estimado de resistencia a un medicamento, el cual es considerado como susceptible si el puntaje se encuentra entre 0 a 9, potencial bajo nivel de resistencia con un cuando el puntaje esta entre 10 a 15, y bajo nivel de resistencia con puntajes entre 15 a 29
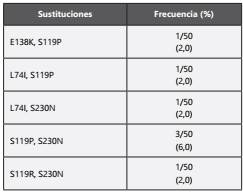
Sumado a lo anterior, en la posición 230, donde la mutación asociada con resistencia es S230R, se observó la substitución S230N en el 23,1% de las secuencias. De igual forma, fue observada (con su respectiva frecuencia) las siguientes variantes aminoacídicas en la posición 119: S119P (29,8%), S119R (8,5%) y S119T (4,2%).
De las 50 muestras evaluadas, seis secuencias presentaban combinación de sustituciones de mutaciones accesorias con otras mutaciones reportadas in vitro asociadas con resistencia a antirretrovirales, mientras que sólo una secuencia presentaba combinación con una mutación mayor (Tabla 5).
Discusión
A pesar de la introducción de los InSTI al mercado colombiano desde el año 2010 y de múltiples reportes de mutaciones asociadas a resistencia a InSTI en otros países20, en Colombia no se han descrito dichas mutaciones en población crónicamente infectada con VIH-1.
En este estudio, realizado con secuencias de integrasa aisladas de pacientes naive para el tratamiento, se observó un test de neutralidad negativo sin valor estadísticamente significativo, valor que no permite rechazar la hipótesis de neutralidad y, por lo tanto, aceptar que no se ejerció presión selectiva sobre las mutaciones21.
Sumado a lo anterior, se identificaron varias mutaciones que se asocian con resistencia a InSTI. La E138K es una mutación mayor que es seleccionada por el tratamiento por RAL, EVG y DTG. Cuando se acompaña de mutaciones como Q1488 ó R26322 disminuye la susceptibilidad del virus a los InSTI. Dado que en este estudio no se identificaron mutaciones en las posiciones 148 ó 263, la presencia de la E138K en un individuo de este estudio sugiere exposición del virus a uno de estos medicamentos en un paso anterior en la cadena de transmisión, pero no necesariamente implica resistencia en el individuo portador.
La mutación E157Q es seleccionada in vivo por RAL e in vitro por EVG23. Un estudio realizado en Polonia en pacientes naive para el tratamiento reportó esta mutación en menos del 1%24; en la población de este estudio se encontró dicha mutación en una frecuencia del 4,2%. La E157Q disminuye casi cinco veces la susceptibilidad a RAL y dos veces a EVG en individuos previamente tratados25,26. Respecto a DTG, Danion y colaboradores reportaron falla virológica en un paciente con la mutación E157Q, adherente al esquema de tratamiento, en ausencia de mutaciones de resistencia para inhibidores de transcriptasa reversa y de proteasa27. Lo anterior indica que la E157Q puede comportarse como una mutación mayor, aunque suele clasificarse como mutación accesoria mayor23. La mutación S230N, observada con una frecuencia del 23,7% en este estudio, no se ha asociado a resistencia clínica a InSTI, pero en un estudio in vitro se observó que, cuando se acompaña de las mutaciones mayores G140S y Q148H, disminuye marcadamente la susceptibilidad a RAL28. Su alta frecuencia en la población de Medellín podría predisponer a la selección de las citadas mutaciones y a la aparición de resistencia a RAL en personas que se expongan a dicho medicamento.
Un paciente de este estudio tenía la mutación A128T, reportada también en estudios europeos con frecuencias entre 1 y 2% en pacientes no tratados29. Según la base de datos de VIH de Stanford, la A128T es una mutación accesoria seleccionada in vitro por EVG pero que no se ha asociado con resistencia a InSTI23; sin embargo, varios reportes indican que esta mutación induce resistencia a un nuevo grupo de fármacos que actúan impidiendo la multimerización de la integrasa con moléculas como el “factor de crecimiento derivado del epitelio del cristalino” (LEDGF), un cofactor requerido en la integración del genoma viral30,31. Estas nuevas drogas, llamadas LEDGIN, son inhibidores alostéricos de la integrasa y pueden constituir un recurso terapéutico importante en el futuro32; sin embargo, hay que tener en cuenta que la presencia de la mutación A128T podría conferir resistencia primaria a estos nuevos medicamentos.
En este estudio los polimorfismos en la posición 119 de la integrasa se presentaron con frecuencias altas (29,8%, 8,5%, y 4,2% para, S119P, S119R y S119T, respectivamente), similar al 26% reportado para el conjunto de estas mutaciones en un estudio en 458 secuencias de VIH-1 subtipo B de individuos naive para el tratamiento33. Mutaciones del residuo S119 tienden a acompañar a las mutaciones mayores N155H y Q148H/R; en particular la S119R se ha asociado a falla virológica en pacientes en tratamiento con RAL.
El mismo estudio demostró que la mutación S119R disminuye significativamente la sensibilidad in vitro a los InSTI cuando acompaña a las mutaciones Y143C, Q148H, N155H, G140S/Q148H o T97A/Y143C33.
Finalmente, la mutación L74I fue observada con una frecuencia del 6,0%. L74I y L74M se han clasificado como mutaciones accesorias mayores pero también como polimorfismos naturales con frecuencias entre 0,5 - 20,0% en la integrasa de pacientes no tratados en diferentes estudios23; sin embargo, en combinación con Q148H/K/R o N155H, L74I puede generar resistencia a RAL y disminución de la susceptibilidad in vitro y de la respuesta virológica a DTG8.
En resumen, en este estudio encontramos una baja frecuencia de mutaciones mayores de resistencia a InSTI y frecuencias variables de mutaciones accesorias y polimorfismos asociados a resistencia, resultado esperado en una población no tratada y en un momento temprano del uso de esta familia de medicamentos. Sin embargo, la frecuencia de dichas mutaciones podría incrementarse a medida que el uso de los InSTI se extienda y con la eventual introducción de nuevos tipos de medicamentos dirigidos a la integrasa viral, como los inhibidores alostéricos.
Limitaciones
La mayor limitación de este estudio es el bajo número de secuencias analizadas y el muestreo restringido a pacientes de una sola ciudad y una única institución asistencial, por lo cual estos resultados deben evaluarse en conjunto con estudios que se realicen en otras poblaciones de Colombia. De esta forma se podrán formular recomendaciones sobre en quienes y en cual momento sería conveniente realizar pruebas genotípicas que incluyan el gen de integrasa antes del inicio de la terapia.