INTRODUCCIÓN
Las hormigas han sido reportadas como enemigos naturales de una gran variedad de artrópodos. Ellas tienen el potencial de ejercer una presión significativa sobre sus presas herbívoras, ya que exhiben una amplia gama de preferencias alimentarias y, debido a su comportamiento y carácter social, pueden consumir especies de todos los tamaños [1,2]. Su ubicuidad en áreas urbanas, boscosas y agrícolas, junto con sus hábitos alimenticios diversos, sugiere que sus patrones de consumo podrían tener efectos importantes para la dinámica de la red alimentaria. Además, varias especies de hormigas son depredadoras importantes de plagas agrícolas tropicales tan diversas como la broca del café Hypothenemus hampei (Ferrari) (Coleoptera: Scolytidae) [7], y de otras plagas como la mosca de la fruta oriental Bactrocera dorsalis (Hendel) (Diptera: Tephritidae) en cítricos [3] y sobre ninfas de Idioscopus nitidulus (Walker) (Hemiptera: Cicadellidae) en mango [8]. Sin embargo, sus interacciones dentro de las redes alimenticias de muchos otros sistemas siguen siendo poco claras. Para caracterizar mejor el impacto de las hormigas como depredadores, es necesario mapear la estructura de sus redes alimenticias y establecer patrones generales de consumo. Los métodos utilizados para caracterizar las redes alimentarias de las hormigas han sido a menudo aproximados y vagos. Los ensayos visuales de forrajeo de hormigas presentan una extrema dificultad en su ejecución, especialmente en las especies forrajeras nocturnas, y proporcionan estimaciones relativamente poco confiables de la depredación.
El análisis molecular del contenido estomacal, un método post-mortem de identificación de enlaces tróficos, es altamente sensible a la identificación de ADN específico de presa dentro del estómago de los depredadores [4] y podría ser una excelente herramienta para identificar los vínculos tróficos y estimar los patrones de depredación de las hormigas sobre especies claves de presas como Hypotenemus hampei.
Para la broca del café, estudios anteriores han utilizado el análisis molecular del contenido intestinal de varios insectos depredadores como Karnyothrips flavipes Jones (Thysanoptera: Phlaeothripidae), Cathartus quadricollis (Guér.) (Coleoptera: Silvanidae) y Leptophloeus sp.(Coleoptera: Laemophloeidae) confirmando el papel depredador de estos insectos en granos de café brocados [5]. Los cebadores del gen COI específicos de especie diseñados para H. hampei demostraron tener un alto grado de especificidad para ADN de broca y no produjeron ningún producto de PCR a partir de ADN molde de otros insectos asociados a los agroecosistemas de café [9]. Igualmente, mediante ensayos de alimentación en laboratorio, Jaramillo y colegas [9] demostraron que un fragmento de 185 pb de ADN de COI de H. hampei podría permanecer intacto durante un máximo de 30 h en el tracto digestivo de K. flavipes. Finalmente, en muestreos de campo los autores encontraron que, en total, 3.327 K. flavipes emergieron de 17.792 frutos infestados con H. hampei recogidos entre abril y septiembre de 2008. A lo largo de la temporada, el 8,3% de K. flavipes dio positivo para ADN de H. hampei, aunque a veces esta cifra se acercó al 50%. Estos resultados revelaron que la disponibilidad de las presas se correlacionó significativamente con el consumo de éstas, lo que indica el impacto potencial sobre las poblaciones de H. hampei. Con los anteriores antecedentes y dado que varias especies de hormigas han sido encontradas depredando la broca, el presente estudio evaluó la especificidad de un par de cebadores del gen mtCOI para identificar broca del café haciendo un análisis molecular del contenido intestinal de hormigas alimentadas con broca empleando el método propuesto en la literatura.
MÉTODO
Establecimiento y selección de las hormigas depredadoras en laboratorio
Se realizó un análisis exploratorio para determinar cuáles géneros de hormigas eran los más abundantes en el campo y los más apropiados para criar en laboratorio y con mayor potencial depredador. Para esto se establecieron colonias artificiales usando cajas plásticas con: Crematogaster montezumia, C. nigropilosa, C. curvispinosa, C. erecta, C. crinosa, Linepithema sp., Tapinoma sp., Nesomyrmex asper, Nylanderia sp., Pheidole sp., Wasmannia auropunctata y Solenopsis stricta y Monomorium floricola, recolectadas en cafetales del Cauca y Chinchiná (Caldas). Posteriormente, las colonias se alimentaron con granos brocados. Se ofreció a las colonias 3 a 4 granos brocados con diferentes estados (larvas, adultos y huevos) de H. hampei obtenidos de granos pergamino de café infestados, proporcionados por el laboratorio Biocafé de Chinchiná (Caldas). Las colonias fueron revisadas diariamente para evaluar el consumo de broca. Las observaciones evidenciaron que las hormigas forrajean sobre los granos pero no penetran por los orificios, la mayoría de estas especies son más grandes que los orificios del grano de café, por los que algunas debían escavar los granos para poder entrar. Sólo W. auropunctata y S. stricta fueron observadas entrando en los granos sin mucho esfuerzo, debido a su diminuto tamaño (±1 mm), y fueron más activas forrajeando sobre los granos. Finalmente, se seleccionó a W. auropunctata, dado que esta especie reportó tasas de depredación del 100% y colonias con numerosas obreras que garantizaban el número de muestras necesarias para los análisis. En total se alimentaron seis colonias de las cuales a tres se les ofreció entre tres a cuatro granos brocados partidos a la mitad con larvas, adultos y huevos de la broca expuestos, por cinco días además de agua y miel. A las colonias remanentes se les ofreció una presa alternativa criada en laboratorio (generalmente Acrididae, Ephesthia kuehniella o Tenebrio mollitor), agua y miel. Antes de iniciar la alimentación con broca, las colonias fueron sometidas a un periodo de ayuno de cinco días (solo se les ofrecía agua y miel) con el objeto de estimular la depredación.
Extracción de ADN
El ADN total se extrajo de especímenes triturados utilizando el kit especializado QIAGEN DNeasy Blood & Tissue Kit siguiendo el protocolo suplementario de purificación de ADN total de insectos del fabricante, con una excepción: en el paso 1 no se usó nitrógeno líquido ni mortero, sino que se añadieron 10 µL de solución ATL (Tissue Lysis Buffer) amortiguadora a la muestra, se maceró con puntas de micropipeta estériles. Posteriormente, en el paso 2, se agregaron los 170 µL restantes para completar 180 µL de la ATL amortiguadora. El resto del proceso se realizó de la forma descrita en el protocolo.
PCR
Se llevó a cabo usando el par de cebadores CBB-COI-F (5’-TTGACAAAGGAGCAGGAACA-3’) y CBB-COI-R (5’-TTCTGGCTGTATCCCAGGAG-3’) específicos de H. hampei para amplificar un fragmento de 185 pb del gen COI, los cuales fueron probados en un trabajo anterior [9]. En dicho trabajo se realizó un análisis extenso de reactividad cruzada contra especies de insectos que se encuentran comúnmente en el interior de los frutos de café y otros 69 organismos no objetivo que representan 41 familias dentro de 11 órdenes de invertebrados. Estos cebadores no produjeron amplificación de ADN de ninguna de las otras especies examinadas.
Además, se utilizó el par de cebadores CI-13 (5’-ATAATTTTTTTTATAGTTATACC-3’) y CI-14 (5’-GTTTCTTTTTTTCCTCTTTC-3’) diseñados en estudios moleculares con el género Crematogaster (Quek et al. 2004) para amplificar un fragmento de aproximadamente 608 pb del gen COI con el fin de confirmar el éxito de la extracción del ADN de las hormigas, así como su viabilidad para su uso en PCR.
Las reacciones de PCR (10 µL de volumen final) se realizaron utilizando Go Taq Master Mix (Promega), con 0,2 µM de cada cebador y 1 µL de ADN molde cuantificado previamente por Nanodrop (0,4 - 40 ng). Las reacciones de PCR se corrieron en un termociclador Benchmark TC 9639. El ciclo térmico de la PCR para CBB-COI-F de 185 pb consistió en 95°C por 5 min seguido por 40 ciclos de 95°C por 30 seg, 55°C por 30 seg, 72°C por 30 seg, con una extensión final de 72°C por 7 min. Para los otros dos cebadores (186 y 164 pb) el ciclo térmico de la PCR consistió en 95°C por 5 min seguido por 40 ciclos de 95°C por 30 seg, 62°C por 30 seg, 72°C por 30 seg, con una extensión final de 72°C por 7 min. Finalmente, se realizaron geles de poliacrilamida y los productos de PCR se visualizaron mediante tinción con nitrato de plata (10 mg/mL).
Análisis genético en hormigas alimentadas con broca del café
Las muestras para los análisis de PCR fueron obtenidas a partir de individuos (adultos), en número variable y por separado (uno, tres y cinco, debido al pequeño tamaño de la hormiga), provenientes de tres colonias de W. auropunctata alimentadas con broca. A estos cebadores no se les cambió las condiciones. Las muestras se tomaron después de 24 h de comprobarse la ingesta de broca por parte de la hormiga. Como controles se emplearon ejemplares de esta especie, de tres colonias diferentes alimentadas sobre larvas de Ephesthia kuehniella, Tenebrio mollitor y especímenes de Acrididae, control de extracción (sin ADN) y control de PCR. Se realizaron tres réplicas de cada nivel de tratamiento. Se efectuó la PCR con un par de cebadores específicos para H. hampei, teniendo como control positivo muestras con ADN extraído de individuos de broca. En cada reacción de PCR se hicieron dos repeticiones usando el ADN de individuos o grupos de individuos que fueron alimentados con broca, así como de los controles (alimentados con otras presas).
RESULTADOS
Los cebadores específicos de H. hampei produjeron amplificación del fragmento de 185 pb en muestras de ADN extraído de adultos y larvas de broca como también en muestras de ADN extraído de obreras de W. auropunctata que habían consumido broca. Sin embargo, se detectó amplificación de una pequeña banda muy próxima a la banda de broca en hormigas que no habían consumido broca (controles). Esta banda no específica de broca, se especula que puede tratarse de un falso positivo atribuible posiblemente a la presencia de material genético bacteriano en el contenido intestinal de la hormiga. Para eliminar la banda de las muestras de hormigas sin consumo de broca, obtenidas con el par de cebadores CBB-COI-F y CBB-COI-R se modificaron las condiciones de temperatura de la PCR desde 55, 57 y 59°C, y también se ensayaron diferentes cantidades de ADN (2 y 4 μL), con el objeto de disminuir la posibilidad de alineamiento de los cebadores a zonas no específicas. Sin embargo, la banda apareció en el 83,72% de las muestras de hormigas sin consumo. Los resultados obtenidos para el otro par de cebadores (186 y 164 pb), fueron similares (cuadro 1).
Cuadro 1 Número total y porcentaje de detección de los cebadores diseñados para broca, en BB: broca; HCC: hormigas con consumo de broca y HSC: hormigas sin consumo de broca.
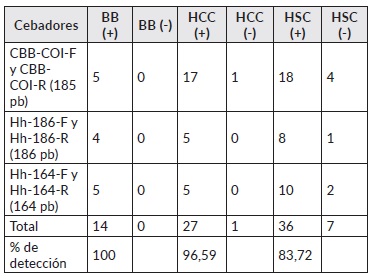
Los resultados del presente estudio no permiten confirmar la potencialidad de los cebadores ensayados para evaluar la conectividad trófica entre la hormiga W. auropunctata y la broca en los ecosistemas cafeteros. Una posible explicación recae en las reacciones cruzadas que aparecen como falsos positivos en el sistema de detección por PCR debido a reacciones de baja eficiencia.
Esto puede estar relacionado con la forma en que las hormigas ingieren su alimento, el cual no se consume por completo. Ellas poseen un saco, llamado buche o estómago social, donde pre-digieren su alimento y parte de su contenido es regurgitado para alimentar a otras obreras y larvas [10]. Por lo tanto, es posible que una cantidad mínima de ADN de broca sea conservada en su estómago. Un estudio [11] ha demostrado que si el ADN dentro de la muestra contiene un pequeño número de secuencias en concentraciones relativamente altas, entonces las secuencias menos concentradas a menudo no amplifican porque la PCR favorece los tipos de ADN dominantes; o por “necesidad” del cebador es posible que se amplifique tanto el ADN de la presa como el del depredador [11]. Este es un problema particular en estudios de dieta molecular, donde el ADN del depredador está a menudo presente en mayor exceso que el ADN derivado del alimento [11].
Pocos estudios han utilizado el contenido estomacal de las hormigas para análisis moleculares debido a que las hormigas han revelado dificultades para obtener ADN de presa usando extracciones de cuerpo entero. Un estudio [12] probó 24 hormigueros para evaluar la depredación de Homalodisca vitripennis (Hemiptera: Cicadellidae) utilizando PCR pero ninguno resultó positivo, a pesar de la discrepancia del 12% de los ensayos positivos usando inmuno absorción enzimática para la misma presa. Del mismo modo, un estudio [13] que investigó la depredación de Camponotus pennsylvanicus (Hymenoptera: Formicidae) sobre barrenadores de roble rojo (Coleoptera: Cerambycidae) reveló que muy pocos especímenes capturados en campo fueron positivos (1,7%) a pesar de altos niveles de observaciones de depredación en las masas de huevos colocadas artificialmente. Aunque estos estudios no analizaron si se inhibía la extracción y la amplificación del ADN del intestino de la hormiga, este fenómeno se ha reportado en Tetramorium caespitum, Solenopsis invicta y Camponotus floridanus [6]. Estos autores encontraron que tanto el gáster como el buche producían niveles significativos de inhibición de la PCR [6].
Dentro de las hormigas, se ha postulado que la inhibición de la PCR podría ser debido a la interferencia de las glándulas dentro del gáster, donde se encuentra la mayoría del tracto digestivo de la hormiga adulta [14]. La incertidumbre en la detección de ADN en el gáster de las hormigas y la falta de fiabilidad de los datos así obtenidos indican la importancia de caracterizar el efecto de los órganos de las hormigas sobre la detección del ADN y el éxito de la amplificación.
Aunque no era el objetivo de este estudio evaluar la eficiencia de depredación sobre la broca, y por tanto no se presentan estos resultados, sí se puede destacar que dos de las especies que se criaron en laboratorio W. auropunctata y Solenopsis stricta depredaron broca en dichas condiciones. Estas hormigas, de hábitos arborícolas y rastreros, exhiben dos características eco-fisiológicas que permitirían, eventualmente, ser involucradas en un manejo integrado de la broca en Colombia. Primero, por ser muy pequeñas (de ± 1 mm), su tamaño facilita la depredación de la broca dentro del grano y, segundo, sus hábitos de anidar en ramitas y en tallos de plátano cosechado lo que permitiría la fácil provisión de sitios de anidación en los cafetales y así aumentar su impacto sobre el control de la broca. En particular, W. auropunctata fue encontrada depredando dentro de los granos en condiciones de laboratorio y campo, lo que indica que es una especie que sube a los arbustos del café para forrajear, y puede disminuir el daño que la broca hace al producto principal. Al mismo tiempo, al anidar en ramitas sobre el suelo puede eliminar sectores de la plaga que se encuentren en los granos que caen al suelo, disminuyendo los focos de reinfección. No obstante, ambas especies, poseen un prontuario bastante negativo por su carácter invasor y agresivo [15], por lo cual interfieren, con sus picaduras, el proceso de recolección del café. Con respecto al carácter invasor de W. auropunctata, se aclara que esta especie se usó como modelo para estandarizar la metodología de detección de broca en el trabajo, pero esta metodología se podría implementar para otras especies de hormigas nativas con potencial depredador hacia la broca del café.
Los resultados de este estudio plantean la necesidad de seguir explorando herramientas moleculares para comprender el papel agroecológico de las hormigas depredadoras en el agroecosistema del café, pues diferentes mecanismos ecológicos y fisiológicos podrían impedir concluir con certeza las conexiones en la red trófica a partir de marcadores moleculares para la broca del café.














