Growth performance of Blanco Orejinegro and Romosinuanobullocks on pasture¤
Desempeño de toretes de las razas criollas Blanco Orejinegro y Romosinuano en prueba de crecimiento en pastoreo
Teste de desempenho para crescimento de touros jovens das raças Blanco Orejinegro e Romosinuano avaliados a pasto.
Rodrigo A Martínez1*, Z, MSc, PhD; Jaime Quiceno2, MVZ; Jaime L Gallego2, MVZ; Henry Mateus2, Agr; Omar Rodríguez1, Z; Pedro Medina1, Z, MSc; Hugo Ballesteros1, Z.
1Centro de Investigaciones Tibaitatá, Km. 14 vía Mosquera, CORPOICA.
]]> 2 Estación ExperimentalEl Nus,SanRoque, Antioquia, CORPOICA.(Recibido:28 julio, 2010; aceptado: 26 abril, 2011)
Summary
Objective: to describe the first performance test on Romosinuano (ROMO) and Blanco-Orejinegro (BON) bullocks held at the Nus Experiment Station in northeastern Antioquia (Colombia). Methods: a total of 15 commercial farms participated in the evaluation. The animals were tested under rotational grazing with three planes of nutrition and weighed every 28 days. The measured traits were daily gain, adjusted weight to 540 days, scrotal circumference, morphometric measurements at the end of the test, and carcass traits by ultrasound. Results: a “bull index” was obtained using these characteristics to select the four most outstanding bulls of each breed. Weight gain for the best Blanco-Oreginegro and Romosinuano bulls was higher than 1,000 and 890 g / animal / day, respectively. In addition, their final weight was greater than 340 kg. Animals were genotyped for variants of genes coding for carcass quality and meat, such as calpain (Capn), myostatin (MYO) and diacylglycerol acyltransferase (DGAT1). Conclusions: all Romosinuano individuals had desirable genotype for the CAPN 316 marker, which is associated with increased meat tenderness. On the other hand, Blanco- Orejinegro animals had the desirable genotype for the DGAT1 gene variant, related to fat deposition and fat content in milk. This is the first study that has been reported to select outstanding bulls in Colombian creole cattle breeds to facilitate the evaluation and use of superior genetic material.
Key words: bovine, genetic, growth, performance test.
Resumen
Objetivo: el presente trabajo tiene por objeto describir los resultados obtenidos en la primera prueba de desempeño de toretes de las razas bovinas criollas Romosinuano (ROMO) y Blanco Orejinegro (BON), realizada en la Estación Experimental el Nus, en el Nordeste Antioqueño, con la participación de 15 ganaderías comerciales. Métodos: los animales fueron mantenidos en pastoreo rotacional, con tres diferentes planos nutricionales a lo largo de la prueba. Se realizaron pesajes cada 28 días y se evaluó la ganancia diaria de peso, el peso ajustado a los 540 días, la circunferencia escrotal, medidas morfométricas de los animales al final de la prueba, y características de la canal medida por ultrasonido. Resultados: a partir de estas características se definió un índice de toro, para seleccionar los animales sobresalientes (cuatro toretes por cada raza), dichos toros superiores presentaron valores de ganancia de peso en la prueba de desempeño superiores a los 1000 gramos animal día en la raza Blanco Oreginegro y 890 gramos animal día en la raza Romosinuano, además presentaron un peso final superior a los 340 kg. Adicionalmente, los animales fueron genotipados para variantes de genes que codifican para Calpaina (CAPN), Miostatina (MYO) y Diacilglicerol Aciltransferesa (DGAT1) relacionados con la calidad de la canal y la carne. Conclusiones: se encontró que todos los individuos de la raza Romosinuano presentaron el genotipo deseable para el marcador CAPN 316, relacionado con mayor terneza de la carne, por otro lado los animales de la raza Blanco Orejinegro presentaron el genotipo deseable para la variante del gen DGAT1, relacionado con deposición grasa y contenido de grasa en la leche. Este es el primer trabajo que se realiza para seleccionar toros sobresalientes en las razas criollas colombianas y permitirá la evaluación y uso de material genético de calidad superior.
]]> Palabras clave: bovinos, crecimiento, genética, pruebas de desempeño
Resumo
Objetivo: este trabalho tem por objetivo descrever os resultados obtidos no primeiro teste de desempenho de touros jovens das raças crioulas Blanco Orejinegro (BON) e Romosinuano (ROMO), realizada na estação experimental El Nus, localizada no nordeste do departamento de Antioquia. Métodos: o teste teve a participação de 15 fazendas de produtores comerciais. Os animais foram mantidos em pastagem rotacional com três diferentes planos nutricionais ao longo do teste. Realizaram-se pesagens a cada 28 dias e avaliou-se o ganho diário de peso, o peso ajustado aos 540 dias, a circunferência escrotal, medidas morfométricas dos animais ao final do teste, e características da carcaça medidas por ultra-som. A partir destas características definiou-se um índice de touro, para selecionar os bois destacados (quatro touros novos por cada raça). Resultados: os touros superiores apresentaram ganhos de peso no teste de desempenho acima de 1000 gramas por cada animal ao dia na raça Blanco Orejinegro e 890 gramas na raça Romosinuano, além disto, apresentaram um peso final superior aos 340 kg. Adicionalmente, os animais foram genotipados para as variantes genéticas que codificam para a Calpaina (CAPN), miostatina (MYO), e Diacilglicerol Aciltransferase (DGAT1) relacionados com a qualidade da carcaça e da carne. Conclusões: encontrou-se que todos os indivíduos da raça Romosinuano apresentaram o genótipo desejável para o marcador CAPN316, relacionado com maior maciez da carne. De outro lado, os animas da raça Blanco Orejinegro apresentaram o genótipo desejável para a variante do gene DGAT1, relacionado coma deposição de gordura e o conteúdo de gordura no leite. Esta é a primeira pesquisa que se realiza para selecionar touros destacados nas raças crioulas colombianas e permitirá a avaliação e o uso de material genético de qualidade superior.
Palavras chave: bovinos, genética, teste de desempenho.
§ Para citar este artículo: Martínez RA, Quiceno J, Gallego JL, Mateus H, Rodríguez O, Medina P, Ballesteros H. Desempeño de toretes de las razas criollas Blanco Orejinegro y Romosinuano en prueba de crecimiento en pastoreo. Rev Colomb Cienc Pecu 2012; 25:36-45
* Autor para correspondencia: Rodrigo Alfredo Martínez Sarmiento. Centro de Investigaciones Tibaitat·, Km. 14 vía Mosquera, CORPOICA. Colombia. E-mail: ramartinez@corpoica.org.co
Introducción
Hace más de seis décadas Knapp y Baker (1943) reportaron la necesidad de realizar pruebas de desempeño en ganado bovino, con el objeto de definir las características que mejor describan el desempeño en ganado de carne, y en su momento dos medidas de eficiencia fueron priorizadas: la eficiencia alimenticia total y la eficiencia alimenticia neta, pero posteriormente Hazel en 1951 describió por primera vez el uso de índices de selección en ganado de carne, que permitió el mejoramiento simultáneo de varias características que podrían diferir en variabilidad, heredabilidad, importancia económica y la correlación entre el genotipo y fenotipo (Hazel et al., 1994).
]]> En Latinoamérica son reducidas las experiencias en el desarrollo de pruebas de desempeño en ganado de carne, una de ellas es la realizada por el Instituto Nacional de Tecnología Agropecuaria INTA, localizado en Barcarcel, Argentina; en esta prueba participan anualmente toros de las razas Angus, Criollos y Hereford. Los reproductores ingresan a una edad cercana a los 12 meses, con un peso que varía entre 381 y 427 kg, los animales se clasifican por su respuesta a diferentes características, mediante un índice de desempeño (Melucci et al., 2008).Por otra parte, las pruebas de ganancia de peso realizadas por la Asociación Brasilera de Criadores de ganado ceb˙ (Josahkian y Cavallari, 2003), eval˙an la ganancia de peso en animales con edades que varían entre los 7 y 10 meses y se basan en un índice que da un valor de 40% a la característica de ganancia media diaria, 40% al peso ajustado a los 550 días y 20% al tipo productivo. En este caso los animales son clasificados en cuatro categorías, elite, superior, regular e inferior. En Colombia, son escasas las experiencias de evaluación del desempeño de toros en prueba, y actualmente no existe un esquema de mejoramiento que aplique pruebas de desempeño y pruebas de progenie para la selección de animales élite para proveer al mercado con material genético probado de origen nacional.
Por lo anterior, el objetivo del presente trabajo es la evaluación de desempeño de toretes de las razas Romosinuano y Blanco Orejinegro mediante el diseño y aplicación de un índice de selección que incluye características de crecimiento, reproducción, desarrollo corporal, eficiencia alimenticia y caracteres de la canal evaluada por ultrasonido, que permita seleccionar toros de alto mérito genético.
Materiales y métodos
Esta prueba dedesempeñoen crecimiento se realizó en la Estación Experimental El Nus, de CORPOICA, localizada en el Municipio de San Roque, Antioquia. Se utilizaron toretes de las razas criollas Blanco Orejinegro (BON) (n=20) (Tabla 1) y Romosinuano (n=16) (Tabla 2), pertenecientes a 15 ganaderías comerciales asociadas a ASOCRIOLLO, o participantes en el Plan de Fomento de Razas Criollas, desarrollado por CORPOICA, ICA y Ministerio de Agricultura y Desarrollo Rural. Se seleccionaron animales de acuerdo a su desarrollo corporal, peso, conformación y la edad de inicio, que varió entre los 10 y los 13 meses. Los animales estuvieron en praderas compuestas de B. decumbens, Braquipara (B. plantaguinea) y estrella (Cynodon nefluensis)y todas las franjas presentaron leguminosas en especial de los géneros Desmodium y maní forrajero (Arachis pintoi). Los animales fueron mantenidos en pastoreo rotacional racional, con suplementación. La prueba se realizó durante 221 días, de los cuales, los primeros 56 días estuvieron en un sistema de pastoreo no suplementado (época de adaptación), durante los siguientes 165 días, los animales fueron sometidos a tres fases de pastoreo suplementado: con acceso libre al suplemento, controlado por grupos de seis animales por comedero (asignados al azar y controlados para evitar competencia por el lugar de alimentación) y controlado individual (asignando animal por comedero, para determinar consumo individual). La suplementación consistió en el suministro de una ración que contenía un 12% de proteína cruda y 2.85 megacalorías de energía metabolizable y constituído por maíz molido, soya extruida y melaza. Además se ofreció un suministro a voluntad de sal mineral (6% de fósforo) y durante este tiempo se proporcionó un manejo sanitario de acuerdo a los requerimientos de la zona.
Cada una de las características evaluadas fueron expresadas en forma estandarizada, como ha sido presentado por Melucci et al. (2008) y descrito por Hazel et al. (1994). La estandarización consiste en transformar los valores reales de las variables a valores comparables entre caracteres, y este valor corresponde a la diferencia entre el valor individual del carácter menos el promedio del grupo, dividido en el desvío estándar del carácter. Esta transformación se realizó con el fin de cuantificar y ajustar la variación de cada carácter, haciendo comparables estas características, por estar expresados en términos de desviación estándar con respecto al promedio. Este procedimiento permite entonces comparar el desempeño relativo de un animal para dos o más variables expresadas en distintas unidades y con distinta variabilidad, al ser estandarizadas todas estarían expresadas en términos de desviaciones estándar.
Los criterios de evaluación utilizados en esta prueba de desempeño incluyeron:
1. La ganancia de peso evaluado a diferentes intervalos y el peso total ganado en la prueba: los animales fueron pesados cada 28 días (potrero a báscula), a partir de la entrada de los animales y hasta los 221 días, para un total de 8 períodos.
2. Peso ajustado a los 540 días: que indica el aumento de peso bajo las condiciones de la prueba y el peso de todos los animales a una edad estándar.
3. La circunferencia escrotal es un carácter relacionado con la capacidad reproductiva del toro y también relacionado con la eficiencia reproductiva de su descendencia. Fue medida al final de la prueba.
4. Características de desarrollo corporal: indican el tamaño, conformación y simetría del animal, en este caso se evaluaron la alzada a la grupa, la altura al anca y la longitud corporal. Estas características se registraron al final de la prueba.
5. Eficiencia alimenticia: fue evaluada mediante una prueba de desafío nutricional realizada durante 23 días de alimentación con suplemento avoluntad, (2.85megacaloríasde energía metabolizable y 12% de proteína). El alimento fue suministrado sin exceder el 30% de la materia seca total consumida. La eficiencia alimenticia fue calculada por el cociente entre el consumo individual de alimento y la ganancia de peso durante el periodo de medición (el peso del suplemento consumido por individuo fue adicionado con una cantidad estimada del consumo de materia seca en función del peso vivo del animal).
6. Caracteres relacionados con la calidad de la canal: estascaracterísticas fueronevaluadas mediante medición ultrasonográfica y tomadas al final de la prueba. Se cuantificó el espesor de grasa subcutánea en la región dorsal, y el área de ojo del lomo de acuerdo a estándares establecidos por ICAR (2008), Estas características están relacionadas con el área total del longisimus dorsi y el contenido de grasa de la canal.
Para cada una de estas características se realizó una ponderación por su importancia económica relativa, para la construcción de un índice de desempeño de los toros (IT). Los valores de ponderación fueron ajustados para las siguientes variables: Ganancia media diaria (GMD), el peso ajustado a los 540 días (PAJ540), circunferencia escrotal(CE),eltamaño(TM)(representado por altura a la cruz [0.05], longitud [0.05], y altura a la cadera [0.05]), cociente para eficiencia alimenticia (EA)(característica que relaciona la ganancia de peso por cada kg de peso de alimento consumido en la prueba de eficiencia alimenticia), y las características de la canal (espesor de grasa [0.09] y área de ojo del lomo [0.09]) (CC). No se incluyeron dentro del cálculo del índice los valores de heredabilidades y correlaciones genéticas, debido a que no se dispone de tal información. Para el cálculo del índice las características fueron tomadas como variables estandarizadas y este incluyó:
IT= GMD(0.3)+PAJ540(0.1)+CE(0.22)+TM(0.15)+ EA(0.05)+CC(0.18)
Genotipificación para marcadores tipo SNP
Se realizó genotipificación para cuatro marcadores tipo SNP (Polimorfismo de Nucleótido Simple) localizados en tres genes: CALPAINA, (Barendse et al.,2008),variantedenominada CAPN316, como fue descrito por White et al. (2005), Smith et al. (2009), Page et al.(2002), Page et al. (2004) y la variante CAPN530, descrito por Casas et al. (2005) y Page et al. (2004). Una tercera variante SNP fue localizada el gen de la Miostatina descrita por Kambadur et al. (1997). Por ˙ltimo se genotiparon los animales para la variante SNP localizada en el gen Diacilglicerol Aciltransferasa como fue descrito por Pannier et al. (2010). Todos los marcadores fueron genotipados utilizando la metodología SSCP (Polimorfismo Conformacional deCadenaSencilla),comofuedescritopor Martínez et al. (2008).
Análisis estadístico
Como se mencionó, las características fueron ajustadas por edad mediante análisis de covarianza, los pesos y ganancias de peso se evaluaron por un análisis de modelos mixtos con medidas repetidas con una estructura de (co)varianzas autoregresiva1, para esto se utilizó el procedimiento MIXED del programa estadístico SAS, el modelo incluyó como efecto fijo la raza y como efecto aleatorio el animal, por ˙ltimo se utilizó como covariable la edad del animal.
Resultados
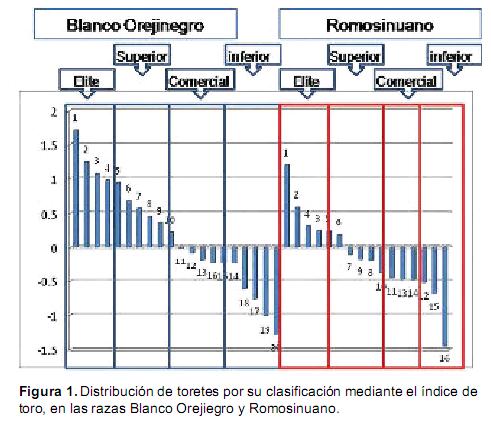
En este trabajo, las características son presentadas en unidades originales y variables estandarizadas, las cuales se presentan como desviaciones por encima y debajo del promedio. Los datos de desempeño son además presentados por raza, organizados de mayor a menor. Los animales sobresalientes son identificados como élite, animales que posteriormente serán utilizados para multiplicación y mejoramiento mediante inseminación artificial.
]]> Índice dedesempeñoEnprimerlugar,se presentalosvalores obtenidos por cada animal para el índice, lo que permitió clasificar los animales de mayor a menor desempeño y así se clasificaron con los n˙meros 1 a 4, los animales élite en cada raza. Como se puede ver, en la raza Blanco Orejinegro, aproximadamente el 50% de los animales se encuentran por encima del promedio, a diferencia de la raza Romosinuano, donde aproximadamente el 40% de los animales se encontraron por encima del promedio, lo que indica que la raza BON presentó mejor desempeño (Figura 1).
Para la ganancia media diaria en los animales élite de la raza BON se encontró un valor que varió entre 650 y 833 gramos animal día, con un desempeño superior al presentado en la raza Romosinuano, donde los animales superiores variaron entre 499 y 711 gramos animal día, a lo largo de la prueba. Es de resaltar que los animales clasificados por el índice entre los primeros cinco animales superiores, también quedaron ubicados entre los primeros lugares para este carácter, debido a su alto valor de ponderación en el índice (Figura 2).
La evaluación de la eficiencia alimenticia en la prueba de desafío nutricional, presentó un desempeño similar entre razas con valores de 745.6 ± 247 g/animal/día en la raza BON y 744 ± 317 g/ animal/ día en la raza Romosinuano, que presentó la mayor variación. Los animales de la raza BON que se encuentran con desempeño superior en el índice, también presentan un mejor desempeño que el resto de los animales de la raza, pero en la raza Romosinuano estos animales se distribuyeron entre diferentes lugares alrededor del promedio, esto puede ser debido a que algunos animales cuando fueron suplementados a voluntad, presentaron mayor desempeño, posiblemente por mayor capacidad de conversión y apetito que les permite consumir más alimento, en comparación con otros animales.
En cuanto al peso ajustado a los 540 días, se presenta un promedio de peso de 285 ± 43.11 kg en la raza BON y de 259 ± 35.73 kg en la raza Romosinuano, en este caso, los animales con los mayores desempeños presentaron valores que variaron entre 310 y 374 kg en la raza BON y con un menor valor en la raza Romosinuano, que varió entre 275 y 314 kg. Además se encontró que los animales clasificados en los primeros cuatro lugares en cada raza siempre presentaron valores superiores al promedio (Figura 3).
La circunferencia escrotal también presentó mayores valores en la raza BON (28.5 ± 3.24 cm) comparado con la raza Romosinuano (26.75 ± 3.21 cm), pero esta característica en la raza BON presentó valores que variaron entre 32 y 34 cm, comportamiento superior de la raza Romosinuano, que presentó valores entre 29 y 32 cm, pero en ambos casos, los animales clasificados en los primeros lugares del índice también se presentaron el mejor desempeño en ambas razas (Figura 4).
]]> En cuanto a característicasde desarrollo corporal, se evaluaron diferentes medidas: altura a la cadera, altura a la cruz y longitud total. En este caso, los animales de la raza BON presentaron un mayor desarrollo y talla, pues se registraron valores de altura a la cadera de 118 ± 6.6 cm y de 115 ± 4.31 cm en la raza Romosinuano. En esta ˙ltima raza, no siempre los animales más pesados y de mejor crecimiento, fueron los animales más altos y de mayor talla, por lo que muchos de estos animales no se presentan entre los primeros lugares; además en esta raza, la variación del carácter es inferior al 5%, por lo que las diferencias entre los animales superiores e inferiores es reducida. Igual situación se encontró en la característica longitud del cuerpo, que presentó valores cercanos a los 110 ± 6.5 cm en la raza BON y 106 ± 4.7 en la raza Romosinuano. Igualmente, en esta característica la variación estuvo cercana al 5%, razón por la cual la diferencia entre animales fue muy baja. En este caso los animales establecidos en los primeros puestos en el índice se encuentran cercanos al promedio (Figura 4).En la evaluación de área de ojo de lomo determinadopor medio de ultrasonografía, se presentó un valor promedio similar entre razas con un valor cercano a los 30 cm2, en este caso se presentó valores más altos en la raza Romosinuano, pero sin diferencias significativas (p>0.05), además se presentó una mayor variación en la raza BON con un desvío estándar de 7.96 cm2, comparado con la raza Romosinuano, con un desvío estándar de 4.94 cm2. Como se puede ver, los animales clasificados en los primeros lugares en la raza BON también presentan los mayores valores para esta característica, con excepción del animal n˙mero 4, que se encuentra en el séptimo lugar. En la raza Romosinuano, los animales superiores se situaron en diferentes lugares por encima del promedio con excepción del animal 4 que se presentó levemente por debajo del promedio, debido a que es el animal que presenta la menor edad (Figura 5).
El espesor de grasa dorsal también evaluado por ultrasonografía, presentó valores mayores en la raza Romosinuano con 2.81 ± 0.40 mm en comparación con la raza BON, con un valor de 2.58 ± 0.40 mm, pero sin diferencias significativas (p>0.05). Los animales superiores en el índice fueron los que siempre presentaron los mayores comportamientos en la raza BON. Al contrario, en el caso de la raza Romosinuano, se presenta una distribución de los animales superiores alrededor del promedio (Figura 5).
En cuanto a la Genotipificación de los toretes que presentaron un comportamiento superior, se encontró para el marcador Capn316 predominancia del genotipo heterocigoto (CG), con excepción del toro de la ganadería La Esmeralda, el cual fue homocigoto para el alelo (CC). En el marcador Capn530, todos los toros presentaron genotipo heterocigoto (AG) y para el marcador DGAT1 igualmente todos los toros presentaron el genotipo homocigoto AA con excepción del toro de la ganadería La Esmeralda, que presentó genotipo hetercigoto (AK). Finalmente, para el marcador de la miostatina se presenta un genotipo heterocigoto (AC) para todos los toros superiores.
Discusión
Una parte importante de la selección de los toretes en pruebas de desempeño actualmente es la información para genes relacionados con características de importancia económica, por lo que se realizó la genotipificación para cuatro marcadores localizados en tres genes relacionados con crecimiento y calidad de la carne. El primero corresponde al gen de la Calpaina, que se ha encontrado relacionado con la terneza ó resistencia al corte de la carne (Barendse et al., 2008), para este gen el genotipo deseable corresponde a la condición homocigota CC, en el marcador Capn316 (White et al., 2005; Smith et al., 2009; Page et al., 2002; Page et al., 2004), los individuos evaluados presentaron principalmente un genotipo heterocigoto para este marcador. En el marcador CAPN530 ubicado en el mismo gen (Casas et al. 2005) se ha encontrado que el genotipo deseable es el alelo G (Page et al., 2004), aunque en este caso, algunos reportes indican que este ˙ltimo marcador es poco informativo (Casas et al., 2005), o tiene bajo efecto; para este marcador los animales evaluados presentaron genotipo heterocigoto.
El tercer marcador evaluado se ubica en el gen de la Miostatina formalmente conocida como factor 8 de crecimiento y diferenciación (Kambadur et al., 1997), este es un factor que limita el crecimiento del tejido muscular y está relacionado con el doble m˙sculo en bovinos (Grobet et al., 1997) y la hipertrofia muscular en varias especies y razas (Kambadur et al., 1997; Alexander et al., 2009), en este marcador se ha encontrado que el alelo A puede estar asociado con mayor desarrollo muscular y rendimiento en carne al sacrificio (Bellinge et al., 2005; Alexander et al., 2009), para este marcador los animales evaluados presentaron también genotipo heterocigoto, por lo que son portadores del alelo deseable. Por ˙ltimo el gen denominado Diacilglicerol Aciltransferasa codifica para una enzima relacionada con la síntesis de triacil glicerol (Pannier et al., 2010) y ha sido encontrado relacionado con contenido de grasa en la leche y el contenido de grasa intramuscular específicamente, donde el alelo K presenta asociación con mayor contenido de grasa en la leche, pero menos proteína (Grisart et al., 2004; Naslund et al., 2008), probablemente debido a mayor producción de triglicéridos, y se ha observado efecto del mismo alelo sobre la deposición de grasa intramuscular en Holstein y Charolais (Thaller et al., 2003) pero no se encontró asociación entre este polimorfismo y características de composición de la canal en la raza Brahman (Casas et al., 2005) además, reportes más recientes indican que esta asociación debe ser revisada (Pannier et al., 2010). En este caso, la mayoría de los animales no presentaron el genotipo deseable y sólo un individuo presentó genotipo heterocigoto. Pero seg˙n Demeter et al. (2009) los animales con genotipo AA podrían ser más deseables con respecto a la calidad nutricional de sus productos (menor grasa pero mayor proteína) y por presentar mejor comportamiento reproductivo.
Selección de toretes de mayor desempeño
]]> Con la información de crecimiento, todos los animales se clasificaron y aquellos que presentaron mayor valor para el índice son descritos en este apartado. En las tablas 1 y 2 se hace una descripción del origen y ubicación de las ganaderías propietarias de los toretes élite en las razas Blanco Orejinegro y Romosinuano, respectivamente.En la raza Blanco Orejinegro, los primeros cuatro animales presentaron desempeño sobresaliente, con una ganancia diaria promedio que varió entre 678 y 873 gramos animal día. En la prueba de eficiencia alimenticia también presentaron excelente desempeño, con un incremento diario promedio entre 870 y 1.174 gramos animal día. En estos animales, las medidas morfométricas indican que están por encima del promedio de la talla de la población.
Para la raza Romosinuano, en términos generales estos animales presentaron un desempeño levemente inferior para algunas características, comparado con la raza Blanco Orejinegro, en este caso, los pesos al inicio de la prueba variaron entre 136 y 221 kg, y alcanzaron un peso final que varió entre 297 y 355 kg, lo cual corresponde a una ganancia diaria promedio que varió entre 500 y 683 gramos animal día. En la prueba de eficiencia se presentó en esta raza el animal con el mejor desempeño, con un valor promedio de ganancia de peso de 1.217 gramos animal día, pero los demás animalespresentaronvaloresinferioresalos presentados en la raza Blanco Orejinegro.
En conclusión, a partir de este trabajo se seleccionaron 8 toros élite jóvenes (cuatro decadaraza) de las razas Romosinuano y Blanco Orejinegro que serán utilizados para criopreservación de semen y uso para prueba de progenie. En términos generales se encontró mejor desempeño de los animales de la raza Blanco Orejinegro, con excepción de las características de la canal, donde se presentó mayores valores en la raza Romosinuano aunque con mayor variación.
Con la estructura y los procedimientos de manejo utilizados para esta prueba se va a tener la oportunidad de seleccionar animales que puedan asegurar un progreso genético predecible en las razas criollas, y de esta forma poder obtener una población adaptada al trópico y con parámetros de crecimiento mejorados. Los productores de ganado criollo, son los principales beneficiarios del progreso genético y por tanto deben contribuir con el desarrollo de este tipo de evaluaciones que aportarán al mejoramiento de la productividad de la ganadería nacional.
Agradecimientos
Los autores expresan sus agradecimientos al Ministerio de Agricultura y Desarrollo Rural, por la financiación del proyecto 2007H7488-683. A los productores de Ganado Criollo y a la asociación de Criadores de ganado criollo, por su aporte al desarrollo de este trabajo.
]]> Referencias
1. Alexander LJ, Kuehn LA, Smith TP, Matukumalli LK, Mote B, Koltes JE, Reecy J, Geary TW, Rule DC, Macneil MD. A Limousin specific myostatin allele affects longissimus muscle area and fatty acid profiles in a Wagyu-Limousin F2 population. J Anim Sci 2009; 87:1576-1581. [ Links ]
2. Barendse W, Harrison BE, Bunch RJ, Thomas MB. Variation at the Calpain 3 gene is associated with meat tenderness in zebu and composite breeds of cattle. BMC Genet 2008; 9:41. [ Links ]
3. Bellinge RH, Liberles DA, Laschi SP, Oíbrien PA, Tay GK. Myostatin and its implications on animal breeding: a review. Anim Genet 2005; 36:1-6. [ Links ]
4. Casas E, White SN, Riley DG, Smith TPL, Brenneman RA, Olson TA, Johnson DD, Coleman SW, Bennett GL, Chase CC. Assessment of single nucleotide polymorphisms in genes residing on chromosomes 14 and 29 for association with carcass composition traits in Bos indicus cattle. J Anim Sci 2005; 83:13-19. [ Links ]
5. Demeter RM, Schopen GCB, Oude Lansink JM, Meuwissen MCM, Van arendonk J. Effects of milk fat composition, DGAT1, and SCD1 on fertility traits in Dutch Holstein cattle J Dairy Sci 2009; 92:5720-5729. [ Links ]
6. Grisart, B, Farnir F, Karim L, Cambisano N, Kim JJ, Kvasz A, Mni M, Simon P, Frere J, Coppieters W, Georges M. Genetic and functional confirmation of the causality of the DGAT1 K232A quantitative trait nucleotide in affecting milk yield and composition. Proc Natl Acad Sci 2004; 101:2398-2403. [ Links ]
7. Grobet L, Martin LJ, Poncelet D, Pirottin D, Brouwers B, Riquet J, Schoeberlein A, Dunner S, Ménissier F, Massabanda J, Fries R, Hanset R, Georges M. A deletion in the bovine myostatin gene causes the double-muscled phenotype in cattle. Nat Genet 1997; 17:71-74. [ Links ]
8. Hazel LN. Construction and use of selection indexes in beef cattle. in Annu. Rep. NC-1 Reg. Coop. Res. Project Improvement of Beef Cattle Through Breeding. Univ. Nebraska, Lincoln. 1951. p.34. [ Links ]
9. Hazel LN, Dikerson GE, Freeman AE. Symposium: selection index theory ñ Selection index, then, now and for the future. J Dairy Sci 1994;77:3236-3251. [ Links ]
10. InternationalCommitteeforAnimalRecording(ICAR), International Agreement of Recording Practices. Section 3. - ICAR rules, standards and guidelines for meat Production recording. Approved by the General Assembly held in Niagara Falls, USA, on 18 June 2008 .p.91-100. [ Links ]
11. Josahkian L, Cavallari C. Regulamento da prova de ganho em peso confinamento. Programa de melhoramento genético de zebuínos. Ministério da Agricultura, Pecuária e Abastecimento. 2003; 17. [ Links ]
12. Kambadur R, Sharma M, Smith TP, Bass JJ. Mutations in myostatin(GDF8) indouble-muscledBelgianBlueand Piedmontese cattle. Genome Res. 1997; 7:910-916. [ Links ]
13. Knapp B, Baker AL. Limited vs. Full-Feeding in Record of Performance Tests for Beef Cattle. J Anim Sci 1943; 2:321-327. [ Links ]
14. Martínez R, Dunner S, Barrera G, Cañon J. Novel variants within the coding regions of the Slc11A1 gene identified in Bos taurusand Bos indicus breeds. J Anim Breed Genet 2008; 125:57-62. [ Links ]
15. Melucci L, Villareal R, Mezadra C, Melluci G. XV Prueba de comportamiento de toros a campo. Unidad Integrada Balcarce. Fac Ciencias Agrarias (UNMDP) - EEA (INTA) Balcarce, Argentina. Grupo de Genética Zootécnica. 2008. p.30. [ Links ]
16. Naslund J, Fikse WF, Pielberg GR, Lunden A. Frequency and effect of the bovine acyl-CoA:diacylglycerol acyltransferase 1 (DGAT1) K232A polymorphism in Swedish dairy cattle. J Dairy Sci 2008; 91:2127-2134. [ Links ]
17. Page BT, Casas E, Heaton MP, Cullen NG. Evaluation of single-nucleotide polymorphisms in CAPN1 for association with meat tenderness in cattle. J Anim Sci 2002; 80:3077-3085. [ Links ]
18. Page BT, Casas E, Quaas RL, Thallman RM, Wheeler TL, Shackelford SD, Koohmaraie M, White SN, Bennett GL, Keele JW, Dikeman ME, Smith TP. Association of markers in the bovine CAPN1 gene with meat tenderness in large crossbred populations that sample influential industry sires. J Anim Sci 2004; 82:3474-3481. [ Links ]
19. Pannier L, Mullen AM, Hamill RM, Stapleton PC, Sweeney T. Association analysis of single nucleotide polymorphisms in DGAT1, TG and FABP4 genes and intramuscular fat in crossbred Bos tauruscattle. Meat Sci 2010; 85:515-518. [ Links ]
20. Smith T, Thomas MG, Bidner TD, Paschal JC, Franke DE. Single nucleotide polymorphisms in Brahman steers and their association with carcass and tenderness traits. Genet Mol Res 2009; 8:39-46. [ Links ]
21. Thaller G, Kühn C, Winter A, Ewald G, Bellmann O, Wegner J, Zühlke H, Fries R. DGAT1, a new positional and functional candidate gene for intramuscular fat deposition in cattle. Anim Genet 2003; 34:354-357. [ Links ]
22. White SN, Casas E, Wheeler TL, Shackelford SD, Koohmaraie M, Riley DG, Chase CC, Johnson DD, Keele JW, SmithTPL. A new single nucleotide polymorphism in CAPN1 extends the current tenderness marker test to include cattle of Bos indicus, Bos taurus, and crossbred descent. J Anim Sci 2005; 83:2001. [ Links ] ]]>