
]]>
REC.: MARZO 08/07. ACEPT.: JULIO 25/07RESUMEN
Se evaluaron 53 individuos de patos Muscovy de los departamentos de Caldas, Risaralda, Antioquia y Valle del Cauca con tres cebadores RAMs. Se generaron 71 loci polimórficos (61.2%) con 0.19 de heterocigosidad. El cebador con mayor heterocigosidad fue CGA (0.23) y CA el de mayor loci polimórfico (76.1%). La técnica RAMs permitió diferenciar los géneros Anas y Cairina a un índice de similitud de 0.83. Con un índice de similitud del 0.894, los patos Muscovy formaron cinco grupos. El mejor cebador para diferenciar especies fue CCA (Fst= 0.274). La diferenciación genética en la muestra poblacional fue moderada (Fst= 0.2045).
Palabras clave: Cairina moschata; Pato Muscovy; RAMs.
ABSTRACT
53 individuals of Muscovy ducks from Caldas, Risaralda, Antioquia and Valle del Cauca departments with three primers RAMs were evaluated. 71 polymorphic loci (61,2%) were generated with 0.19 of heterocigozity. The primer with the highest heterocigozity was CGA (0.23) and CA had the highest polymorphic loci (76.1%). The RAMs technique allowed to discriminate Anas and Cairina genus with an index of similarity of 0.83. At a 0.894 of similarity index, the Muscovy ducks formed 5 groups. The best primer to discriminate species was CCA (Fst= 0.274). The genetic differentiation was moderate (Fst= 0.2045).
Key-word: Cairina moschata, Muscovy ducks, RAMs
El pato Pekín (Anas platylirrhynchos) es el utilizado para producción de carne pero en Francia entre 80- 90% es reemplazado por pato Muscovy y Mula (macho Muscovy por hembra Pekín) por mayor productividad y exigencias del mercado (López y Ospina, 2000).
La mayoría de las investigaciones en el país sobre patos se han realizado en linajes modernos, seleccionados comercialmente e importados, que han perdido habilidades naturales como la capacidad de reproducirse en condiciones naturales (cloquera) (Segura y Montes, 2001). Los núcleos de patos comunes se encuentran dispersos en todo el país, no se han caracterizado genéticamente y es posible que en alto porcentaje se encuentren cruzados o absorbidos por los linajes comerciales.
Los marcadores moleculares se han utilizado para la identificación genealógica, para la caracterización de distancias genéticas entre razas y para ayudar a comprender características de producción como de adaptación (Delgado et al., 2001). En el Laboratorio de Biología Molecular de la Universidad Nacional de Colombia sede Palmira se han desarrollado investigaciones utilizando la técnica RAMs con diversas especies animales, entre ellas bovinos criollos, como ganado Hartón del Valle (Piedrahíta, 2003), cerdos criollos (Oslinger et al., 2006) y otras especies animales (álvarez et al., 2005).
El objetivo principal del presente trabajo fue evaluar la diversidad genética utilizando marcadores moleculares RAMs y con técnicas multivariadas establecer la relación entre grupo genético y origen geográfico del pato criollo Cairina moschata L.
Los patos obtenidos para el estudio provinieron de granjas de cuatro departamentos: Antioquia (4 individuos), Caldas (10 individuos), Risaralda (9 individuos) y Valle (30 individuos), los cuales se encuentran en la Granja Mario González Aranda de la Universidad Nacional de Colombia Sede Palmira (1.001 msnm, 23°C).
Las muestras de ADN se extrajeron de 0.2 ml de sangre mediante punción en la vena humeral, utilizando el protocolo de extracción de Salting Out (Oslinger et al., 2006). La concentración de ADN se determinó por comparación con ADN del bacteriófago lambda, a concentraciones conocidas y visualizándose a través de un gel de agarosa al 0.8% teñido con bromuro de etidio en una cámara Maxicell Primo EC-340 Electroforesis Gel System. Las muestras de ADN se diluyeron a un volumen total de 100 µl a 10 ng.ul-1. Las muestras de ADN se evaluaron con tres cebadores RAMs (Tabla 1).
]]>
Para estandarizar las condiciones de PCR se evaluaron 10 individuos y se realizaron en un volumen total de 25 µl que contenían tampón de PCR 1X, 0.2mM de cada DNTP, 4µM de cebador, una unidad de Taq polimerasa, 20 ng de ADN y 2,5µM de MgCl2. La amplificación se llevó a cabo en un termociclador PTC 100 Programmable Termal Controller (MJ. Research, Inc). El perfil comprendió la desnaturalización inicial por 5 minutos a 95°C, seguido de 37 ciclos de 95°C por 30 segundos, 55-58°C por 30 segundos, 72°C por 2 minutos. Se realizó una extensión final a 72°C por 7 minutos. La temperatura de hibridación para los cebadores CT y CGA fue 58°C y para el cebador CCA fue 55°C.
Los productos amplificados por PCR se separaron mediante electroforesis utilizando una cámara de secuenciación (BIORAD Sequi-Gen Sequencing Cell) y geles de poliacrilamida al 4% (29:1 acrilamida bisacrilamida), en condiciones desnaturantes (urea 5M). Cada muestra (25 µl) se mezcló con 8 µl de buffer desnaturante (95% Formamida, 0.025% Azul de Bromofenol, 0.025% Xylene cyanol), se sometieron a 95°C durante 5 minutos y puestas en hielo inmediatamente. Se cargaron 5 µl de la mezcla y se corrió el gel a 120 Watts durante una hora. La tinción se realizó usando sales de plata.
La lectura de los geles se realizó con base en el criterio de Berg y Hamrick (1997), quienes consideran como locus polimórfico aquel en el cual el alelo más común tiene una frecuencia menor del 95%. Se creó una matriz de variables binarias de ceros y unos (ausencia o presencia). La similitud genética entre los individuos se calculó utilizando el coeficiente de similitud de Nei Li (Leung Nelson y Leach, 1993), también conocido como DICE (1945) (Sneath y Sokal, 1973). Se realizó un análisis de correspondencia múltiple y un dendrograma de haplotipos empleando el programa NTSYS (Numerical Taxonomy System for personal Computer, versión 2.02 PC). Para evaluar la diversidad genética se estimó el número de alelos polimórficos por locus, heterocigosidad y diferenciación poblacional (estadístico Fst) utilizando el programa TFPGA® (Tools for population genetic analysis versión 1.3, 1997).
Se hizo necesario realizar una dilución inicial de 1:20 ADN - agua (V/V) antes de cuantificar el ADN. Este se encuentra en el Laboratorio de Biología Molecular de la Universidad Nacional de Colombia sede Palmira y hace parte del primer banco de ADN de patos criollos colombianos. Entre seis cebadores RAMs (CA, CCA, CGA, GT, TG y CT) se eligieron los que presentaron mayor número de bandas polimórficas (CA, CCA, CGA). En conjunto generaron 116 patrones de bandas, distinguibles en un rango entre 80 y 1.200 pares de bases. El cebador con mayor número de bandas polimórficas fue CCA (Figura 1) y el menor CA (Tabla 2).
]]>


Se obtuvieron 5 loci con alelos raros (IPGRI Cornell University, 2004) con los cebadores CCA y CGA. La cantidad de bandas obtenidas utilizando tres cebadores RAMs visualizadas en geles de secuenciación pueden ser equivalentes a utilizar la técnica AFLP, que es costosa y requiere más tiempo para la implementación.
Las bandas presentes en el pato Muscovy y ausentes en Pekín y Chileno hicieron posible diferenciar especies. La técnica RAMS permitió identificar individuos con alelos poco frecuentes (alelos raros) que se sugiere conservar para mantener la diversidad en la población.
Se obtuvo una heterocigosidad de 0.19 para todos los cebadores y valores que oscilaron entre 0.16 y 0.23. La mayor heterocigosidad (He) fue para el cebador CGA (0.23), seguido por CA (0.18) y por último CCA (0.16). El porcentaje de loci polimórfico es uno de los indicadores del potencial de un marcador para evaluar diversidad. Al igual que para los valores de He, el cebador que obtuvo el mayor valor de loci polimórfico fue el CA (Tabla 3).
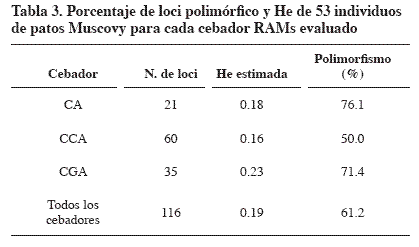
Aunque el cebador CA presentó el menor número de bandas fue el más polimórfico. El cebador de menor polimorfismo (CCA) presentó el mayor número de bandas. En animales genéticamente muy alejados se obtuvieron, con estos cebadores, valores de heterocigosidad diferentes; en bovinos criollos (Piedrahíta, 2003) y en cerdos criollos (Oslinger et al., 2003) encontraron valores de heterocigosidad más altos para el cebador CCA (0.30 y 0.22 respectivamente), mientras que para el cebador CGA el valor de heterocigosidad fue menor (0.22 y 0.19 respectivamente).
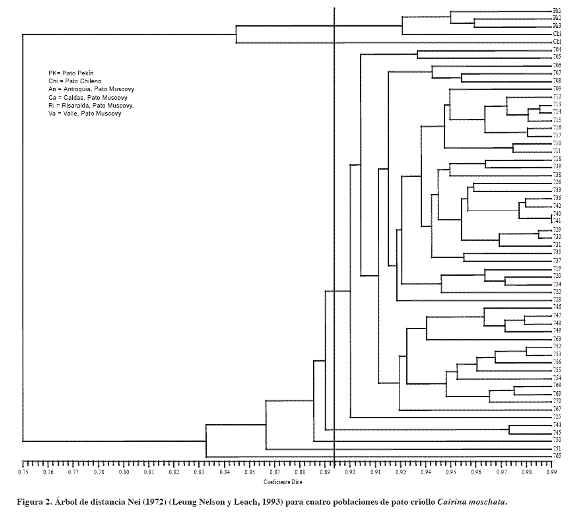
]]> En trabajos anteriores (Stai y Hughes, 2003) hallaron valores de He de 0.884 para individuos provenientes de Paraguay, Brasil y Estados Unidos. La He encontrada en este estudio (0.19) se puede explicar por el bajo número de individuos muestreados procedentes de zonas geográficas no muy alejadas.El dendrograma (Figura 2) permitió diferenciar entre géneros. A 83% de similitud se diferenciaron dos grupos; el primero, formado por los patos Pekín y Chilenos (utilizados para el análisis como punto de referencia), especies del género Anas, y el segundo grupo conformado por los patos Muscovy del género Cairina. Los patos Muscovy formaron cinco grupos a un índice de similitud de 0.894. Un grupo formado por individuos de todas las procedencias (Antioquia, Caldas, Risaralda y Valle) y los otros conformados por individuos del Valle del Cauca. Lo anterior indica posible flujo de genes, posibilitado por el transporte de individuos de un departamento a otro.
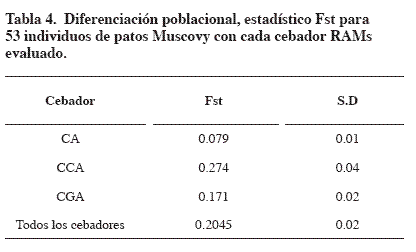
El mayor valor de Fst se consiguió con el cebador CCA (0.274) (Tabla 4), lo cual indica que este fue el mejor cebador para diferenciar entre especies. Para los tres cebadores el Fst fue de 0.2045, con una desviación estándar de 0.0249, que indica una moderada diferenciación genética (Wright, 1978). Stai y Hughes (2003) hallaron un valor de Fst = 0.24.
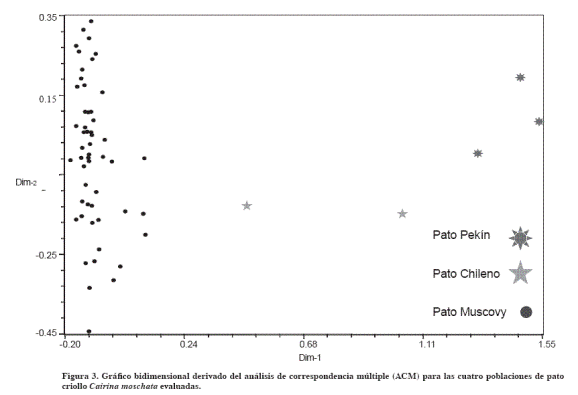
El análisis de correspondencia múltiple (Figura 3) separó la población en tres grupos correspondientes a patos Pekín, Chileno y Muscovy y confirmó la nula relación entre grupo genético y origen geográfico en el pato Muscovy.
A la Dirección de Investigación de la Universidad Nacional de Colombia sede Palmira (DIPAL) por la financiación del trabajo de grado de los zootecnistas D. Hernández y D. Muñoz a partir del cual se generó la información presentada en el artículo.
1. Álvarez, L. A.; Muñoz, J. E.; Posso A. M. 2005. Programa de investigación en utilización y conservación de recursos zoogenéticos. Universidad Nacional de Colombia, Palmira. 82 p. [ Links ]
2. Berg, E.; Hamrick, J. 1997. Quantification of genetic diversity at allozyme loci. Canad. J. Forest Res. 27:415-424. [ Links ]
3. Delgado J. V.; Barba. C.; Camacho, M. E.; Sereno. F. T. P. S.; Martínez. A.; Vega- Pla. J. L. 2001. Caracterización de los animales domésticos en España. Boletín de Información sobre Recursos Genéticos Animales. FAO. (Disponible en http://www.fao.org/dad-is/) 11-18-2006 [ Links ]
4. Ipgri Cornell University. 2004. Módulo de Aprendizaje sobre Marcadores Moleculares Cd-rom interactivo Vol. 1 y 2. [ Links ]
5. Johnsgard, A. P. 1980. Hybridazation in the Anatidas an its taxonomic implications. Condor. 62. 152. [ Links ]
6. Leung, H.; Nelson, R.; H.; Leach, J. E. 1993. Population structure of plant pathogenic fungi and bacteria. Adv. Plant Pathol. 10: 157-205. [ Links ]
7. López, A. M. Ospina, R. 2000. Caracterización biológica del eyaculado del pato Muscovy Cairina moschata L. Trabajo de Grado (Zootec). Universidad Nacional de Colombia. Palmira. 84 p. [ Links ]
8. Oslinger, A.; Muñoz J. E.; Álvarez L. A.; Moreno, F.; Posso A. 2006. Caracterización de cerdos criollos colombianos mediante la técnica molecular RAMs. Acta Agron. 55 (4) 45-50. [ Links ]
9. Piedrahíta, A. M. 2003. Caracterización molecular de ganado criollo Hartón del Valle mediante marcadores moleculares tipo RAM´s. Trabajo de Grado (Zootec). Universidad Nacional de Colombia. Palmira. 103 p. [ Links ]
10. Segura-Correa, J. C.; Montes-Pérez, R. C. 2001. Razones y estrategias para la conservación de los recursos genéticos animales (RGA). Rev. Biomed (U. Autónoma de Yucatán). Disponible en: http//www.uady.mx/~biomedic/rb011237.pdf. 11-18-2006 [ Links ]
11. Sneath, P. H.; Sokal, R. 1973. Numerical taxonomy: the principles and practice of numerical classification. San Francisco: W. H. Freeman; 573p. [ Links ]
12. Stai, S. M.; Hughes, C. R. 2003. Characterization of microsatellite loci in wild and domestic Muscovy ducks (Cairina moschata). Anim Genet. 34: 387. [ Links ]
13. Wright, S. 1978. Evolution and the genetics of populations, variability within and among natural populations. Vol 4. University of Chicago Press. 335 p. [ Links ] ]]>