Identificación molecular de micobacterias no tuberculosas mediante el análisis de los patrones de restricción, Colombia 1995-2005
Claudia Marcela Castro, Gloria Puerto, Luz Mary García, Dora Leticia Orjuela, Claudia Llerena Polo, María Consuelo Garzón, Wellman Ribón
Grupo de Micobacterias, Instituto Nacional de Salud, Bogotá, D. C., Colombia
Recibido: 22/03/07; aceptado: 25/06/07
Introducción.
Las micobacterias no tuberculosas pueden ser saprofitas, patógenas u oportunistas; las enfermedades más comunes producidas por estos microorganismos son las infecciones posquirúrgicas, principalmente por procedimiento estéticos, infecciones asociadas con catéteres, enfermedades cutáneas diseminadas, enfermedades pulmonares y del sistema nervioso central que afectan especialmente a pacientes infectados con el virus de la inmunodeficiencia humana. La identificación fenotípica de las micobacterias no tuberculosas incluye pruebas microbiológicas y bioquímicas, las cuales pueden tomar varias semanas y algunas veces no logran diferenciar entre los miembros de un complejo.Objetivo. El objetivo fue evaluar la metodología de reacción en cadena de la polimerasa-análisis de restricción, como método de identificación genotípica de micobacterias no tuberculosas aisladas de muestras clínicas que pertenecen a la colección del Instituto Nacional de Salud.
Materiales y métodos. Se estudiaron 70 aislamientos clínicos de micobacterias no tuberculosas, criopreservados en glicerol al 50% e identificados mediante metodologías fenotípicas. La identificación genotípica se realizó por reacción en cadena de la polimerasa-análisis de restricción y se evaluó la concordancia entre las metodologías.
Resultados. Se obtuvo una concordancia del 100% en la identificación de Mycobacterium terrae, M. szulgai, M. avium, M. chelonae y M. scrofulaceum, en las especies M. fortuitum, M. abscessus M. gordonae y M. intracellulare varió de 44% a 89%; no se obtuvo concordancia en la identificación de las especies M. flavescens y M. malmoense.
Conclusiones. El análisis de restricción es una alternativa para la identificación de especies de micobacterias no tuberculosas, rápida, económica y segura para la identificación, que permite la diferenciación entre especies de un complejo y la determinación del subtipo de cada especie.
]]> Palabras clave: infecciones atípicas por Mycobacterium, reacción en cadena de la polimerasa, técnicas de diagnóstico molecular, infecciones oportunistas, salud pública.Molecular Identification of non-tuberculous mycobacteria
Introduction. Nontuberculous mycobacteria can be saprophytic, pathogenic or opportunistic. The most common diseases produced by these microorganisms are the post-surgical infections due to anesthetic procedures, infections associated with catheters, disseminated cutaneous diseases and pulmonary and central nervous system diseases that especially affect HIV patients.
Identification of the nontuberculous mycobacteria can take several weeks and even then, differentiation of complex members is not possible.
Objective. The PCR-restriction analysis (PRA) technique was evaluated as a method for genotypic identification of nontuberculous mycobacteria isolated of clinical samples located in the culture collection of the Instituto Nacional de Salud (National Institute of Health), Bogotá, Colombia.
Materials and methods. Seventy clinical isolates of nontuberculous mycobacteria stored in 50% glycerol at -70°C were identified by phenotypic techniques. The genotypic identification was made using the PCR-restriction analysis (PRA) using the restriction enzymes BstEII and HseIII, the restriction products were visualized on gels of agarose to 3%, and the concordance between the methodologies was evaluated.
Results. A matching of 100% was obtained in the identification of Mycobacterium terrae, M. szulgai, M. avium, M. chelonae and M. scrofulaceum, the matching between M. fortuitum species, M. abscessus, M. gordonae and M. intracellulare varied from 44 to 89%; there was no concurrence in the identification of species M. flavescens and M. malmoense.
Conclusions. PRA provided a fast, inexpensive and accurate alternative for the identification of nontuberculous mycobacteria that permited the differentiation among species of a complex and determining the subtype of each species sample.
Key words: Mycobacterium infections, atypical, polymerase chain reaction, molecular diagnostic techniques, opportunistic infections, public health.
Las micobacterias no tuberculosas pueden ser saprofitas, patógenas u oportunistas; entre ellas se incluyen especies de rápido y de lento crecimiento (1). A diferencia de Mycobacterium tuberculosis y Mycobacterium leprae, éstas no son patógenos obligados, por lo cual su hábitat general es el medio ambiente (2). Se han encontrado en el agua, el suelo y la vegetación; sin embargo, algunas tienen la habilidad de infectar a los animales y al hombre, y poseen la capacidad de colonizar sus células (3).
]]> Las especies más comúnmente encontradas a nivel mundial son Mycobacterium avium, Mycobacterium fortuitum y Mycobacterium chelonae (3). Las enfermedades más comunes producidas por las micobacterias no tuberculosas se encuentran asociadas a infecciones posquirúrgicas, entre las que se describen los procedimientos estéticos, como mesoterapias y lipoesculturas, la aparición de abscesos después de una inyección, las infecciones asociadas con catéteres, las enferme-dades cutáneas diseminadas, la enfermedad pulmonar y las enfermedades del sistema nervioso central que afectan especialmente a los pacientes infectados con el virus de la inmunodeficiencia humana (VIH) y a los niños (4-6).En Colombia, se ha descrito una serie de casos de infecciones oportunistas y hospitalarias causados por este grupo de microorganismos (7-10). También, se han aislado micobacterias no tuberculosas en 5,3% a 28% de los pacientes infectados con el VIH (11-12). Las principales especies aisladas en estos pacientes son, en orden de importancia: el complejo M. avium-intracellulare, M. fortuitum, M. chelonae, M. gordonae y M. simiae (13). Sin embargo, no se conoce en el país la prevalencia de las enferme-dades causadas por estos microorganismos (7).
La identificación fenotípica de las micobacterias no tuberculosas incluye una serie de estudios microbiológicos y bioquímicos, los cuales pueden tomar varias semanas, son dispendiosos de realizar y algunas veces no logran diferenciar entre miembros de complejos como M. avium-intracellulare, M. chelonae-abscessus, M. peregrinum-fortuitum y especies como M. smegmatis, M. goodii y M. wolinskyi (14). La importancia de la diferenciación entre los complejos radica, principalmente, en el conocimiento del pronóstico de la enfermedad y en la orientación de la quimioterapia. Vélez et al., en 1999, determinaron la actividad in vitro de diferentes antimicobacterianos frente a micobacterias no tuberculosas aisladas en Colombia, con el fin de contribuir al establecimiento de esquemas adecuados de tratamiento, y reportó su susceptibilidad y resistencia frente a los medicamentos empleados (15).
Actualmente, el estudio del gen hsp65, común en todas las micobacterias, y la descripción de la metodología de identificación molecular mediante reacción en cadena de la polimerasa PCR-análisis de restricción (16) han sido adoptados por muchos grupos de trabajo para la diferenciación de especies de micobacterias no tuberculosas (14,16-19); inclusive, en la diferenciación de M. canetti dentro del complejo M. tuberculosis y en el estudio de M. leprae (20). Ante la facilidad del método de PCR-análisis de restricción, en el mundo se han realizado una serie de estudios para lograr su estandarización y probar la reproducibilidad de la técnica (21). La principal ventaja de PCR-análisis de restricción es que, siendo un método de amplificación, desde la muestra se puede identificar la especie, en corto tiempo y con gran efectividad (18); en la mayoría de los casos, es capaz de diferenciar entre especies de los grupos de micobacterias, como el complejo M. avium-intracellulare de gran importancia clínica, aunque no diferencia los nuevos miembros del complejo, que son M. chimaera y M. colombiense (22-23).
El objetivo de este trabajo fue evaluar el PCR-análisis de restricción como método de identificación genotípica de las micobacterias no tuberculosas aisladas de muestras clínicas que pertenecen a la colección del Instituto Nacional de Salud (INS), recuperadas de 1995 a 2005.
Materiales y métodos
Muestra de estudio
La muestra constaba de 70 aislamientos clínicos de micobacterias no tuberculosas procedentes de la colección del Grupo de Micobacterias del INS, criopreservados en glicerol al 50% y recolectados durante el periodo de 1995 a 2005. Como control positivo para la amplificación e identificación genotípica, se utilizó la cepa de referencia M. tuberculosis H37Rv.
Identificación fenotípica
A todos los aislamientos se les realizó la coloración de Zielh Neelsen y se les identificó mediante metodologías fenotípicas, como: temperatura de crecimiento en medio de Lowenstein Jensen a 20°C (temperatura ambiente), 32°C, 37°C y 45°C; pruebas de crecimiento o inhibición en medios de cultivo de Ogawa Kudoh, Lowenstein Jensen, Stonebrink modificado por Giraldo, Sauton, Sauton pícrico, Mac Conkey sin cristal violeta, Lowenstein Jensen más NaCl, Lowenstein Jensen más hidroxilamina: y, las pruebas de catalasa, reducción de nitratos, fosfatasa ácida, ureasa, pirazinamidasa, tween y arilsulfatasa. Además, se determinó la producción de pigmento (24,25).
]]> Las micobacterias no tuberculosas se identificaron: 21, como M. chelonae; 15, como M. fortuitum; 8, como M. abscessus; 5, como complejo M. avium intracellulare; 4, como M. gordonae; 4, como MAI; 4, como M. scrofulaceum; 1, como M. flavescens; 1, como M. szulgai; 1, como M. terrae; y 6, como especies del grupo escoto-cromógeno IV de la clasificación de Runyon.Recuperación de aislamientos criopreservados
Los aislamientos de micobacterias no tuberculosas se descongelaron durante una hora, a cada una de las siguientes temperaturas: -20°C, 4°C y 20°C (temperatura ambiente). Luego, se homogenizó el contenido del vial de criopreservación en el que se encontraban y se sembraron 0,2 ml en medio Lowenstein Jensen, el cual se incubó a 37°C.
Identificación genotípica por la metodología de PCR-análisis de restricción
Extracción de ADN. Se siguió el protocolo descrito por van Soolingen (26). Este método incluye la lisis celular mediante adición de lisozima, la extracción de los ácidos nucleicos con el empleo de dodecil sulfato de sodio, proteinasa K, CTAB y cloroformo-alcohol isoamílico, y la precipitación del ADN con isopropanol y etanol al 70%.
Amplificación del gen hsp65. Se siguió el protocolo descrito por Telenti (16). Se realizó la amplificación del gen hsp65 mediante la utilización de los iniciadores Tb11 (ACCAACGATGGTGT-GTCCAT) y Tb12 (CTTGTCGAACCGCATACCCT). La PCR consistió en un ciclo a 95°C por 5 minutos, 45 ciclos a 94°C por 1 minuto, un ciclo a 68°C por 1 minuto, 1 ciclo a 72°C por 1 minuto y un paso final de extensión a 72°C por 7 minutos. La amplificación de un fragmento de 441 pb fue verificada por la visualización de 10 µl del amplificado en geles de agarosa de rutina (Sigma) al 1,4%.
Digestión del amplificado. Se sometieron a digestión 20 µl de los amplificados hsp65, con las enzimas de restricción HaeIII (Sigma) a 37°C y BstEII (Sigma) a 60°C durante 16 horas. Finalmente. los patrones de restricción se visualizaron en geles de agarosa de rutina (Sigma) al 3% teñidos con bromuro de etidio.
Análisis de resultados
Los resultados de la identificación fenotípica para micobacterias no tuberculosas fueron analizados de acuerdo con las tablas de identificación del Manual de Procedimientos de las Micobacterias de la Red Nacional de Laboratorios (27). Los resultados de los patrones del PCR-análisis de restricción se hicieron según lo establecido en el sitio Prasite http://app.chuv.ch/prasite el cual proporciona el acceso a una base de datos de los perfiles de restricción obtenidos por el método de PCR-análisis de restricción, que incluye la búsqueda por el nombre de las especies de micobacteria o el patrón de restricción obtenido y muestra los patrones para cada especie, o una lista de 10 especies que exhibe los patrones más cercanos.
Para la comparación de los resultados obtenidos de la identificación fenotípica y genotípica, se estableció una base de datos en EpiInfo 2003.
]]> ConcordanciaSe definió la concordancia como el número de aislamientos cuya identificación fue la misma por las metodologías fenotípicas y genotípicas.
Resultados
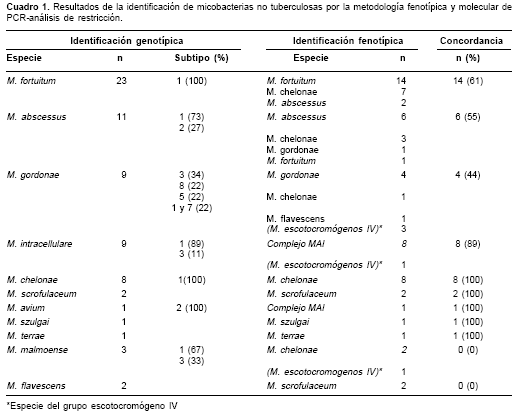
El cuadro 1 muestra los resultados de la identificación y los subtipos de micobacterias no tuberculosas por la metodología PCR-análisis de restricción, la identificación fenotípica y la concordancia de identificación entre las metodologías. La metodología PCR-análisis de restricción determina la especie y el subtipo de las micobacterias no tuberculosas, mientras que, en algunos casos, la metodología fenotípica sólo determina la clasificación de las micobacterias no tuberculosas en uno de los cuatro grupos de la clasificación de Runyon, establecida con base en las características bioquímicas y de crecimiento.

Como ejemplo de las limitaciones de la metodología fenotípica, vemos que, dadas las características bioquímicas y de crecimiento de M. malmoense como especie de difícil identificación, la mayoría de las veces, su determinación especie específica sólo se logra por metodologías moleculares como PCR-análisis de restricción.
Según los resultados que se muestran en el cuadro 1, se obtuvo concordancia del 100% en la identificación de M. terrae, M szulgai, M. avium, M. chelonae y M. scrofulaceum; la concordancia de las especies M. fortuitum, M. abscessus, M. gordonae y M. intracellulare varió de 44% a 89%; no se obtuvo concordancia en la identificación de las especies M. flavescens y M. malmoense. Por la metodología PCR-análisis de restricción, se determinó el subtipo de las especies M. fortuitum, M. abscessus, M. gordonae, M. chelonae, complejo M. avium intracelulare, M. malmoense y M. avium.
En 5 (7,14%) de los casos, la metodología fenotípica no logró identificar la especie de micobacterias no tuberculosas y sólo determinó su clasificación como especie del grupo escotocromógeno IV de la clasificación de Runyon, mientras que la metodología PCR-análisis de restricción sí identificó la especie y el subtipo.
Discusión
]]> La diferenciación de las especies del género Mycobacterium se ha realizado tradicionalmente mediante pruebas fenotípicas, las cuales son metodologías que se realizan en un periodo de tres a seis semanas y, en algunos casos, no logran diferenciar entre especies de un complejo; de hecho, el fenotipo de una especie no es una propiedad absoluta, puede exhibir gran variabilidad y las bases de datos de las características se limitan a especies comunes y no permiten discriminar especies nuevas (28).En este estudio se identificaron 70 aislamientos clínicos procedentes de todo el país, recibidos en el Grupo de Micobacterias en un periodo de 11 años, entre 1995 a 2005, los cuales se identificaron inicialmente mediante metodologías fenotípicas y, luego, por la metodología molecular PCR-análisis de restricción, y se determinó la concordancia entre las dos metodologías (
cuadro 1). La metodología de PCR-análisis de restricción (16) logró identificar todas las especies de micobacterias no tuberculosas y diferenció entre las especies que conforman un complejo hasta llegar al subtipo; este poder discriminatorio no lo posee la metodología fenotípica, que en cinco casos sólo determinó el grupo establecido por la clasificación de Runyon, identificando la micobacteria no tuberculosa como perteneciente al grupo escotocromógeno IV, y en cuatro aislamientos, determinó que eran especies del complejo M. avium intracellulare, sin establecer la especie; estas limitantes afectaron la concordancia entre las dos metodologías evaluadas en este estudio.Con estos resultados, podemos destacar la metodología PCR-análisis de restricción, establecida como práctica desde 1993 (16,19), como un método rápido para la identificación de micobacterias, fácil de implementar y no costoso en comparación con otros métodos, como secuenciación y high-performance liquid chromatography (HPLC), que requieren de equipos de alto costo (14). Además, se pudo constatar la efectividad de la metodología PCR-análisis de restricción en la identificación de micobacterias no tuberculosas de rápido y de lento crecimiento, al lograr identificar, por ejemplo, las especies de M. intracellulare, especie de lento crecimiento y M. abscessus, especie de rápido crecimiento (24). Los métodos alternativos para la identificación rápida de micobacterias como PCR-análisis de restricción pueden ser implementados de rutina en los laboratorios de microbiología por los avances significativos, la efectividad y la reproducibilidad entre laboratorios (21). Se ha observado una buena correlación entre PCR-análisis de restricción y los métodos de identificación fenotípica de aislamientos en Brasil, y además, una buena relación costo-beneficio (17).
En este estudio, el tiempo necesario para la realización de PCR-análisis de restricción fue de tres días; considerando los reactivos y materiales, el método es más económico que la identificación fenotípica y lo puede realizar una sola persona (las metodologías fenotípicas involucran varios profesionales para su realización). En la metodología PCR-análisis de restricción, sólo se manipula el microorganismo vivo al inicio de la extracción del ADN, lo cual implica una mayor bioseguridad (datos no mostrados). En un estudio realizado por Da Silva et al., se reportaron hallazgos similares (15).
En los resultados discordantes se pudo ver que las características de crecimiento de cada especie son de gran importancia. Se presentaron dificultades al realizar la identificación por la metodología de PCR-análisis de restricción; por ello sugerimos consultar las características de crecimiento de estos aislamientos, ya que, cuando se realiza sólo la metodología de PCR-análisis de restricción, no se dispone de esta información.
Los resultados de este estudio se correlacionan con los obtenidos por el Instituto Pasteur, donde los mayores problemas se presentaron en la identificación de M. fortuitum, M. peregrinum, M. chelonae y M. abscessus, referidos antes como complejo M. fortuitum (M. fortuitum variedad fortuitum, M. fortuitum variedad peregrinum, M. chelonae subespecie chelonae y M. chelonae subespecie abscessus) (18).
Ante la probabilidad de encontrar discrepancia en los tamaños moleculares de las bandas para la realización de la metodología PCR-análisis de restricción, se ha sugerido la construcción de una base de datos con los patrones de las micobacterias no tuberculosas más prevalentes en cada país (19).
En conclusión, el PCR-análisis de restricción es una alternativa para la identificación de especies de micobacterias no tuberculosas, rápida, económica y segura para la identificación de mico-bacterias patógenas y potencialmente patógenas, (17). La determinación del subtipo de cada especie de micobacterias no tuberculosas identificada es importante debido a la diferencia en la virulencia de cada subtipo y a la capacidad de producir enfermedad en el humano, como se ha establecido para M. abscessus y M. avium (29,30).
En Colombia no se conoce la prevalencia de micobacteriosis, debido a varios factores, entre los que podemos mencionar la falta de conocimiento de estas especies como causantes de enfermedad en el hombre y el no sospechar estas enfermedades infecciosas cuando no hay respuesta al tratamiento con antibióticos (10). En la actualidad, en el país son pocos los laboratorios que realizan pruebas bioquímicas o moleculares para la identificación de micobacterias no tuberculosas. Para la confirmación de una mico-bacteriosis, es necesaria la toma de dos o más muestras y completar los requisitos para definir el diagnóstico, ya que en un estudio realizado por el Grupo de Micobacterias del INS el 62% de los casos remitidos no pudieron confirmarse. Por esta razón, los pacientes difícilmente acceden a estas pruebas diagnósticas y sus cuadros clínicos se tornan crónicos por un manejo inadecuado de la patología (10). La implementación de la metodolo-gía de PCR-análisis de restricción es una alternativa para las instituciones que cuenten con una unidad de diagnóstico molecular de enfermedades infecciosas y que cumplan los requisitos establecidos por la Red Nacional de Laboratorios para la confirmación de casos de micobacteriosis, y contribuiría a determinar la frecuencia de esta enfermedad en el país y, por lo tanto, a un manejo oportuno y adecuado de los pacientes infectados.
La vigilancia de las micobacterias no tuberculosas es una actividad que desarrolla el Laboratorio Nacional de Referencia de Micobacterias del INS para la Red Nacional de Laboratorios (10). El PCR-análisis de restricción es una herramienta que contribuye a la identificación de micobacterias no tuberculosas como agente causal de enfermedad (31).
]]> AgradecimientosA Elizabeth Castañeda por su apoyo en la realización de este trabajo y sus aportes en la redacción de este artículo; a Iván Cortés, Cristina Galindo, Jaime Rodríguez y Blanca Ruth Velandia, por el apoyo técnico para la realización de este proyecto.
Conflicto de intereses
Los autores del artículo hacen constar que no existe, de manera directa o indirecta, ningún tipo de conflicto de intereses financieros, académicos o personales que puedan poner en peligro la validez de lo comunicado.
Financiación
Este trabajo fue financiado por el Instituto Nacional de Salud (CTIN 02/06).
Correspondencia:
Wellman Ribón, Grupo de Micobacterias, Instituto Nacional de Salud, Avenida calle 26 Nº 51-20. Teléfono: (571) 220 0926, 220 7700 extensión 436 o 498, fax: (571) 220 0926. wribon@ins.gov.co
Referencias
1. Brown-Elliott BA, Wallace RJ Jr. Clinical and taxonomic status of pathogenic nonpigmented or late-pigmenting rapidly growing mycobacteria. Clin Microbiol Rev. 2002;15:716-46. [ Links ]
2. Primm TP, Lucero CA, Falkinham JO 3rd. Health impacts of environmental mycobacteria. Clin Microbiol Rev. 2004;17:98-106. [ Links ]
3. Tortoli E. Impact of genotypic studies on mycobacterial taxonomy: the new mycobacteria of the 1990s. Clin Microbiol Rev. 2003;16:319-54. [ Links ]
4. Nuñez-Guzman J, Starke J, Correa A, Graviss E, Pan X, Popek E, et al. A report of cutaneous tuberculosis in siblings. Pediatr Dermatol. 2003; 20:404-7. [ Links ]
5. Duttaroy B, Agrawal C, Pendse A. Spinal tuberculosis due to dissemination of atypical mycobacteria. Indian J Med Sci. 2004;58:203-5. [ Links ]
6. Holmes GF, Harrington SM, Romagnoli MJ, Merz WG. Recurrent, disseminated Mycobacterium marinum infection caused by the same genotypically defined strain in an immunocompromised patient. J Clin Microbiol. 1999;37:3059-61. [ Links ]
7. Murcia-Aranguren MI, Gómez-Marín JE, Alvarado FS, Bustillo JG, de Mendivelson E, Gomez B, et al. Frequency of tuberculous and non-tuberculous mycobacteria in HIV infected patients from Bogotá, Colombia. BMC Infect Dis. 2001;1:21. [ Links ]
8. Camargo D, Saad C, Ruiz F, Ramírez ME, Lineros M, Rodríguez G, et al. Iatrogenic outbreak of M. chelonae skin abscesses. Epidemiol Infect. 1996;177:113-9. [ Links ]
9. Ortegón M, Rodríguez G, Camargo D, Orozco LC. Mycobacterium chelonae y Mycobacterium abscessus: patógenos emergentes. Biomédica. 1996;16:217-38. [ Links ]
10. Garzón M, Orjuela D, Naranjo O, Llerena C. Micobacterias no tuberculosas en Colombia 1995-2003. Inf Quinc Epidemiol Nac. 2005;10:161-76. [ Links ]
11. León CI, Jiménez Y, López OJ, Pavas J, Bustillo JG, Guerrero MI. Evolución de la asociación micobacteriana HIV-SIDA en Bogotá 1995-2003. Infectio. 2004;8:99. [ Links ]
12. Crespo M, Corral R, Alzate A. Micobacterias no tuberculosas en personas VIH positivas y en personas sin factores de riesgo a la infección. Colombia Med. 1994;25:86-91. [ Links ]
13. León CI. Presencia de las micobacterias no tuberculosas en Colombia. Médicas UIS. 1998;12: 181-7. [ Links ]
14. Wang SX, Tay L, Sing LH. Rapid identification of pathogenic rapidly growing mycobacteria by PCR-restriction endonuclease analysis. Ann Acad Med Singapore. 2005;34:137-40. [ Links ]
15. Vélez E. Actividad in vitro de diferentes antimicobacterianos frente a cepas de micobacterias no tuberculosas aisladas en Colombia (tesis). Bogotá: Universidad Nacional de Colombia; 1999. [ Links ]
16. Telenti A, Marchesi F, Balz M, Bally F, Bötter EC, Bodmer T. Rapid identification of mycobacteria to the species level by polymerase chain reaction and restriction enzyme analysis. J Clin Microbiol. 1993;31: 175-8. [ Links ]
17. Da Silva C, Misuka S, Cássia D, Cardoso S. Hsp65 PCRrestriction enzyme analysis (PRA) for identification of mycobacteria in the clinical laboratory. Rev Inst Med Trop Sao Paulo. 2001;43:25-8. [ Links ]
18. Devallois A, Goh KS, Rastogi N. Rapid identification of mycobacteria to species level by PCR-restriction fragment length polymorphism analysis of the hsp65 gene and proposition of an algorithm to differentiate 34 mycobacteria species. J Clin Microbiol. 1997;35: 2969-73. [ Links ]
19. Brunello F, Ligozzi M, Cristelli E, Bonora S, Tortoli E, Fontana R. Identification of 54 mycobacterial species by PCR-restriction fragment length polymorphism analysis of the hsp65 gene. J Clin Microbiol. 2001;39:2799-806. [ Links ]
20. Rastogi N, Goh KS, Berchel M. Species-specific identification of Mycobacterium leprae by PCR-restriction fragment length polymorphism analysis of the hsp65 gene. J Clin Microbiol. 1999;37:2016-9. [ Links ]
21. Leao SC, Bernardelli A, Cataldi A, Zumarraga M, Robledo J, Realpe T, et al. Multicenter evaluation of mycobacteria identification by PCR restriction enzyme analysis in laboratories from Latin America and the Caribbean. J Microbiol Methods. 2005;61:193-9. [ Links ]
22. Murcia MI, Tortoli E, Menéndez MC, Palenque E, García MJ. Mycobacterium colombiense sp. nov., a novel member of the Mycobacterium avium complex and description of MAC-X as a new ITS genetic variant. Int J Syst Evol Microbiol. 2006;56:2049-54. [ Links ]
23. Tortoli E, Rindi L, Garcia MJ, Chiaradonna P, Dei R, Garzelli C, et al. Proposal to elevate the genetic variant MAC-A, included in the Mycobacterium avium complex, to species rank as Mycobacterium chimaera sp nov. Int J Syst Evol Microbiol. 2004;54:1277-85 [ Links ]
24. Leao S, Martn A, Mejía G, Palomino J, Robledo J, Telles Da Silva M, et al. Practical handbook for phenotypic and genotypic identification of Micobacteria. First edition. Brussels: European Commision, International Cooperation for Developing Countries; 2004. [ Links ]
25. Garzón MC, Naranjo ON, Sierra CR, Llerena C, Orjuela DL. Bacteriología del Mycobacterium tuberculosis y de micobacterias no tuberculosas. Manual de Procedimientos. 1ª edición. Bogotá: Instituto Nacional de Salud; 2001. [ Links ]
26. Van Soolingen D, Hermans PW, de Haas PE, Soll DR, van Embden JD. The occurrence and stability of insertion sequences in Mycobacterium tuberculosis complex strains; evaluation of IS-dependent DNA polymorphism as a tool in the epidemiology of tuberculosis. J Clin Microbiol. 1991;29:2578-86. [ Links ]
27. Garzón MC, Naranjo ON, Llerena C, Orjuela DL. Identificación de las micobacterias. Manual de procedimientos. Bogotá: Instituto Nacional de Salud; 2002. [ Links ]
28. Springer B, Stockman L, Teschner K, Roberts GD, Bottger EC. Two laboratory collaborative study on identification of mycobacteria: molecular versus phenotypic methods. J Clin Microbiol. 1996;34:296-303. [ Links ]
29. Byrd TF, Lyons CR. Preliminary characterization of a Mycobacterium abscessus mutant in human and murine models of infection. Infect Immun. 1999;67:4700-7. [ Links ]
30. Maekura R, Okuda Y, Hirotani A, Kitada S, Hiraga T, Yoshimura K, et al. Clinical and prognostic importance of serotyping Mycobacterium avium-Mycobacterium intracellulare complex isolates in human immunodeficiency virus-negative patients. J Clin Microbiol. 2005;43:3150-8. [ Links ]
31. García LM, Garzón M, Orjuela D, Mejía G, Llerena C, Angee D. Mycobacterium tuberculosis y micobacterias no tuberculosas en procedimientos de mesoterapia. Inf Quinc Epidemiol Nac. 2007;12:40-4. [ Links ] ]]>