Búsqueda del plásmido de virulencia de Salmonella en aislamientos clínicos colombiano
Search of the Salmonella virulence plasmid in Colombian clinical isolate
DANIEL FELIPE PATIÑO GARCÍA1, NORA MARÍA CARDONA CASTRO2, MIRYAM MARGOT SÁNCHEZ JIMÉNEZ3
1 Técnico profesional en Histocitotecnología. Estudiante Biología Universidad CES.
2MD. MSc. Investigadora Instituto Colombiano de Medicina Tropical – Universidad CES. Grupo de investigación en Medicina Tropical, ICMT-CES.
Correo electrónico: ncardona@ces.edu.co
3 Investigadora Instituto Colombiano de Medicina Tropical – Universidad CES. Grupo de Investigación en Medicina Tropical, ICMT-CES
RESUMEN
]]> Introducción: Salmonella es un bacilo Gram negativo, patógeno intracelular que invade células intestinales no fagocíticas y macrófagos en un proceso complejo que requiere múltiples genes. El plásmido de virulencia de Salmonella "spv" contiene el gen spvR cuya función es aumentar su virulencia produciendo invasión sistémica en ratones.Métodos: Se buscó el gen spvR de Salmonella spp en aislamientos clínicos humanos provenientes de pacientes con sintomatología sistémica (fiebre tifoidea) y no sistémica (diarrea), con el fin de comparar la presencia del gen con la clínica del paciente. El gen spvR se buscó en 55 aislamientos de S. Typhi de pacientes con fiebre tifoidea, 20 de S. Enteritidis y 20 de S. Typhimurium, aislados de pacientes con diarrea. Se realizó PCR a partir de ADN genómico y plasmídico. Los productos se secuenciaron y las secuencias obtenidas de material genómico y plasmídico se compararon utilizando análisis bioinformáticos.
Resultados: El 100 % de los aislamientos de S. Typhi fueron negativos para spvR, mientras que 75 % de los aislamientos de S. Enteritidis y 40 % de S. Typhimurium, presentaron amplificación del gen spvR, tanto en material genómico como plasmídico. Se evidenció también la presencia de secuencias plasmídicas homólogas al gen spvR en regiones cromosomales de los serotipos estudiados.
Conclusiones: Los resultados muestran que la ausencia del plásmido de virulencia de Salmonella no está relacionada con la infección sistémica, pues no fue encontrado en S. Typhi productora de fiebre tifoidea. Se confirmó también que existe material cromosomal homólogo al gen spvR del plásmido de virulencia en el cromosoma de los serotipos S. Enteritidis y S. Typhimurium, pero no se encontró material similar en el cromosoma de S. Typhi.
PALABRAS CLAVES
Salmonella, Virulencia, Plásmido, Colombia
ABSTRACT
Introduction: Salmonella is a Gram negative bacillus, intracellular pathogen that invades nonphagocytic intestinal cells and macrophages in a complex process that requires multiple genes. The salmonella virulence plasmid "spv" contains the spvR gene whose function is to increase its virulence producing systemic invasion in mice.
Methods: We search for spvR gene in human clinical isolates of Salmonella spp from patients with systemic infection (typhoid fever) and with nonsystemic infection (diarrheal), in order to compare the presence of the gene to clinical outcome. spvR was searched in 55 clinical isolates of S. Typhi from typhoid fever patients, 20 of S. Enteritidis and 20 of S. Typhimurium isolates from patients with diarrheal. PCR from chromosomal and plasmid DNA was performed. The PCR products were sequenced and the sequences obtained from genomic and plasmid materials were compared using bioinformatics analysis.
Results: 55 (100 %) isolates of S. Typhi were negative for spvR. 15 (75 %) isolates of S. Enteritidis and 8 (40 %) of S. Typhimurium were positive for spvR both from genomic and plasmid material. These results show that clinical isolates of S. Typhi considered more virulent not showed spvR, and that diarrhea-producing serotypes S. Enteritidis and S. Typhimurium in 75 and 40 % respectively were positive for the gene, questioning the role of virulence of the gene in strains producing human infections. It also showed the presence of plasmid gene sequences homologous to chromosomal regions in the studied serotypes. ]]>
Conclusion: Results show that the absence of the plasmid of Salmonella's virulence is not related with the systemic outcome in the clinical isolates of Salmonella Typhi that were studied. There was also confirmed that exists chromosomal material homologous to the gene spvR virulence plasmid in the chromosome of serotypes S. Enteritidis and S. Typhimurium but similar material wasn't found in S. Typhi chromosome.
KEY WORDS
Salmonella , Virulence, Plasmid, Colombia
INTRODUCCIÓN
Salmonella es un bacilo Gram negativo, patógeno intracelular que invade células intestinales no fagocíticas y macrófagos en un proceso complejo que requiere múltiples genes (1). Salmonella spp puede infectar animales o humanos y es considerada una zoonosis (2). Dependiendo del serotipo de Salmonella se pueden producir diferentes manifestaciones clínicas como gastroenteritis (la cual puede ser producida por más de 2 000 serotipos), o fiebre tifoidea si el serotipo que infecta es S. Typhi, o fiebre paratifoidea producida por S. Paratyphi A, Paratyphi B o Paratyphi C (2,3).
El serotipo de Salmonella más estudiado ha sido el Typhimurium, debido a su fácil manipulación en el laboratorio y a la reproducción de un cuadro clínico que semeja la fiebre tifoidea de los humanos en un modelo murino (4). De los otros serotipos se posee menos información a nivel genómico (5).
El material genético de S. Typhimurium está compuesto por 4 600 genes organizados en un cromosoma único y por un plásmido específico de serotipo el cual varía en tamaño (6). Algunos serotipos presentan plásmidos de virulencia que son importantes para la producción de infección sistémica. Se conoce que ocho serotipos presentan el plásmido de virulencia de Salmonella (SPV): S. Paratyphi C, S. Enteritidis, S. Typhimurium, S. Dublin, S. Choleraesuis, S. Gallinarum, S. Pullorum y S. Abortusovis (7).
El SPV varía en tamaño dependiendo del serotipo: 95 kb para S. Typhimurium, 60 kb para S. Enteritidis, 80 kb para S. Dublin y entre 50 y 100 kb para S. Choleraesuis (5,7), y tiene una región altamente conservada de 7,8 kb, la cual es un operón compuesto por cinco genes, denominado región spvRABCD (8).
]]> Estos genes spv se han definido sobre la base de su habilidad para aumentar la virulencia de serotipos de Salmonella enterica capaces de producir enfermedad letal en ratones (8). En estudios utilizando un modelo murino se demostró que los genes spv no afectan la colonización ni la invasión a través de la mucosa intestinal y que no son requeridos para infectar tejido extraintestinal como el hígado y el bazo; sin embargo, aumentan significativamente la tasa de crecimiento de la bacteria dentro de este tejido, probablemente en un compartimiento intracelular de la bacteria de estos órganos (9).Esta región spv pudo haber sido adquirida horizontalmente, ya que está ubicada adyacente a un elemento insercional y el contenido de guanina - citosina es más bajo (46 %) que en el resto del cromosoma de S. Typhimurium (8). Los genes spv son expresados durante la fase estacionaria del crecimiento y durante estadios intracelulares de infección; los serotipos que no poseen el plásmido de virulencia o que tienen la región spv cortada, son avirulentos en modelos animales (10). El gen spvR cumple una función importante en la virulencia, ya que regula a los otros cuatro genes que conforman el operón spv (11).
Hay reportes que mencionan que S. Typhi no tiene el plásmido de virulencia y que no todos los aislamientos de los serotipos lo poseen (8,12). Estas divergencias en la presencia o no de spv en distintos serotipos y la diversidad clínica que producen, confunden acerca del papel del plásmido de virulencia en la patogénesis de Salmonella, el cual continúa aún siendo un enigma. Siendo el spv importante en la producción de infección sistémica, llama la atención que no esté presente en el serotipo que produce fiebre tifoidea (5).
La mayoría de los estudios han sido realizados en cepas de laboratorio y en modelos murinos; hay pocos estudios de este tipo realizados en aislamientos clínicos de pacientes (12). En este trabajo se buscó spv en aislamientos clínicos de S. enterica provenientes de pacientes con diarrea y fiebre tifoidea, para comparar la presencia del plásmido con el serotipo y con el cuadro clínico producido.
MATERIALES Y MÉTODOS
Aislamientos bacterianos estudiados
Se evaluaron 95 aislamientos: 55 de S. Typhi aisladas de pacientes con fiebre tifoidea, 20 de S. Typhimurium y 20 de S. Enteritidis aisladas de pacientes con diarrea. Todas las cepas estudiadas son aislamientos de muestras clínicas humanas. Las cepas de S. Typhi se aislaron de pacientes afectados por un brote epidémico de fiebre tifoidea (infección sistémica), ocurrido en el año 2005 en Apartadó, Antioquia y de otros pacientes exporadicos con fiebre tifoidea. Las cepas de S. Typhimurium y S. Enteritidis fueron aisladas de pacientes con diarrea y quienes eran provenientes de Antioquia, Valle y Cundinamarca. Las cepas pertenecen al cepario del Instituto Colombiano de Medicina Tropical (ICMT) y se encontraban almacenados en agar blando más glicerol a -70 °C. Para recuperarlos y confirmar características morfológicas, se replicaron en agar Mueller Hinton y en agar Mc Conkey. Para confirmar características propias de género se les realizaron pruebas bioquímicas y para confirmar serovar se realizó PCR múltiple.
Reacción en cadena de la polimerasa (PCR)
]]> Extracción de ADN genómico: cada aislamiento almacenado se sembró en caldo BHI y se incubó a 37 °C durante 18 horas para verificar su viabilidad. Posteriormente, al verificar turbidez en el medio, se procedió a sembrar una asada en agar Mueller Hinton y se incubó nuevamente a 37 °C durante 18 horas; a partir del cultivo puro se tomaron dos colonias y se inocularon en 200 µL de agua destilada estéril, se mezcló en vórtex y se realizó la extracción por el método de ebullición ("boiling prep") (13).Brevemente, las muestras se sometieron a ebullición por 10 minutos, posteriormente se centrifugaron a 12 000 rpm, por cinco minutos y se transfirieron 100 µL del sobrenadante a un tubo nuevo. El ADN genómico se conservó a -20 °C hasta ser usado para la amplificación. Este proceso se realizó por duplicado para cada muestra. Se midió la concentración de ADN por espectrofotometría y se utilizó como muestra para PCR una concentración de 100 µM.
Extracción de ADN plasmídico: la extracción de ADN plasmídico se realizó solo en aquellos aislamientos en los cuales se obtuvo amplificación del gen spvR a partir de ADN genómico. Se utilizó el protocolo MiniPrep (14), se tomaron varias colonias del agar Mueller Hinton y se sembraron en 1,5 ml de agua destilada, se centrifugó a 11 000 rpm a 4°C por dos minutos, se aspiró el sobrenadante y posteriormente se adicionaron 100 µL de solución 1 (50 mM glucosa, 10 mM EDTA, 25 mM Tris); se resuspendió el sedimento con vórtex y se colocó en hielo por 5 m. Se adicionaron 200 µL de solución 2 (0,2 N NaOH, 1 % SDS), se mezcló por inversión, se agitó y colocó en hielo por cinco minutos. Luego se adicionaron 150 µL de solución 3 (3M NaOAC, pH= 4,80), se mezcló por inversión hasta que se formó un precipitado blanco y se colocó en hielo durante 5 m. Posteriormente se centrifugó a 11 000 rpm a 4°C durante 5 m, se transfirió el sobrenadante a tubos limpios, se adicionaron 450 µl de fenol cloroformo isoamílico y se mezcló por inversión suavemente.
Luego se centrifugó a 11 000 rpm a 4°C por 5 m, se transfirió la capa superior acuosa a tubos limpios y se adicionó 1 mL de etanol absoluto frío, posteriormente se colocó en hielo 5 m, se centrifugó a 11 000 rpm a 4°C durante 5 m, se aspiró el sobrenadante, se adicionaron 500 µL de etanol al 70 % al sedimento y se centrifugó nuevamente por otros 5 m, se aspiró el sobrenadante, se dejó secar y por último se resuspendió el sedimento en 50 µl de TE y se guardó a -20°C hasta realizar la PCR.
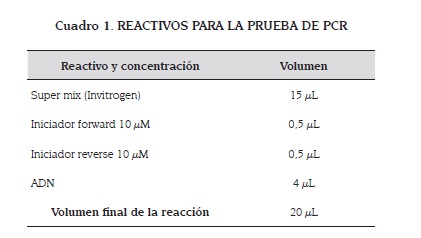
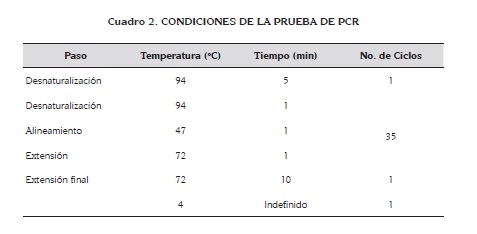
Amplificación de ADN: Para la realización de las pruebas de PCR, tanto de material genómico como de material plasmídico, para buscar el gen spvR se utilizaron los reactivos y condiciones de amplificación que se pueden observar en los cuadros 1 y 2.
Iniciadores: Los iniciadores (primers) utilizados para detectar el gen spvR por PCR, fueron diseñados por investigadores de la sección de Microbiología Clínica y Experimental de la Universidad de Sassari - Italia (datos no publicados). Estos cebadores se diseñaron utilizando la secuencia del genoma de S. Typhimurium LT2 encontrado en el GenBank (número de acceso NC_ 003197). En el cuadro 3 se pueden observar las secuencias de estos cebadores.
]]>
Para todas las PCR realizadas se utilizo como control positivo la cepa ATCC 14028 de S. Typhimurium, en la cual estan presentes la secuencia que se busco en el presente trabajo y como control negativo se utilizo agua destilada esteril.
Confirmacion de serotipo: Se realizaron dos PCR multiples para confirmar los serotipos de los aislamientos incluidos en el estudio, con cebadores especificos desarrollados previamente (15,16). En la primera PCR se realizo la confirmacion de serogrupo (15) y en la segunda PCR multiple se realizo la confirmacion de serotipo (16).
Deteccion de productos de amplificacion: Para el gen spvR 10 µL del producto de amplificacion se fraccionaron electroforeticamente en un gel de agarosa al 1 % tenido con SYBR® SAFE, a 100 voltios por una hora. En cada gel se corrieron adicionalmente un control positivo y un control negativo, ademas de un marcador de peso molecular GeneRuler 100pb DNA ladder (Fermentas, Toronto, Canada). Para la PCR de serogrupo y la de serotipo se utilizo un gel con las mismas condiciones pero con una concentracion de agarosa del 2,5 %.
Secuenciacion de los productos de amplificacion: Para conocer la secuencia del producto amplificado, fue enviado a Macrogen (Corea).
Analisis de los fragmentos amplificados: Los fragmentos secuenciados se analizaron en el software en linea BLAST y el software BioEdit, para determinar sus similitudes. Se realizo el analisis in silico de los cebadores que se utilizaron en el estudio, con la base de datos BLAST, para verificar nuevamente su especificidad, pues estas bases de datos genomicos son actualizadas constantemente.
]]> Control de errores y sesgos: Cada ensayo de laboratorio se realizo por triplicado para evitar falsos positivos o falsos negativos, se usaron tambien controles negativos y positivos para la realizacion de las pruebas.Aspectos éticos: Las cepas estudiadas provienen de cepario, por lo tanto no hubo contacto con el paciente en este estudio.
Procesamiento y análisis de los resultados
Se elaboró una base de datos en el programa Microsoft Excel 2003 (Microsoft Corp., Rendomd, WA) y el procesamiento de la información se realizó en el programa Epi Info versión 6,0. El análisis estadístico de las variables cualitativas se realizó mediante el cálculo de frecuencias absolutas y relativas. Se realizó una PCR electrónica in silico (http://insilico.es) para comprobar la especificidad de los primers usados. Los productos de PCR se enviaron a secuenciar y se compararon las secuencias obtenidas utilizando el software BioEdit y la base de datos BLAST del NCBI (www.ncbi.nlm.nih.gov/blast) para búsqueda de información genómica de Salmonella.
RESULTADOS
El 100 % de los aislamientos de S. Typhi fueron negativos para spvR, mientras que 75 % de los aislamientos de S. Enteritidis y 40 % de S. Typhimurium, presentaron amplificación del gen spvR, tanto en material genómico como plasmídico. Se evidenció también la presencia de secuencias plasmídicas homólogas al gen spvR en regiones cromosomales de los serotipos estudiados. Al realizar el BLAST a los cebadores para el gen spvR, se evidenció que estos amplifican no solo este gen, sino también otros ubicados en otros plásmidos de serotipos de Salmonella como los genes mba1, mkfC, mkfD y vsdA-F. También amplifican in silico los genes mkaC, virR y katF que se encuentran en el cromosoma de S. Typhimurium, factor que se solucionó con la secuenciación de los productos la cual permitió definir si spvR fue amplificado. En ninguna de las 55 muestras de S. Typhi se encontró el gen spvR (Figura 1).
]]>
De los otros 20 aislamientos del serotipo S. Enteritidis, 15 (75 %) presentaron amplificación del gen spvR y de los 20 aislamientos de S. Typhimurium, 8 (40 %) presentaron el gen spvR tanto a nivel genómico como plasmídico (Figura 2).
La comparación de las secuencias obtenidas utilizando el software BioEdit y la base de datos BLAST del NCBI concluyen que tanto los productos de ADN genómico como de ADN plasmídico, presentaron secuencias altamente similares en todos los aislamientos analizados. No se encontró in silico ninguna secuencia similar en el cromosoma ni en plásmidos de S. Typhi.
DISCUSIÓN
Los resultados confirmaron la ausencia del plásmido de virulencia de Salmonella en los aislamientos clínicos colombianos de S. Typhi estudiados. Se confirmó también que existe material cromosomal homólogo al gen spvR del plásmido de virulencia en el cromosoma de los serotipos S. Enteritidis y S. Typhimurium, pero no se encontró material similar en el cromosoma de S. Typhi.
]]> Los resultados de este trabajo concuerdan con lo expuesto por Rotger y colaboradores (7) quienes reportan la presencia del plásmido de virulencia solo en algunos serotipos de Salmonella (S. Enteritidis, S. Choleraesuis, S. Typhimurium, S. Paratyphi C, S. Dublin, S. Gallinarum, S. Pullorum y S. Abortusovis) y no en todos los aislamientos del mismo serotipo. Esto es también similar a lo reportado por Bacci y colaboradores (17), quienes analizaron aislamientos de diferentes serotipos de Salmonella provenientes de cerdos y ganado vacuno y encontraron el gen spvR en uno de diez aislamientos de S. Enteritidis y en cuatro de 13 aislamientos de S. Typhimurium.Es poco lo reportado en la literatura sobre la presencia del plásmido de virulencia de Salmonella en S. Typhi. En este trabajo se descartó esta posibilidad por lo menos en los 55 aislamientos colombianos analizados, pero en una investigación de Huang y colaboradores (18) se reporta la presencia del gen spvR en el plásmido pRst98, que es un plásmido que confiere resistencia a antibióticos en aislamientos de S. Typhi. Esta podría ser una posibilidad a tener en cuenta en futuros análisis en más aislamientos colombianos de S. Typhi, pues en el presente trabajo solo se investigó la presencia de spvR y no la presencia de otros plásmidos en los cuales podría estar incluido este gen y que están involucrados en procesos de virulencia de los serotipos que los portan, igual función que la atribuida al plásmido de virulencia (19-21).
S. Typhi produce en humanos fiebre tifoidea, siendo éstos los únicos hospederos identificados para este serotipo (19,20). S. Typhimurium y S. Enteritidis son aisladas con frecuencia de pacientes con diarrea y por su transmisión se conoce como zoonosis, pues las cepas que infectan al humano provienen de hospederos animales y se adquieren por contaminación hídrica y alimentaria (20).
La presencia de genes de virulencia como spv se ha asociado a la capacidad invasora de las cepas, la cual estaría relacionada con el tipo de sintomatología que producen en el hospedero (21). Se conoce por experimentos previos que los genes spv son expresados durante la fase estacionaria del crecimiento y durante estadios intracelulares de infección; los serotipos que no poseen el plásmido de virulencia o que tienen la región spv cortada, son avirulentos en modelos animales (10). Sin embargo, estos estudios son realizados con modelos animales de infección y difieren con lo encontrado en aislamientos clínicos de pacientes (7,17).
En nuestro estudio encontramos que el 100 % de los aislamientos de S. Typhi fueron negativos para spvR, tampoco encontramos material cromosomal homólogo al gen spvR del plásmido de virulencia en el cromosoma de S. Typhi, pero sí en el cromosoma y en otros plásmidos de otros serotipos de S. enterica.
Estos hallazgos en aislamientos de S. Typhi de muestras clínicas de pacientes colombianos concuerdan con lo encontrado por otros investigadores (7,17), y pudieran ayudar a esclarecer que este gen no tiene función de invasividad en S. Typhi si se tiene en cuenta el carácter invasivo de la bacteria para producir fiebre tifoidea (22-24).
El 75 % de los aislamientos estudiados de S. Enteritidis y 40 % de S. Typhimurium, fueron positivos para el gen spvR, tanto en material genómico como plasmídico, cepas aisladas de pacientes con diarrea sin enfermedad sistémica, corroborando que el papel de este plásmido de invasividad pudiera haber sido sobreestimado en los resultados obtenidos con los modelos animales (10).
El número de cepas estudiadas corresponde a una muestra limitada, por lo tanto con estos resultados no podemos afirmar que todos los aislamientos de Salmonella en pacientes colombianos tengan las mismas características encontradas en este trabajo.
Se conoce que el gen spvR cumple una función importante en la virulencia ya que regula a los otros cuatro genes que conforman el operón spv (11). Siendo el spv importante en la producción de infección sistémica, llama la atención que no esté presente en el serotipo que produce fiebre tifoidea y que se encuentre en serotipos que producen diarrea sin invasión sistémica (25,26).
Estas divergencias en la presencia o no de spv en distintos serotipos y la diversidad clínica que producen, confunden acerca del papel del plásmido de virulencia en la patogénesis de Salmonella (27,28).
]]>
CONFLICTOS DE INTERÉS
Los autores declaran no tener conflictos de interés con los resultados obtenidos en este trabajo.
FINANCIACIÓN
Este proyecto fue financiado por la Dirección de Investigación de la Universidad CES (Código 200709 C112), por Colciencias (Código 3256- 408-20564) y por el Instituto Colombiano de Medicina Tropical-CES.
]]> REFERENCIAS
1. Darwin KH, Miller VL. Molecular basis of the interaction of Salmonella with the intestinal mucosa. Mol Microbiol Rev 1999;12:405-28. [ Links ]
2. Miller S, Hohmann E, Pegues DA. Salmonella (including Salmonella Typhi) in: Mandell J, Bennett A, Dolin E (eds). Mandell, Douglas, and Bennett's Principles and Practice of Infectious Diseases. 6th Ed. Philadelphia, Churchill Livingstone 2004; 2013-33. [ Links ]
3. Murray PR, Rosenthal KS, Kobayashi GS, Pfaller MA. Salmonella. In: Michael Braun Ed. Medical Microbiology. 3a ed. St Louis: Mosby Inc; 1998. p. 237-39. [ Links ]
4. Mills DM, Bajaj V, Lee CA. A 40 kb chromosomal fragment encoding Salmonella Typhimurium invasion genes is absent from the corresponding region of the Escherichia coli K-12 chromosome. Mol Microbiol 1995; 15: 749-59. [ Links ]
4. Chu CS, Hong SF, Tsai CJ, Lin WS, Liu TP, Ou JT. Comparative physical and genetic maps of the virulence plasmids of Salmonella enterica serovars Typhimurium, Enteritidis, Choleraesuis, and Dublin. Infect Immun 1999; 67:2611–2614 [ Links ]
4. McClleland M, Florea L, Sanderson K, Clifton SW, Parkhill J, Churcher C et al. Comparison of the Escherichia coli K- 12 genome with samples genomes of a Klebsiella pneumoniae and three Salmonella enterica serovars, Typhimurium, Typhi and Paratyphi. Nucleic Acid Res 2000; 24: 4974-86. [ Links ]
5. Rotger R, Casadesús J. The virulence plasmids of Salmonella. Internatl Microbiol 1999; 2:177–84 [ Links ]
6. Lax AJ, Pullinger GD, Spink JM, Qureshi F, Wood MW, Jones PW., Plasmid genes involved in virulence in Salmonella, In: Biology of Salmonella, 1993, Edited by F. Cabello et al. Plenum Press, New York. [ Links ]
7. Libby SJ, Adams LG, Ficht TA, Allen C, Whitford HA, Buchmeier NA, Bossie S, Guiney DJ. The spv genes on the Salmonella Dublin virulence plasmid are required for severe enteritis and systemic infection in the natural host. Infect Immun 1997; 65: 1786-92. [ Links ]
8. Gulig PA, Doyle TJ. The Salmonella Typhimurium virulence plasmid increases the growth rate of salmonellae in mice. Infect Immun 1993; 61:504–511. [ Links ]
9. Boyd EF, Hartl Dl. Salmonella Virulence Plasmid: Modular Acquisition of the spv Virulence Region by an F-Plasmid in Salmonella enterica Subspecies I and Insertion Into the Chromosome of Subspecies II, IIIa, IV and VII Isolates. Genetics 1998; 149: 1183-90. [ Links ]
10. Geimba MP, Tondo EC, De Oliveria FA, Canal CW, Brandelli A. Serological characterization and prevalence of spvR gene in Salmonella isolated from foods involved in outbreaks in Brazil. J Food Prot 2004; 67: 1229 – 33. [ Links ]
11. Fantasia M, Paglietti B, Filetici E, Anastasio MP, Rubino S. Conventional and molecular approaches to isolates of Salmonella hadar from sporadic and epidemic cases. J Appl Micro 1997; 82: 494-8 [ Links ]
12. Chowdhury K. One step 'miniprep' method for the isolation of plasmid DNA. Nuc Acid Res 1991; 19: 2792. [ Links ]
13. Lavalett L, Sánchez M, Múñoz N, Moreno J, Cardona-Castro N. Desarrollo y validación de una reacción en cadena de la polimerasa múltiple para la identificación de los serogrupos B, C2, D y E de Salmonella enterica. Biomédica 2009;29:244-52. [ Links ]
14. Cardona-Castro N, Sánchez-Jiménez M, Lavalett L, Múñoz N, Moreno J. Development and evaluation of a multiplex polymerase chain reaction assay to identify Salmonella serogroups and serotypes. Diagnostic Microbiology and Infectious Disease 65 (2009) 327–330. [ Links ]
15. Bacci C, Paris A, Salsi A, Bonardi S, Brindani F. Relation between the presence of extrachromosomal DNA and virulence features in Salmonella enterica strains. Ann Fac Medic Vet di Parma 2005; XXV: 175-180. [ Links ]
16. Huang R, Wu S, Zhang X, Zhang Y. Molecular analysis and identification of virulence gene on pRST98 from multi-drug resistant Salmonella Typhi. Cell Mol Immun 2005; 2: 136-140. [ Links ]
17. Hornick RB. Selective primary health care: strategies for control of disease in the developing world. XX Typhoid fever. Rev Infect Dis 1985; 7: 536-46. [ Links ]
18. Hendriksen SWM, Orsel K, Wagenaar JA, Miko A, van Duijkeren E. Animal-to-Human Transmission of Salmonella Typhimurium DT104A Variant. Emer Infect Dis 2004; 10: 2225-7. [ Links ]
19. Concha- Valdez FG, Flores-Abuxapqui JJ, Puc-Franco MA, Heredia-Navarrete MR. Frecuencia del gen spv en cepas de Salmonella spp. aisladas de niños con y sin diarrea. Rev Biomed 2004; 15: 201-6. [ Links ]
20. Ramos-Morales F, Prieto AI, Beuzón CR, Holden DW, Casadesús J. Role for Salmonella enterica enterobacterial common antigen in bile resistance and virulence. J Bacteriol 2003; 185: 5328-32. [ Links ]
21. Figueroa-Bossi N, Bossi L. Inducible prophages contribute to Salmonella virulence in mice. Mol Microbiol 1999; 33: 167- 76. [ Links ]
22. Figueroa-Bossi N, Uzzau S, Maloriol D, Bossi L. Variable assortment of prophages provides a transferable repertoire of pathogenic determinants in lysogenic conversion is a major mechanism driving the evolution of Salmonella bacteria. Mol Microbiol 2001; 39: 260-71. [ Links ]
23. Ridley AM, Threlfall EJ, Rowe B. Genotypic Characterization of Salmonella Enteritidis phage types by plasmid analysis, ribotyping, and pulsed-field gel electrophoresis. J Clinical Microbiol 1998; 36:2314–21. [ Links ]
24. Refsum TH, Heir E, Kapperud G, Vardund T, Holstad G. Molecular epidemiology of Salmonella enterica serovar Typhimurium isolates determined by Pulsed-Field gel electrophoresis: comparison of isolates from avian wildlife, domestic animals, and the environment in Norway. Appl Envir Microbiol 2002; 68: 5600-6. [ Links ]
25. Parvathi A, Vijayan J, Murali G, Chandran P Comparative virulence genotyping and antimicrobial susceptibility profiling of environmental and clinical Salmonella enterica from Cochin, India. Curr Microbiol 2011; 62:21-6. [ Links ]
26. Ammari S, Laglaoui A, En-nanei L, Bertrand S, Wildemauwe C, Barrijal S, Abid M Characterization of Salmonella Enteritidis isolated from foods and patients in northern Morocco. J Infect Dev Ctries 2009; 9:695-703. [ Links ]
Forma de citar: Patiño-García DF, Cardona-Castro NM, Sánchez- Jiménez MM. Búsqueda del plásmido de virulencia de Salmonella en aislamientos clínicos colombianos. Rev CES Med 2011; 25(1):54-64
]]>